用元数据着色稀疏曲线(纯素包) (phyloseq包)
用元数据着色稀疏曲线(纯素包) (phyloseq包)
提问于 2017-11-11 05:46:31
第一次提问者在这里。我无法在其他帖子中找到这个问题的答案(爱stackexchange,顺便说一句)。
不管怎样..。我通过素食包创建了一个稀薄的曲线,我得到了一个非常混乱的地块,在图的底部有一个很厚的黑色条状图,它遮住了一些低多样性的样本线。理想情况下,我想用我的所有线条(169;我可以将它减少到144)生成一个地块,但我可以绘制一个合成图,按样本年着色,并为每个池塘绘制不同类型的线条(即:2个样本年份:2016年、2017年和3个池塘:1、2、5)。我使用phyloseq使用所有数据创建了一个对象,然后将OTU丰度表从我的元数据中分离为不同的对象(jt = OTU表和sampledata =元数据)。我现在的代码是:
jt <- as.data.frame(t(j)) # transform it to make it compatible with the proceeding commands
rarecurve(jt
, step = 100
, sample = 6000
, main = "Alpha Rarefaction Curve"
, cex = 0.2
, color = sampledata$PondYear)
# A very small subset of the sample metadata
Pond Year
F16.5.d.1.1.R2 5 2016
F17.1.D.6.1.R1 1 2017
F16.1.D15.1.R3 1 2016
F17.2.D00.1.R2 2 2017回答 1
Stack Overflow用户
回答已采纳
发布于 2017-11-11 08:33:23
这里是一个例子,如何绘制一个稀薄的曲线与to图。我使用了从生物导体获得的帕洛塞克包中的数据。
安装phyloseq:
source('http://bioconductor.org/biocLite.R')
biocLite('phyloseq')
library(phyloseq)其他需要的图书馆
library(tidyverse)
library(vegan)数据:
mothlist <- system.file("extdata", "esophagus.fn.list.gz", package = "phyloseq")
mothgroup <- system.file("extdata", "esophagus.good.groups.gz", package = "phyloseq")
mothtree <- system.file("extdata", "esophagus.tree.gz", package = "phyloseq")
cutoff <- "0.10"
esophman <- import_mothur(mothlist, mothgroup, mothtree, cutoff)提取OTU表,转置并转换为数据帧
otu <- otu_table(esophman)
otu <- as.data.frame(t(otu))
sample_names <- rownames(otu)
out <- rarecurve(otu, step = 5, sample = 6000, label = T)现在您有了一个列表,每个元素对应于一个示例:
把清单整理一下:
rare <- lapply(out, function(x){
b <- as.data.frame(x)
b <- data.frame(OTU = b[,1], raw.read = rownames(b))
b$raw.read <- as.numeric(gsub("N", "", b$raw.read))
return(b)
})标签列表
names(rare) <- sample_names转换为数据框架:
rare <- map_dfr(rare, function(x){
z <- data.frame(x)
return(z)
}, .id = "sample")让我们看看它的外观:
head(rare)
sample OTU raw.read
1 B 1.000000 1
2 B 5.977595 6
3 B 10.919090 11
4 B 15.826125 16
5 B 20.700279 21
6 B 25.543070 26用ggplot2绘图
ggplot(data = rare)+
geom_line(aes(x = raw.read, y = OTU, color = sample))+
scale_x_continuous(labels = scales::scientific_format())
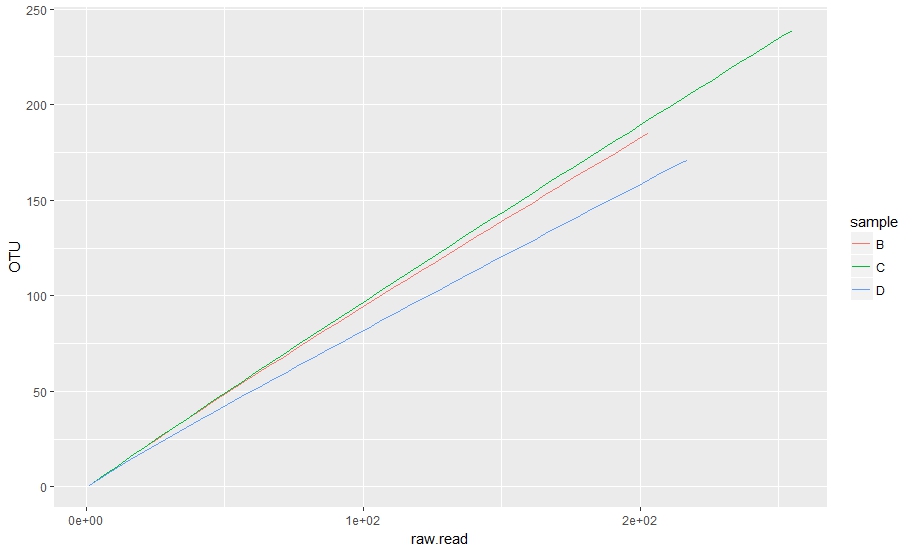
纯素情节:
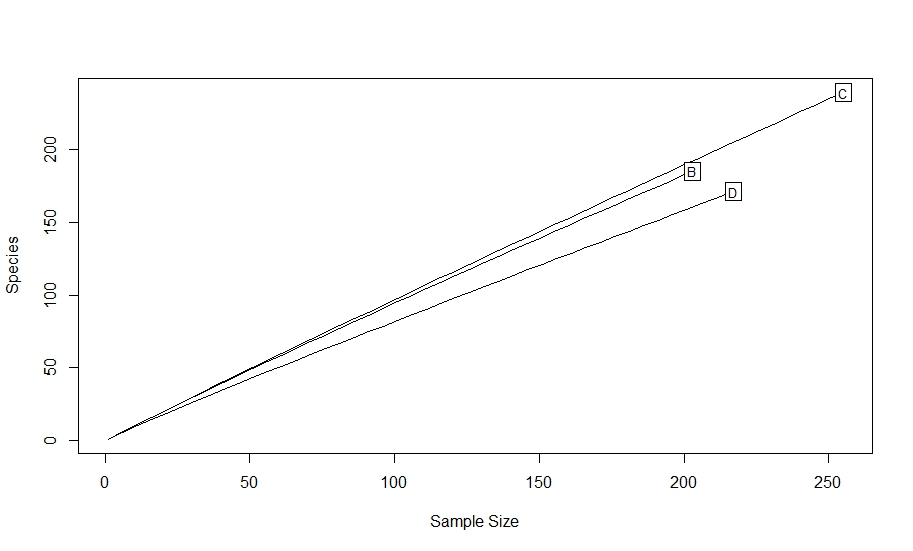
rarecurve(otu, step = 5, sample = 6000, label = T) #low step size because of low abundance
根据这一点,我们可以制作一个额外的分组和颜色列。
下面是一个如何添加另一个分组的示例。让我们假设您有一个表单的表:
groupings <- data.frame(sample = c("B", "C", "D"),
location = c("one", "one", "two"), stringsAsFactors = F)
groupings
sample location
1 B one
2 C one
3 D two根据另一个特征对样本进行分组。您可以使用lapply或map_dfr来检查groupings$sample和标签rare$location。
rare <- map_dfr(groupings$sample, function(x){ #loop over samples
z <- rare[rare$sample == x,] #subset rare according to sample
loc <- groupings$location[groupings$sample == x] #subset groupings according to sample, if more than one grouping repeat for all
z <- data.frame(z, loc) #make a new data frame with the subsets
return(z)
})
head(rare)
sample OTU raw.read loc
1 B 1.000000 1 one
2 B 5.977595 6 one
3 B 10.919090 11 one
4 B 15.826125 16 one
5 B 20.700279 21 one
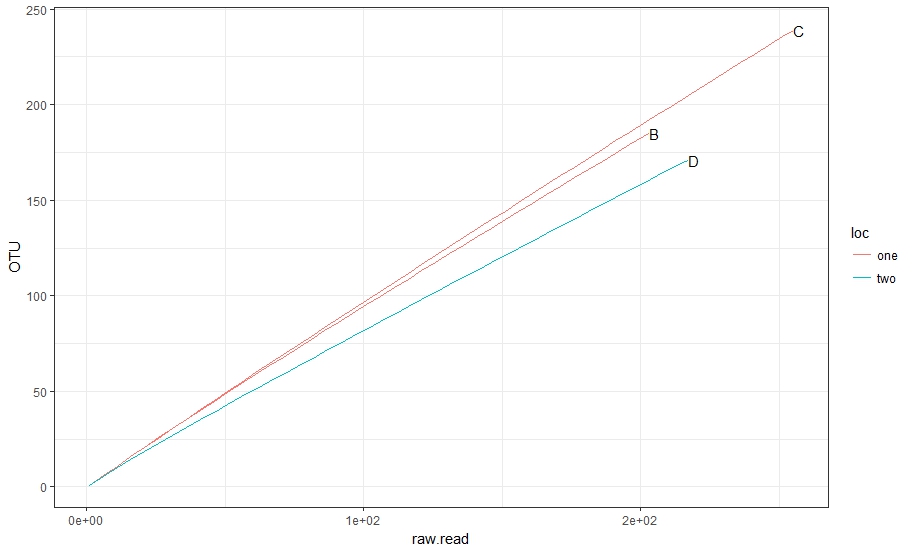
6 B 25.543070 26 one让我们用这个做一个好的计划。
ggplot(data = rare)+
geom_line(aes(x = raw.read, y = OTU, group = sample, color = loc))+
geom_text(data = rare %>% #here we need coordinates of the labels
group_by(sample) %>% #first group by samples
summarise(max_OTU = max(OTU), #find max OTU
max_raw = max(raw.read)), #find max raw read
aes(x = max_raw, y = max_OTU, label = sample), check_overlap = T, hjust = 0)+
scale_x_continuous(labels = scales::scientific_format())+
theme_bw()
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/47234809
复制相关文章
相似问题

