Nat. Mach. Intell. | ImmunoStruct: 赋能免疫原性预测的多模态深度学习框架
Nat. Mach. Intell. | ImmunoStruct: 赋能免疫原性预测的多模态深度学习框架

DrugAI
发布于 2026-01-06 14:29:02
发布于 2026-01-06 14:29:02
DRUGONE
基于表位的疫苗在传染病和癌症治疗中具有重要潜力,但准确识别真正具有免疫原性的肽段仍极具挑战性。现有方法多依赖氨基酸序列信息,难以充分利用蛋白结构和生化特征。研究人员提出 ImmunoStruct,一种融合序列、结构与生化性质的多模态深度学习模型,用于预测多等位基因 I 类肽–MHC 的免疫原性。基于包含 26,049 个肽–MHC 复合物的多模态数据集,ImmunoStruct 在传染病表位和癌症新抗原预测中均显著优于现有方法,并具备良好的可解释性。模型预测结果与 SARS-CoV-2 表位的体外实验高度一致,同时在癌症患者的生存预测任务中展现出潜在临床价值。

免疫系统通过 MHC 分子呈递肽段并激活 T 细胞反应,而只有极少数呈递肽真正具有免疫原性。在疫苗设计和癌症新抗原筛选中,候选肽数量受限且实验验证成本高昂,因此亟需可靠的计算预测工具。然而,免疫原性受多因素共同影响,包括肽–MHC 结合构象、肽在 MHC 表面的空间暴露以及与 TCR 的相互作用,仅依赖序列信息往往难以刻画这些关键决定因素。
尽管近年来出现了一些深度学习模型用于肽–MHC 预测,但多数方法未系统整合结构信息和生化特征,限制了预测精度和生物学解释能力。为解决这一问题,研究人员提出利用多模态建模框架,将结构生物学信息直接纳入免疫原性预测过程。
方法
ImmunoStruct 通过三条并行分支分别建模肽–MHC 序列、三维结构和生化性质信息。研究人员使用 AlphaFold2 预测肽–MHC 复合物结构,并将其转化为包含空间坐标与相互作用信息的图结构,由等变图神经网络进行处理;序列信息通过变分自编码器压缩为连续潜在表示;生化特征(如分子量、电荷、疏水性及溶剂可及表面积)由多层感知机编码。三种模态的表示随后通过多头注意力机制融合,并用于免疫原性预测。模型采用迁移学习策略进行训练,并在癌症新抗原场景中引入突变体–野生型对比学习,以强化对细微免疫差异的识别能力。
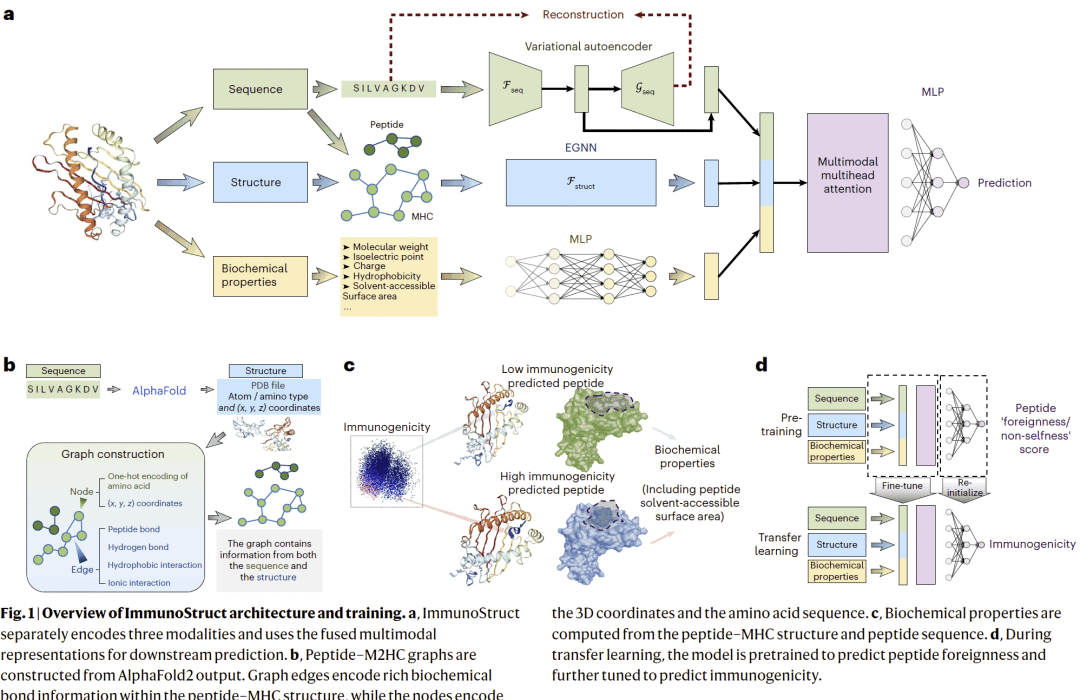
图 1|ImmunoStruct 多模态架构与训练流程。
结果
传染病表位的免疫原性预测性能
在 IEDB 传染病表位数据集上,ImmunoStruct 在 AUROC、AUPRC 及临床相关的候选肽排序指标上均显著优于现有方法。消融实验表明,序列、结构与生化信息的联合建模以及迁移学习策略对性能提升具有协同作用。
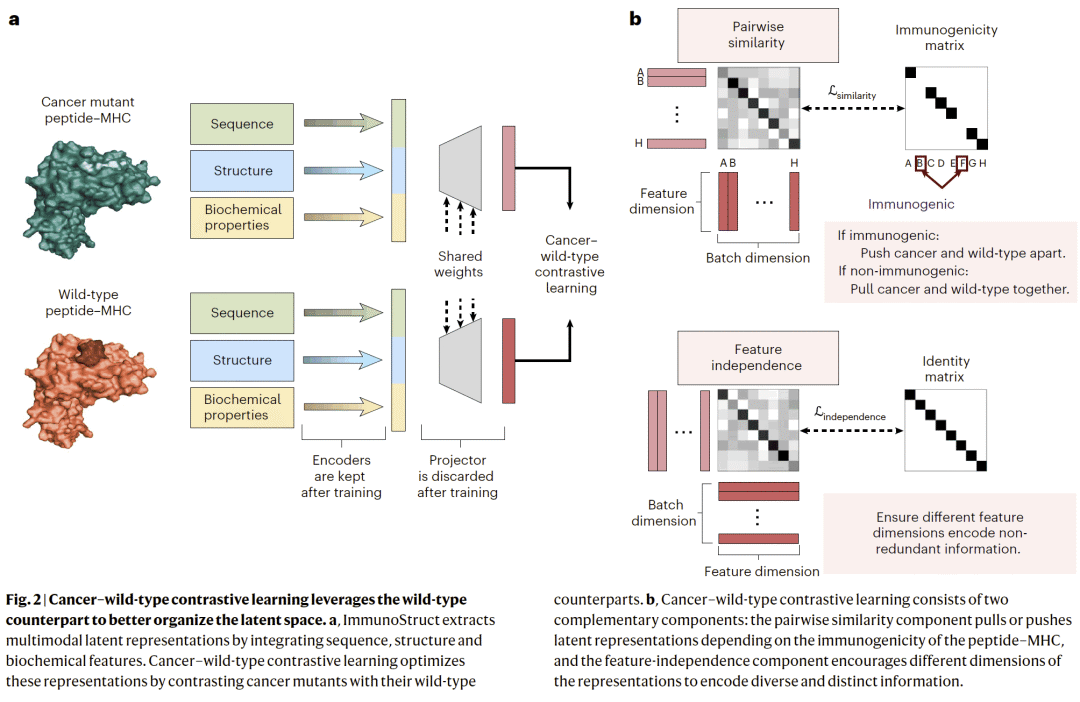
图 2|传染病表位免疫原性预测性能对比。
多模态表示与结构可解释性分析
通过对潜在空间的可视化,研究人员发现 ImmunoStruct 能够形成清晰区分免疫原性与非免疫原性肽–MHC 的结构化嵌入。基于结构注意力的分析进一步显示,模型重点关注肽段中面向 TCR 的关键位置,这些位置在免疫原性肽中呈现更一致的结构和氨基酸偏好。
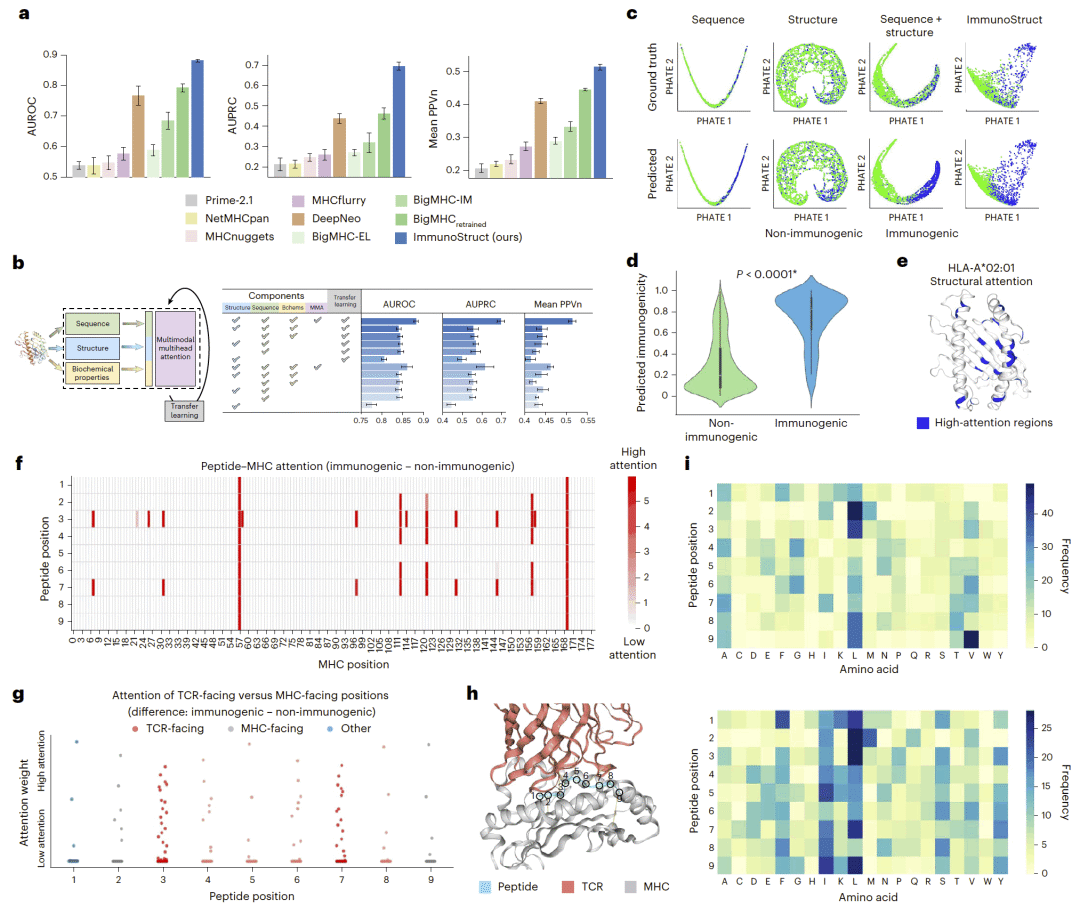
图 3|多模态嵌入空间与结构注意力分析。
癌症新抗原免疫原性预测
在癌症新抗原数据集中,ImmunoStruct 同样显著优于现有方法。引入突变体–野生型对比学习后,模型能够有效区分仅有单个氨基酸差异的免疫原性与非免疫原性肽段。以 KRAS 突变为例,模型成功捕捉到不同突变体在肽–MHC 构象层面的细微差异,并与实验观测结果一致。
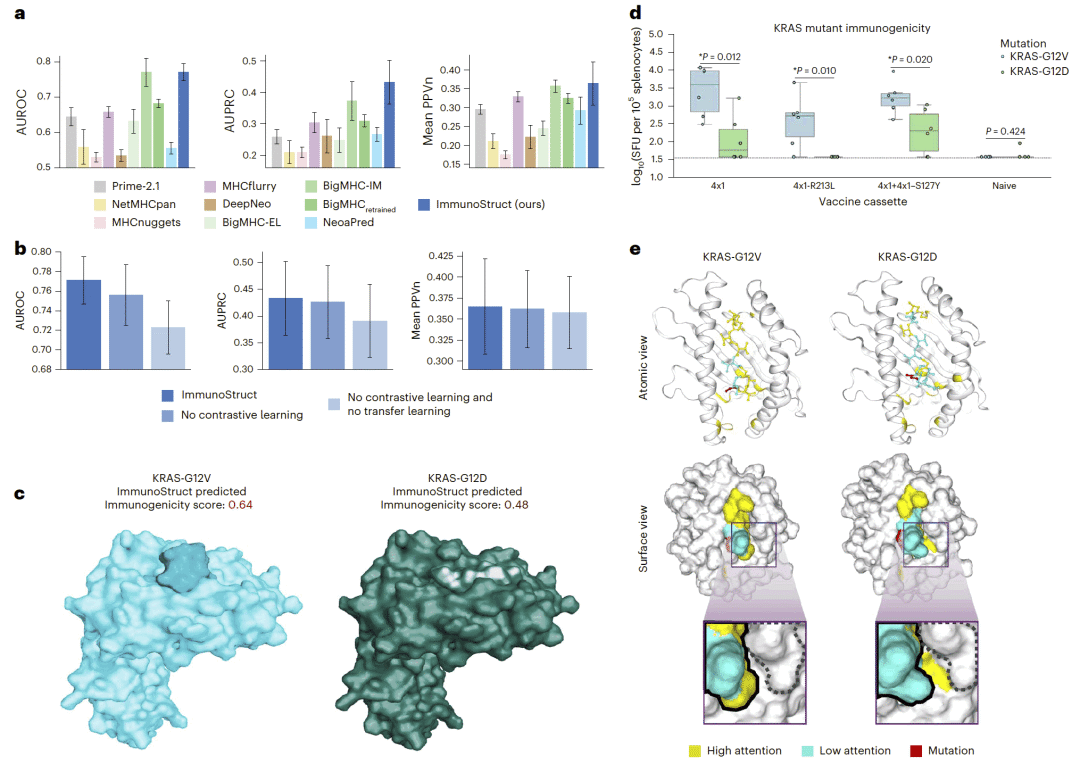
图 4|癌症新抗原预测与结构差异解析。
实验验证与临床相关性评估
在 SARS-CoV-2 表位的体外 IFN-γ ELISpot 实验中,ImmunoStruct 的预测结果与实验测量高度一致。此外,在癌症免疫治疗患者队列中,基于 ImmunoStruct 预测的免疫原性负荷能够更有效地区分患者总体生存期和无进展生存期,优于多种现有指标。
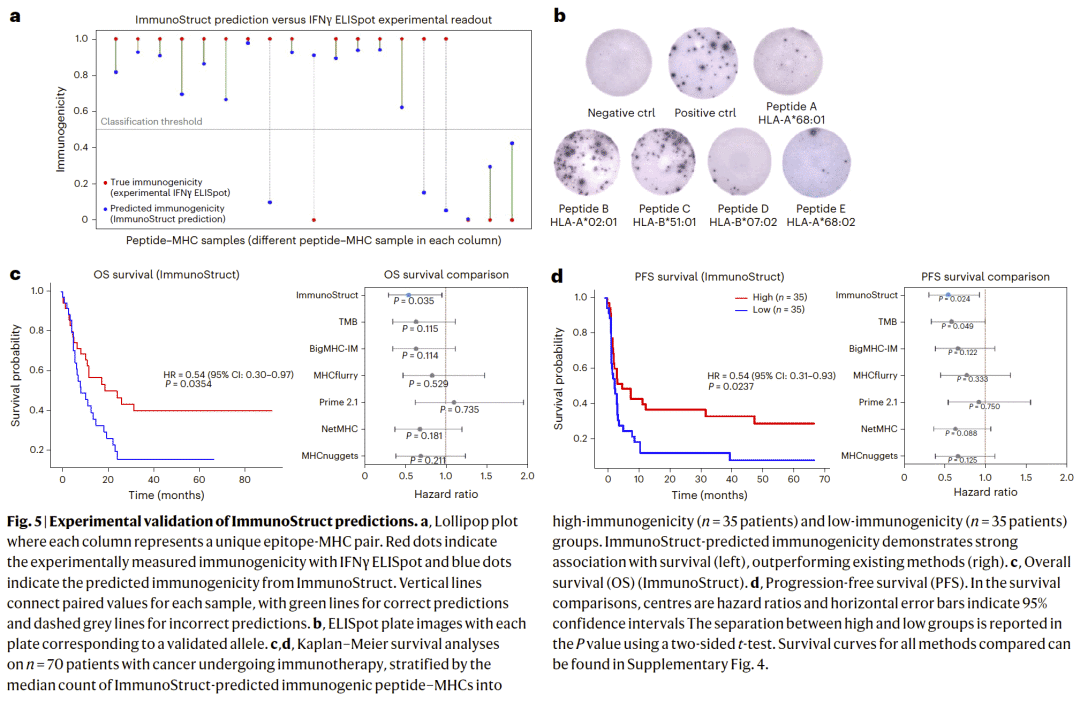
图 5|实验验证与癌症患者生存分析。
讨论
ImmunoStruct 通过系统整合序列、结构和生化信息,为免疫原性预测提供了一种兼具性能与可解释性的多模态深度学习框架。结构等变图建模和注意力机制使模型能够直接学习与 TCR 识别相关的空间特征,而迁移学习与对比学习策略则提升了模型在数据稀缺和细微突变场景下的鲁棒性。
尽管如此,模型仍受限于公共肽–MHC 数据在等位基因和实验条件上的偏倚,以及缺乏 TCR 序列信息等问题。未来,结合更大规模的结构数据、分子动力学信息以及多模态免疫学数据,有望进一步提升免疫原性预测的准确性与临床实用性。
整理 | DrugOne团队
参考资料
Givechian, K.B., Rocha, J.F., Liu, C. et al. ImmunoStruct enables multimodal deep learning for immunogenicity prediction. Nat Mach Intell (2025).
https://doi.org/10.1038/s42256-025-01163-y
内容为【DrugOne】公众号原创|转载请注明来源
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-01-01,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

