ODesign Antibody version正式开源!
ODesign Antibody version正式开源!

DrugOne
发布于 2025-12-25 15:05:42
发布于 2025-12-25 15:05:42
ODesign Antibody version是ODesign的特化子版本,是一个用作de novo antibody design的pipeline。它包括antibody design model和odesign inversefolding model两个模块,实现了从端到端的抗体设计。
ODesign Antibody采用了ODesign的架构,但在constraint模块有所不同。抗体设计着重于抗体可变区的设计,可变区又分为骨架区(framework)和互补决定区(CDR)。互补决定区的高度灵活构象决定了抗原和抗体的结合模式。因此,抗体设计通常保留模版骨架的序列,并重新设计CDR区。因此,在设计流程中,ODesign Antibody在设计CDR区的同时,重构骨架区的构象,使骨架区与CDR区高度兼容。
ODesign Antibody无需抗体结构信息,根据输入的抗体序列和定义的设计区域及长度,实现靶向抗原表位的抗体设计。ODesign Antibody能够实现nanobody(纳米抗体)、scfv以及fab抗体的设计。
ODesign Antibody测试了其在il7ra、rbd、HA、rsv site1和tcdb五个表位上的纳米抗体生成能力。我们为每个表位生成了100个纳米抗体,用LigandMPNN side chain packing生成CDR区侧链构象,仅使用pyrosetta fast relax 3轮以纠正LigandMPNN生成的侧链,在5个表位上达到了平均-42的ddG以及423的cms。


Example
1.拷贝项目文件
git clone https://github.com/The-Institute-for-AI-Molecular-Design/ODesign.git
git switch ODesign-antibody2.下载模型权重
cd /path/to/project
bash ./ckpt/get_odesign_ckpt.sh3.按照https://github.com/The-Institute-for-AI-Molecular-Design/ODesign/tree/main中配置环境的流程配置环境
4.下载
https://drive.google.com/drive/folders/1wPmwIrC3G52q1JFY0RXY95tjKDl7YEln?usp=drive_link至./data5.采样
python scripts/inference.py \
exp.exp_name=antibody_design \
input_json_path =”./examples/nanobody.json” \
seeds=”[42, 101]”6.结果
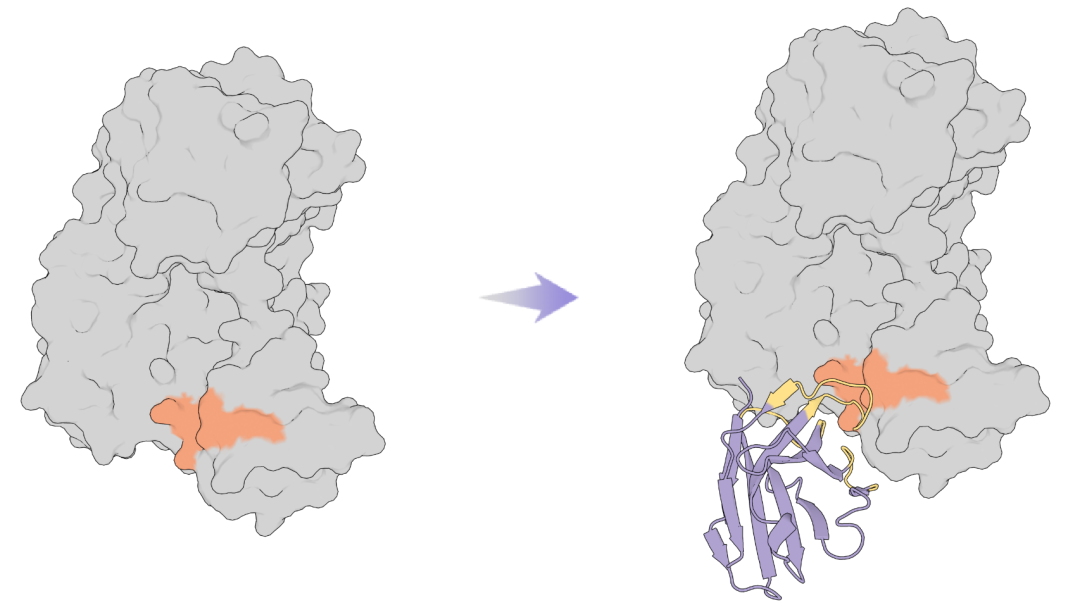
code available
https://github.com/The-Institute-for-AI-Molecular-Design/ODesign/tree/ODesign-antibody
除了最新发布antibody设计功能, ODesign作为全模态分子设计模型,可以一站式完成蛋白、小分子配体和核酸的设计。下面展示的是当前已支持的典型设计能力:
- Protein Generation(蛋白设计)
- Protein-binding Protein(蛋白-蛋白结合设计)

ODesign能够针对给定的蛋白靶标,设计与之特异性结合的新蛋白链,并在指定界面残基附近形成稳定的蛋白-蛋白相互作用界面。
- Ligand-binding Protein(小分子配体结合蛋白)

ODesign可以生成与特定小分子配体结合的蛋白,通过在配体附近自动构建合适的结合口袋,使蛋白与小分子形成空间和化学上合理的相互作用。
- Atom Scaffold(原子级 Scaffold 设计)
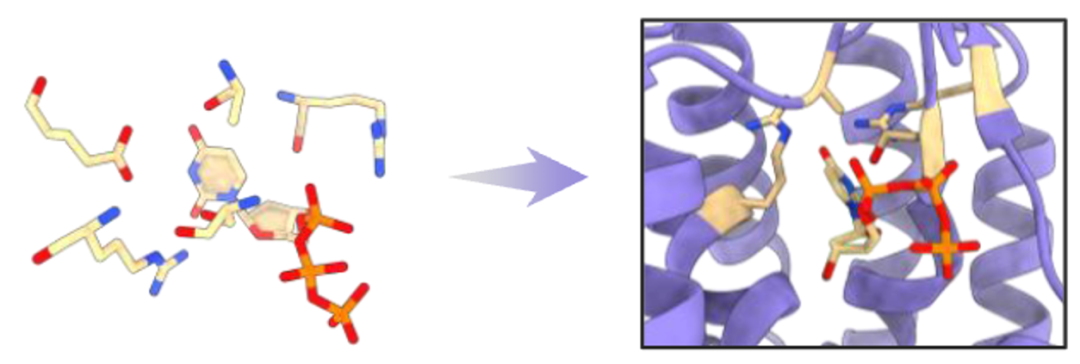
ODesign 能够围绕特定原子或官能团进行 scaffold 设计,将这些关键原子精确固定在目标几何位置,用于构建精细配位、金属结合位点或化学反应中心等。
- Motif Scaffold(功能基序 Scaffold)
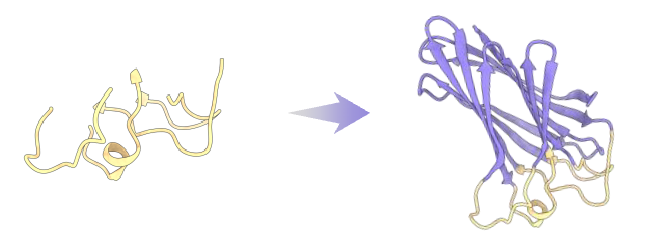
ODesign 可以在给定功能基序(motif)的基础上,自动生成周围支撑结构,实现对催化基序、受体结合片段等功能片段的稳定化与“移植”,从而构建具有新折叠或新功能的蛋白。
- Ligand Generation(小分子配体设计)
- Protein-binding Ligand(蛋白结合小分子)

ODesign 还支持直接生成与特定蛋白靶标结合的小分子配体,在指定口袋和关键残基附近构建满足空间与化学约束的新颖小分子结构。
- Nucleic Acid Generation(核酸设计)
- Backbone Generation(核酸主链生成)

ODesign可以从零开始生成给定长度的核酸主链结构,用于 RNA/DNA 分子的de novo设计,无需事先提供参考结构。
- Protein-binding Nucleic Acid(蛋白结合核酸)

ODesign能够设计与蛋白靶标结合的核酸分子,在指定界面残基附近自动生成具备合理空间构象和相互作用模式的核酸链。
通过以上这些任务能力,加上最新发布的 ODesign Antibody 抗体设计功能(支持 nanobody、scFv、Fab 等多种抗体格式),ODesign已经覆盖了从蛋白、抗体到核酸、小分子配体的多模态分子设计,为端到端结构与功能导向的分子生成提供了统一的技术基础。
code available
https://github.com/The-Institute-for-AI-Molecular-Design/ODesign
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2025-12-23,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读

