内容补充--空间转录组联合GWAS数据分析
原创内容补充--空间转录组联合GWAS数据分析
原创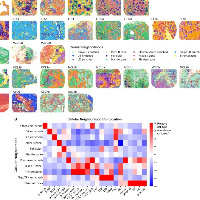
追风少年i
发布于 2025-10-12 09:32:20
发布于 2025-10-12 09:32:20
作者,Evil Genius
今天我们补充空间转录组联合GWAS数据分析,内容来源于顶刊

图片部分

其中i图:全基因组关联研究SNP在主要细胞类型中的富集评分。
J图:空间转录组数据中GWAS12左心室射血分数相关SNP富集情况可视化。
我们来看看文章的解释
为探究遗传变异与细胞类型的关联,基于细胞类型特异性 pseudo-bulk ATAC-seq谱和全基因组关联研究(GWAS)获得的心肌病相关单核苷酸多态性(SNPs)进行了富集分析。重点关注与左心室功能相关的SNPs,推测这些变异可能为心肌组织细胞组成提供最具生物学意义的信息。分析显示:与每搏输出量和左心室舒张末期容积相关的SNPs在内皮细胞中显著富集,这与内皮细胞在心脏舒张和扩张中的作用相吻合;而与左心室收缩末期容积和左心室射血分数相关的SNPs则在心肌细胞中富集,印证了收缩功能与这些左心室测量指标间的内在关联。进一步通过空间转录组技术将左心室射血分数相关SNPs映射至各组织点位,实现了GWAS信号的空间分布可视化。总之,构建的整合空间图谱实现了对心脏组织全域的细胞丰度、信号通路活性、转录因子结合活性及GWAS信号的系统解析,为人类心肌梗死后的组织重塑过程提供了深度视角。
再来看看方法部分
细胞类型特异性GWAS信号富集分析
从心血管疾病知识门户(https://cvd.hugeamp.org/)获取了4项基于MRI的左心室功能参数的GWAS摘要统计资料。针对每个表型,使用Plink(v1.9)对GWAS摘要统计数据进行聚类分析以识别index SNPs(聚类p值=0.0001,聚类距离=250kb,聚类r²=0.5),并以千人基因组计划中的欧洲样本作为参考群体。
随后,通过LiftOver工具将index SNPs的坐标从hg19版本转换为hg38版本。针对每种主要细胞类型,利用所有细胞的snATAC-seq数据生成平均染色质可及性谱。采用gchromVAR(v0.3.2)进行细胞类型特异性GWAS信号富集分析,并将富集分数标准化为z值。基于z值计算p值,并通过Benjamini-Hochberg方法进行多重检验校正。
生活很好,有你更好
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
评论
登录后参与评论
推荐阅读
目录

