numpy比numba和cython快,如何改进numba代码
这里我有一个简单的例子来帮助我理解使用numba和cython。我是numba和cython的新手。我已经尽力将所有的技巧结合起来,使numba快速,在某种程度上,对于cython也是如此,但是我的numpy代码几乎比numba ( float64)快2倍,如果使用float32,则比numba快2倍。不知道我在这里错过了什么。
我在想,也许问题不再是编码,而是更多关于编译器之类的问题,这一点我不太熟悉。
我浏览了很多关于numpy,numba和cython的堆叠文章,却没有找到任何直接的答案。
numpy版本:
def py_expsum(x):
return np.sum( np.exp(x) )numba版本:
@numba.jit( nopython=True)
def nb_expsum(x):
nx, ny = x.shape
val = 0.0
for ix in range(nx):
for iy in range(ny):
val += np.exp(x[ix, iy])
return valCython版本:
import numpy as np
import cython
from libc.math cimport exp
@cython.boundscheck(False)
@cython.wraparound(False)
cpdef double cy_expsum2 ( double[:,:] x, int nx, int ny ):
cdef:
double val = 0.0
int ix, iy
for ix in range(nx):
for iy in range(ny):
val += exp(x[ix, iy])
return val播放大小为2000 x 1000的数组,并循环超过100次。对于numba来说,它第一次被激活并不会被计算在循环中。
使用python 3 (anaconda分发版),窗口10
float64 / float32
1. numpy : 0.56 sec / 0.23 sec
2. numba : 0.93 sec / 0.74 sec
3. cython: 0.83 seccython在numba附近。所以对我来说最重要的问题是为什么numba不能打败numpy的运行时?我在这里做错了什么或者错过了什么?其他因素如何促成,我如何找出呢?
回答 3
Stack Overflow用户
发布于 2019-07-07 12:57:41
正如我们将要看到的,行为取决于使用numpy-分发的是什么。
这个答案将集中在英特尔的VML (矢量数学库)的Anacoda发行版上,在另一个硬件和numpy版本的情况下,磨耗可能会有所不同。
它还将展示如何通过Cython或numexpr来使用VML,如果不使用Anacoda-分发,它将在VML中插入一些numpy操作。
我可以复制您的结果,如下所示
N,M=2*10**4, 10**3
a=np.random.rand(N, M)我得到:
%timeit py_expsum(a) # 87ms
%timeit nb_expsum(a) # 672ms
%timeit nb_expsum2(a) # 412ms计算时间的绝大部分(约90%)用于评估exp功能,正如我们将要看到的,这是一个CPU密集型任务。
快速浏览top-statistics显示,numpy的版本已被平分化,但numba的情况并非如此。然而,在只有两个处理器的VM上,并行化本身并不能解释因子7的巨大差异(如DavidW的版本nb_expsum2所示)。
通过perf对这两个版本的代码进行分析如下:
nb_expsum
Overhead Command Shared Object Symbol
62,56% python libm-2.23.so [.] __ieee754_exp_avx
16,16% python libm-2.23.so [.] __GI___exp
5,25% python perf-28936.map [.] 0x00007f1658d53213
2,21% python mtrand.cpython-37m-x86_64-linux-gnu.so [.] rk_randompy_expsum
31,84% python libmkl_vml_avx.so [.] mkl_vml_kernel_dExp_E9HAynn ▒
9,47% python libiomp5.so [.] _INTERNAL_25_______src_kmp_barrier_cpp_38a91946::__kmp_wait_te▒
6,21% python [unknown] [k] 0xffffffff8140290c ▒
5,27% python mtrand.cpython-37m-x86_64-linux-gnu.so [.] rk_random 可以看到: numpy在引擎盖下使用英特尔的Paralliized矢量化mkl/vml版本,它的性能轻松超过numba使用的gnu-数学库(lm.so)版本(或者是numba的并行版本,或者是cython的版本)。我们可以通过使用分段技术来平平地面,但是mkl的矢量化版本的性能仍然优于numba和cython。
然而,只看到一个大小的性能并不是很有启发性,对于exp (对于其他先验函数),有两个维度需要考虑:
- 数组缓存效应中的元素数和不同大小的不同算法(在numpy中不是闻所未闻)可以导致不同的性能。
- 根据
x-value,计算exp(x)需要不同的时间。通常,有三种不同类型的输入,导致不同的计算时间:非常小,正常和非常大(与非有限的结果)。
我正在使用完善图来可视化结果(参见附录中的代码)。对于“正常”范围,我们得到以下性能:
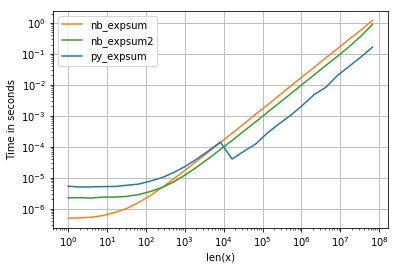
虽然0.0的性能相似,但我们可以看到,一旦结果变得无限,Intel的VML就会受到相当大的负面影响:
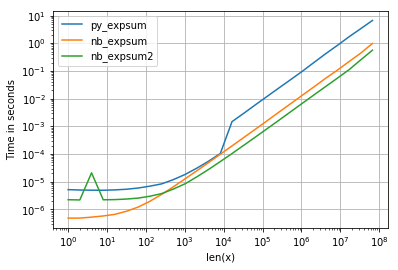
然而,还有其他需要注意的事情:
- 对于向量大小,
<= 8192 = 2^13numpy使用非并行化的glibc版本的exp (同样的numba和cython也在使用)。 - Anaconda发行版,我使用的是> 8192的覆盖numpy的功能并插入Intel的VML库,它是矢量化和并行化的--这解释了大小10^4的运行时间减少的原因。
- numba轻松地击败了通常的glibc版本(对于numpy来说开销太大),但是对于更大的数组(如果numpy不会切换到VML)则不会有太大的差别。
- 它似乎是一个CPU绑定的任务--我们看不到缓存--任何地方的边界。
- 只有当有超过500个元素时,Parallized版本才有意义。
那么后果是什么呢?
- 如果不超过8192个元素,应该使用numba版本.
- 否则,numpy版本(即使没有VML插件,也不会损失很多)。
注: numba不能自动使用英特尔VML中的vdExp (如注释中部分建议的那样),因为它单独计算exp(x),而VML则在整个数组上运行。
在写入和加载数据时,可以减少缓存丢失,该数据由numpy版本使用以下算法执行:
- 对适合高速缓存但也不太小(开销)的部分数据执行VML的
vdExp。 - 总结得到的工作数组。
- 为下一部分数据执行1.+2。直到整个数据被处理为止。
然而,与numpy的版本相比,我不会期望获得超过10% (但也许我错了),因为无论如何,90%的计算时间都是用在MVL上的。
然而,下面是Cython中一个可能的快速和肮脏的实现:
%%cython -L=<path_mkl_libs> --link-args=-Wl,-rpath=<path_mkl_libs> --link-args=-Wl,--no-as-needed -l=mkl_intel_ilp64 -l=mkl_core -l=mkl_gnu_thread -l=iomp5
# path to mkl can be found via np.show_config()
# which libraries needed: https://software.intel.com/en-us/articles/intel-mkl-link-line-advisor
# another option would be to wrap mkl.h:
cdef extern from *:
"""
// MKL_INT is 64bit integer for mkl-ilp64
// see https://software.intel.com/en-us/mkl-developer-reference-c-c-datatypes-specific-to-intel-mkl
#define MKL_INT long long int
void vdExp(MKL_INT n, const double *x, double *y);
"""
void vdExp(long long int n, const double *x, double *y)
def cy_expsum(const double[:,:] v):
cdef:
double[1024] w;
int n = v.size
int current = 0;
double res = 0.0
int size = 0
int i = 0
while current<n:
size = n-current
if size>1024:
size = 1024
vdExp(size, &v[0,0]+current, w)
for i in range(size):
res+=w[i]
current+=size
return res然而,正是numexpr所做的,它也使用英特尔的vml作为后端:
import numexpr as ne
def ne_expsum(x):
return ne.evaluate("sum(exp(x))")至于时间安排,我们可以看到以下情况:
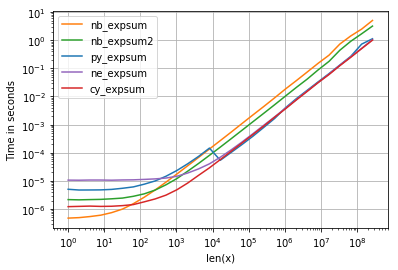
以下是值得注意的细节:
- numpy、numexpr和cython版本对于更大的数组具有几乎相同的性能--这并不奇怪,因为它们使用相同的vml-功能。
- 从这三个版本中,cython版本的开销最小,numexpr的开销最大。
- numexpr-版本可能是最容易编写的(考虑到并非每个numpy发行版plugsin mvl-功能)。
清单:
情节:
import numpy as np
def py_expsum(x):
return np.sum(np.exp(x))
import numba as nb
@nb.jit( nopython=True)
def nb_expsum(x):
nx, ny = x.shape
val = 0.0
for ix in range(nx):
for iy in range(ny):
val += np.exp( x[ix, iy] )
return val
@nb.jit( nopython=True, parallel=True)
def nb_expsum2(x):
nx, ny = x.shape
val = 0.0
for ix in range(nx):
for iy in nb.prange(ny):
val += np.exp( x[ix, iy] )
return val
import perfplot
factor = 1.0 # 0.0 or 1e4
perfplot.show(
setup=lambda n: factor*np.random.rand(1,n),
n_range=[2**k for k in range(0,27)],
kernels=[
py_expsum,
nb_expsum,
nb_expsum2,
],
logx=True,
logy=True,
xlabel='len(x)'
)Stack Overflow用户
发布于 2019-07-07 09:51:12
添加并行化。在Numba中,这只需要将外部循环prange和parallel=True添加到jit选项中:
@numba.jit( nopython=True,parallel=True)
def nb_expsum2(x):
nx, ny = x.shape
val = 0.0
for ix in numba.prange(nx):
for iy in range(ny):
val += np.exp( x[ix, iy] )
return val在我的PC上,它比非并行版本加速了3.2倍。这就是说,在我的个人电脑上,Numba和Cython都像写的那样击败了Numpy。
您也可以做Cython中的并行化 --我还没有在这里测试过它,但是我希望在性能上与Numba类似。(还请注意,对于Cython,您可以从nx和x.shape[1]获得x.shape[0]和x.shape[1],这样您就不必关闭边界检查,然后完全依赖用户输入才能保持在界限内)。
Stack Overflow用户
发布于 2019-07-08 16:38:55
它依赖于exp的实现和并行化。
如果在Numpy中使用Intel SVML,也可以在Numba、Numexpr或Cython等其他包中使用它。Numba性能提示
如果Numpy命令被并行化,也尝试在Numba或Cython中并行化。
码
import os
#Have to be before importing numpy
#Test with 1 Thread against a single thread Numba/Cython Version and
#at least with number of physical cores against parallel versions
os.environ["MKL_NUM_THREADS"] = "1"
import numpy as np
#from version 0.43 until 0.47 this has to be set before importing numba
#Bug: https://github.com/numba/numba/issues/4689
from llvmlite import binding
binding.set_option('SVML', '-vector-library=SVML')
import numba as nb
def py_expsum(x):
return np.sum( np.exp(x) )
@nb.njit(parallel=False,fastmath=True) #set it to True for a parallel version
def nb_expsum(x):
val = nb.float32(0.)#change this to float64 on the float64 version
for ix in nb.prange(x.shape[0]):
for iy in range(x.shape[1]):
val += np.exp(x[ix,iy])
return val
N,M=2000, 1000
#a=np.random.rand(N*M).reshape((N,M)).astype(np.float32)
a=np.random.rand(N*M).reshape((N,M))基准测试
#float64
%timeit py_expsum(a) #os.environ["MKL_NUM_THREADS"] = "1"
#7.44 ms ± 86.7 µs per loop (mean ± std. dev. of 7 runs, 100 loops each)
%timeit py_expsum(a) #os.environ["MKL_NUM_THREADS"] = "6"
#4.83 ms ± 139 µs per loop (mean ± std. dev. of 7 runs, 100 loops each)
%timeit nb_expsum(a) #parallel=false
#2.49 ms ± 25.1 µs per loop (mean ± std. dev. of 7 runs, 100 loops each)
%timeit nb_expsum(a) ##parallel=true
#568 µs ± 45.2 µs per loop (mean ± std. dev. of 7 runs, 1000 loops each)
#float32
%timeit py_expsum(a) #os.environ["MKL_NUM_THREADS"] = "1"
#3.44 ms ± 66.7 µs per loop (mean ± std. dev. of 7 runs, 100 loops each)
%timeit py_expsum(a) #os.environ["MKL_NUM_THREADS"] = "6"
#2.59 ms ± 35.7 µs per loop (mean ± std. dev. of 7 runs, 100 loops each)
%timeit nb_expsum(a) #parallel=false
#1 ms ± 12.6 µs per loop (mean ± std. dev. of 7 runs, 1000 loops each)
%timeit nb_expsum(a) #parallel=true
#252 µs ± 19.5 µs per loop (mean ± std. dev. of 7 runs, 1000 loops each)基于SVML的实现
import numpy as np
#from version 0.43 until 0.47 this has to be set before importing numba
#Bug: https://github.com/numba/numba/issues/4689
from llvmlite import binding
binding.set_option('SVML', '-vector-library=SVML')
import numba as nb
def py_expsum(x):
return np.sum(np.exp(x))
@nb.jit( nopython=True,parallel=False,fastmath=False)
def nb_expsum_single_thread(x):
nx, ny = x.shape
val = 0.0
for ix in range(nx):
for iy in range(ny):
val += np.exp( x[ix, iy] )
return val
#fastmath makes SIMD-vectorization possible
#val+=some_value is not vectorizable (scalar depends on scalar)
#This would also prevents the usage of SVML
@nb.jit( nopython=True,parallel=False,fastmath=True)
def nb_expsum_single_thread_vec(x):
nx, ny = x.shape
val = 0.0
for ix in range(nx):
for iy in range(ny):
val += np.exp( x[ix, iy] )
return val
@nb.jit(nopython=True,parallel=True,fastmath=False)
def nb_expsum_parallel(x):
nx, ny = x.shape
val = 0.0
#parallelization over the outer loop is almost every time faster
#except for rare cases like this (x.shape -> (1,n))
for ix in range(nx):
for iy in nb.prange(ny):
val += np.exp( x[ix, iy] )
return val
#fastmath makes SIMD-vectorization possible
#val+=some_value is not vectorizable (scalar depends on scalar)
#This would also prevents the usage of SVML
@nb.jit(nopython=True,parallel=True,fastmath=True)
def nb_expsum_parallel_vec(x):
nx, ny = x.shape
val = 0.0
#parallelization over the outer loop is almost every time faster
#except for rare cases like this (x.shape -> (1,n))
for ix in range(nx):
for iy in nb.prange(ny):
val += np.exp( x[ix, iy] )
return val
import perfplot
factor = 1.0 # 0.0 or 1e4
perfplot.show(
setup=lambda n: factor*np.random.rand(1,n),
n_range=[2**k for k in range(0,27)],
kernels=[
py_expsum,
nb_expsum_single_thread,
nb_expsum_single_thread_vec,
nb_expsum_parallel,
nb_expsum_parallel_vec,
cy_expsum
],
logx=True,
logy=True,
xlabel='len(x)'
)
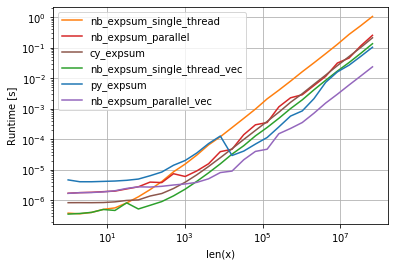
检查SVML是否已被使用
检查是否一切都如预期一样是有用的。
def check_SVML(func):
if 'intel_svmlcc' in func.inspect_llvm(func.signatures[0]):
print("found")
else:
print("not found")
check_SVML(nb_expsum_parallel_vec)
#foundhttps://stackoverflow.com/questions/56920713
复制相似问题

