树形枝与丛生枝间的差异
树形枝与丛生枝间的差异
提问于 2017-12-29 19:00:53
我有一个数据集,由4种不同基因型的小鼠每日取水情况组成。我正试图编写一个脚本,以便根据这些动物的取水模式,使用层次聚类分析法对它们进行分类,然后创建一个纵向图,绘制出每一群动物的日平均取水量。
为此,我首先创建分层集群,如下所示:
library("dendextend")
library("ggplot2")
library("reshape2")
data=read.csv("data.csv", header=T, row.names=1)
trimmed=data[, -ncol(data)]
hc <- as.dendrogram(hclust(dist(trimmed)))
labels.drk=data[,ncol(data)]
groups.drk=labels.drk[order.dendrogram(hc)]
genotypes=as.character(unique(data[,ncol(data)]))
k=4
cluster_cols=rainbow(k)
hc <- hc %>%
color_branches(k = k, col=cluster_cols) %>%
set("branches_lwd", 1) %>%
set("leaves_pch", rep(c(21, 19), length(genotypes))[groups.drk]) %>%
set("leaves_col", palette()[groups.drk])
plot(hc, main="Total animals" ,horiz=T)
legend("topleft", legend=genotypes,
col=palette(), pch = rep(c(21,19), length(genotypes)),
title="Genotypes")
legend("bottomleft", legend=1:k,
col=cluster_cols, lty = 1, lwd = 2,
title="Drinking group")然后,我用树函数来评估哪一种动物属于哪一组,以便绘制每组的平均取水量。
groups<-cutree(hc, k=k, order_clusters_as_data = FALSE))
x<-cbind(data,groups)
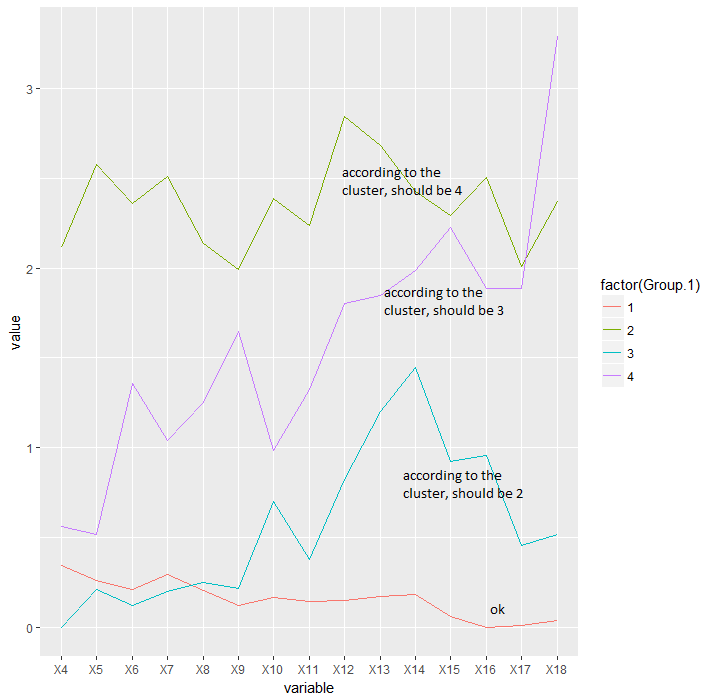
intake_avg=aggregate(data[, -ncol(data)], list(x$groups), mean, header=T)
df <- melt(intake_avg, id.vars = "Group.1")
ggplot(df, aes(variable, value, group=factor(Group.1))) + geom_line(aes(color=factor(Group.1)))问题是,我从分层聚类中得到的数字与由cutree函数分配的数字不一致。当集群将分支从1向上向上排序时,cutree函数使用了一些我不熟悉的其他排序参数。正因为如此,集群图中的标签和摄入量图中的标签不匹配。
我在编码方面非常初级,所以我确实使用了太多的冗余行和循环,所以我的代码可以被缩短,但是如果你们能帮我解决这个具体问题,我会很高兴的。
专题组:
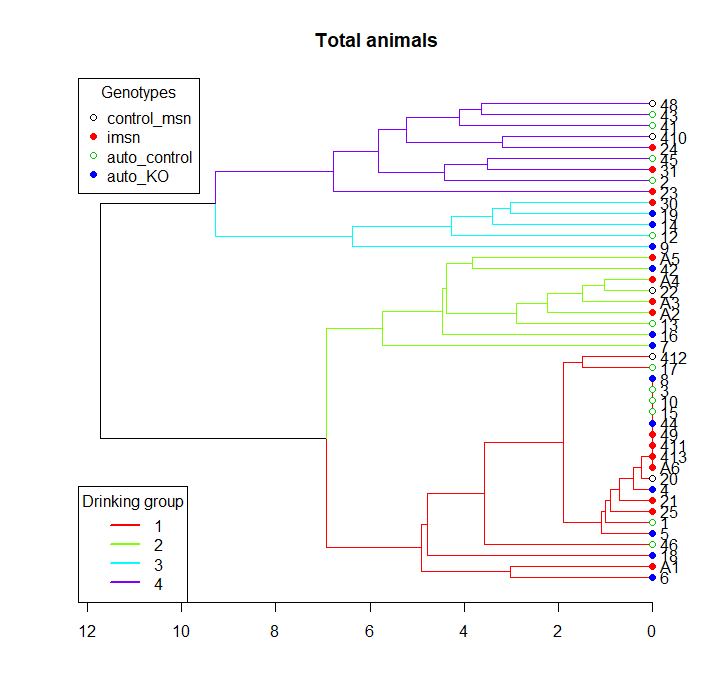
进气图
回答 1
Stack Overflow用户
回答已采纳
发布于 2017-12-30 11:56:52
要在树状图中获得相同的集群,您需要使用:
groups <- dendextend:::cutree(hc, k=k, order_clusters_as_data = FALSE)
idx <- match(rownames(data), names(groups))
x <- cbind(data,groups[idx])
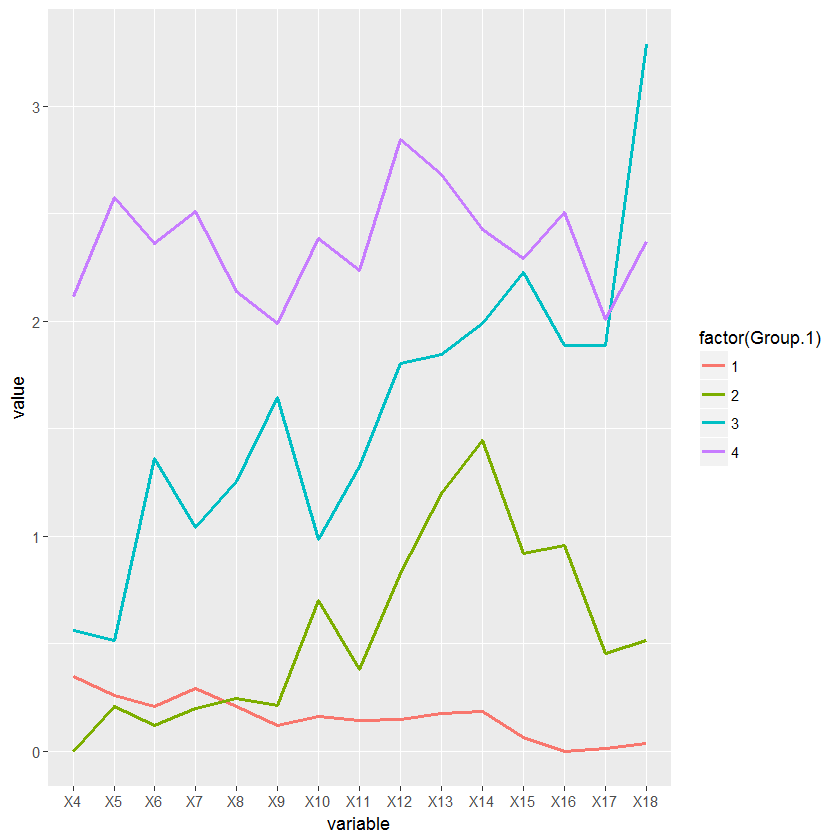
intake_avg <- aggregate(data[, -ncol(data)], list(x$groups), mean, header=T)
df <- melt(intake_avg, id.vars = "Group.1")
ggplot(df, aes(variable, value, group=factor(Group.1))) +
geom_line(aes(color=factor(Group.1)), lwd=1)以下是摄取量图:
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/48027184
复制相关文章
相似问题

