pheatmap cytokine_annotation
pheatmap cytokine_annotation
提问于 2017-09-25 08:10:00
我试图在pheatmap中开发cytokine_annotation并获取错误消息。
Seq.int中的错误(rx1L,rx2L,length.out = nb):'from‘必须是有限的
R版本3.3.3 pheatmap_1.0.8
可复制的例子:
#Using cytokine annotations
M<-matrix(rnorm(8*20),ncol=8)
row_annotation<-data.frame(A=gl(4,nrow(M)/4),B=gl(4,nrow(M)/4))
eg<-expand.grid(factor(c(0,1)),factor(c(0,1)),factor(c(0,1)))
colnames(eg)<-c("IFNg","TNFa","IL2")
rownames(eg)<-apply(eg,1,function(x)paste0(x,collapse=""))
rownames(M)<-1:nrow(M)
colnames(M)<-rownames(eg)
cytokine_annotation=eg
pheatmap(M,annotation=annotation,row_annotation=row_annotation,annotation_legend=TRUE,row_annotation_legend=TRUE,cluster_rows=FALSE,cytokine_annotation=cytokine_annotation,cluster_cols=FALSE)回答 2
Stack Overflow用户
回答已采纳
发布于 2017-09-25 09:15:59
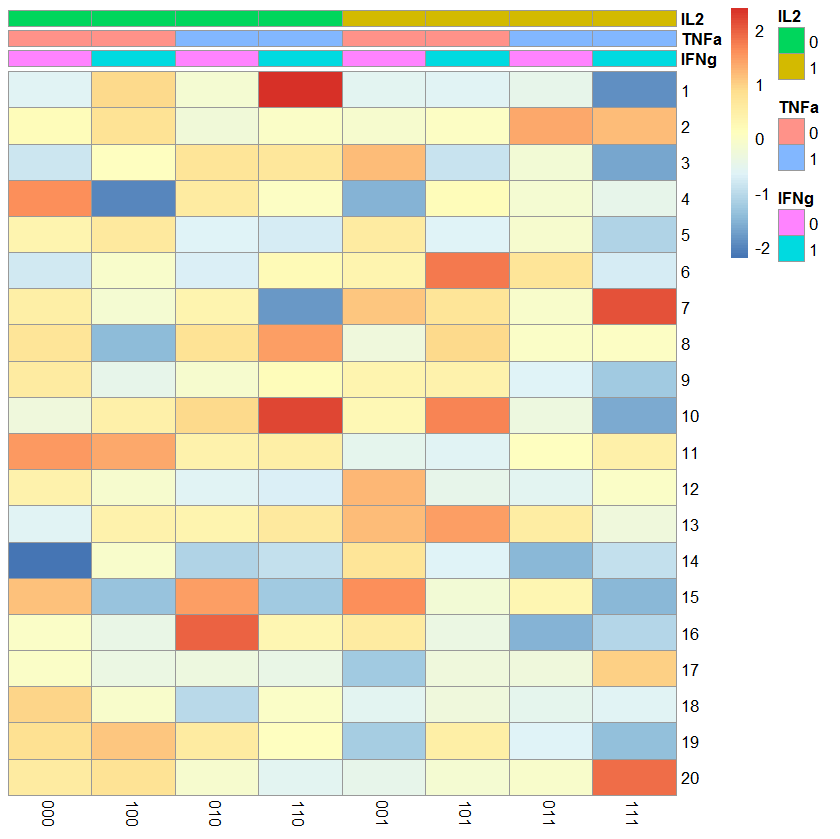
在我的R3.3.3中使用pheatmap_1.0.8,下面的代码可以工作:
set.seed(1)
M <- matrix(rnorm(8*20),ncol=8)
row_annotation <- data.frame(A=gl(4,nrow(M)/4),B=gl(4,nrow(M)/4))
eg <- expand.grid(factor(c(0,1)),factor(c(0,1)),factor(c(0,1)))
colnames(eg) <- c("IFNg","TNFa","IL2")
rownames(eg) <- apply(eg,1,function(x)paste0(x,collapse=""))
rownames(M) <- 1:nrow(M)
colnames(M) <- rownames(eg)
cytokine_annotation <- eg
library(pheatmap)
pheatmap(M, annotation=cytokine_annotation, row_annotation=row_annotation,
annotation_legend=TRUE, row_annotation_legend=TRUE, cluster_rows=FALSE,
cytokine_annotation=cytokine_annotation, cluster_cols=FALSE)
Stack Overflow用户
发布于 2021-03-08 07:08:05
我也有这个问题,发现简单地重新启动R解决了这个问题。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/46400386
复制相关文章
相似问题

