测试betadisper()输出的方差
我有一些群体基因组数据,其中我有针对每种治疗的祖先基因组的SNPs的等位基因频率。
我想看看不同处理之间的β多样性是否不同,所以在欧几里得距离上使用了vegan包和betadisper()。
在从模型中提取所有信息并将其放入数据仓库以便ggplot2喜欢之后,我就可以得到这个图了。
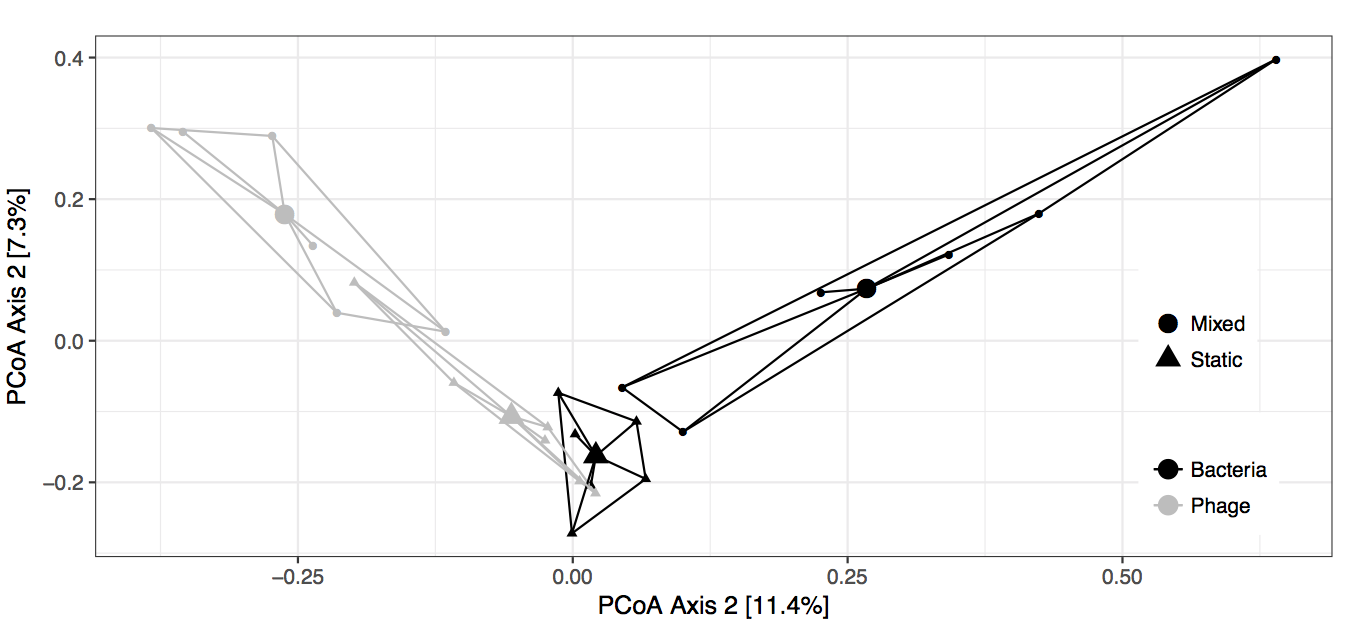
虽然在我看来,混合(圆)处理比静态(三角形)处理具有更高的β多样性,但anova()、permutest()和TukeyHSD()方法给出了我们不拒绝关于方差同质性的零假设的结果。此外,大多数这些测试的p值为p> 0.8。
根据我所能得出的结果,在betadisper()模型对象上进行的这些测试考虑到到质心的平均距离的差异,这在不同的治疗方法中并没有什么不同。
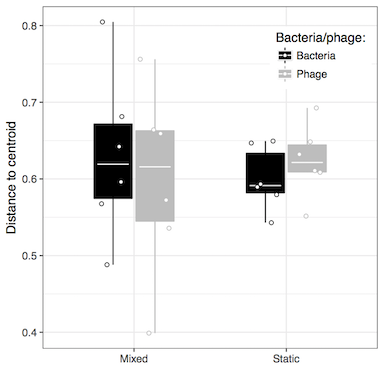
然而,与质心距离的传播似乎在两种治疗方法之间是不同的。
我只是想知道,我是否可以做一些像Bartlett测试或levene测试(在car包中),将每个组的质心距离的差异看作是另一个“β多样性”(组间的差异)。或者,如果在素食者中有方法,任何人都知道,看看与质心距离的变化,以及对质心的平均距离的变化。
回答 1
Stack Overflow用户
发布于 2017-07-13 07:34:57
您的图形具有误导性:您应该在PCoA中使用等高宽比(等距缩放),但是水平轴被拉伸,垂直轴在绘图中被压缩。此外,凸包可能是误导的,因为它集中在极端观测,但测试重点是“典型”距离质心。所以你的“眼睛”是错误的,被图形误导了。我们确实提供了正确的图形作为betadisper的方法,使用这些而不是自组装的ggplot2图形可以帮助您避免这个问题,或者至少您可以使用这些图形交叉检查您自己的版本。
请注意,betadisper已经处理了方差的“同质性”,而具有方差(=距离质心距离的方差)可能不是有用的,也不容易解释。我们得到的函数对分别是adonis2和betadisper,对于色散w.r.t的大小。去质心。
https://stackoverflow.com/questions/45052633
复制相似问题

