每对观测的Mahalanobis距离
每对观测的Mahalanobis距离
提问于 2016-12-07 19:23:13
我正在试图计算dataset dat的每个观测之间的Mahalanobis距离,其中每一行都是一个观察,每一列都是一个变量。这种距离的定义是:
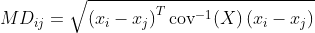
我写了一个函数来完成它,但我觉得它很慢。在R中有更好的方法来计算这个吗?
要生成一些数据来测试函数,请执行以下操作:
generateData <- function(nObs, nVar){
library(MASS)
mvrnorm(n=nObs, rep(0,nVar), diag(nVar))
}这是我到目前为止写的函数。对于我的数据(800个obs和90个变量),它们都可以工作,method = "forLoop"和method = "apply"分别需要大约30秒和33秒的时间。
mhbd_calc2 <- function(dat, method) { #Method is either "forLoop" or "apply"
dat <- as.matrix(na.omit(dat))
nObs <- nrow(dat)
mhbd <- matrix(nrow=nObs,ncol = nObs)
cv_mat_inv = solve(var(dat))
distMH = function(x){ #Mahalanobis distance function
diff = dat[x[1],]-dat[x[2],]
diff %*% cv_mat_inv %*% diff
}
if(method=="forLoop")
{
for (i in 1:nObs){
for(j in 1:i){
mhbd[i,j] <- distMH(c(i,j))
}
}
}
if(method=="apply")
{
mhbd[lower.tri(mhbd)] = apply(combn(nrow(dat),2),2, distMH)
}
result = sqrt(mhbd)
colnames(result)=rownames(dat)
rownames(result)=rownames(dat)
return(as.dist(result))
}注:我试过使用outer(),但速度更慢(60秒)。
回答 1
Stack Overflow用户
回答已采纳
发布于 2016-12-07 19:34:52
你需要一些数学知识。
- 做一个Cholesky因子的经验协方差,然后标准化你的观察;
- 利用
dist计算变换后的欧氏距离。
dist.maha <- function (dat) {
X <- as.matrix(na.omit(dat)) ## ensure a valid matrix
V <- cov(X) ## empirical covariance; positive definite
L <- t(chol(V)) ## lower triangular factor
stdX <- t(forwardsolve(L, t(X))) ## standardization
dist(stdX) ## use `dist`
}示例
set.seed(0)
x <- matrix(rnorm(6 * 3), 6, 3)
dist.maha(x)
# 1 2 3 4 5
#2 2.362109
#3 1.725084 1.495655
#4 2.959946 2.715641 2.690788
#5 3.044610 1.218184 1.531026 2.717390
#6 2.740958 1.694767 2.877993 2.978265 2.794879结果与您的mhbd_calc2一致。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/41025674
复制相关文章
相似问题

