为什么‘`skbio's pcoa`不是随机的呢?
我试图找出如何用不同的距离度量来实现Principal Coordinate Analysis。我偶然发现了skbio和sklearn的实现。我不明白为什么每次sklearn**'s实现都是不同的,而** skbio 是一样的?对Multidimensional Scaling,特别是Principal Coordinate Analysis有一定程度的随机性吗?我看到所有的集群都非常相似,但它们为什么不同?我是否正确地实现了这一点?
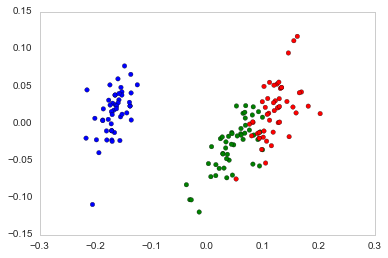
使用Principal Coordinate Analysis运行Scikit-bio (即Skbio)总是得到相同的结果:
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
from sklearn.datasets import load_iris
from sklearn.preprocessing import StandardScaler
from sklearn import decomposition
import seaborn as sns; sns.set_style("whitegrid", {'axes.grid' : False})
import skbio
from scipy.spatial import distance
%matplotlib inline
np.random.seed(0)
# Iris dataset
DF_data = pd.DataFrame(load_iris().data,
index = ["iris_%d" % i for i in range(load_iris().data.shape[0])],
columns = load_iris().feature_names)
n,m = DF_data.shape
# print(n,m)
# 150 4
Se_targets = pd.Series(load_iris().target,
index = ["iris_%d" % i for i in range(load_iris().data.shape[0])],
name = "Species")
# Scaling mean = 0, var = 1
DF_standard = pd.DataFrame(StandardScaler().fit_transform(DF_data),
index = DF_data.index,
columns = DF_data.columns)
# Distance Matrix
Ar_dist = distance.squareform(distance.pdist(DF_data, metric="braycurtis")) # (n x n) distance measure
DM_dist = skbio.stats.distance.DistanceMatrix(Ar_dist, ids=DF_standard.index)
PCoA = skbio.stats.ordination.pcoa(DM_dist)
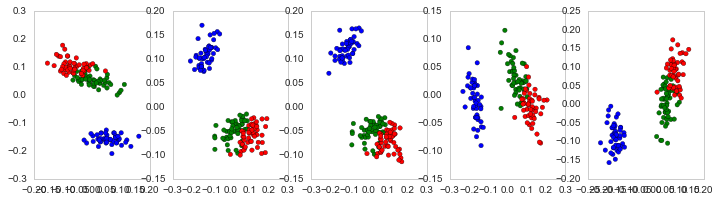
现在有了sklearn的Multidimensional Scaling
from sklearn.manifold import MDS
fig, ax=plt.subplots(ncols=5, figsize=(12,3))
for rs in range(5):
M = MDS(n_components=2, metric=True, random_state=rs, dissimilarity='precomputed')
A = M.fit(Ar_dist).embedding_
ax[rs].scatter(A[:,0],A[:,1], c=[{0:"b", 1:"g", 2:"r"}[t] for t in Se_targets])
回答 2
Stack Overflow用户
发布于 2016-08-12 16:54:48
scikit bio的PCoA (skbio.stats.ordination.pcoa)和scikit的MDS (sklearn.manifold.MDS)使用完全不同的算法来转换数据。scikit bio直接解决对称特征值问题,而scikit学习使用迭代最小化过程1。
scikit-bio的PCoA是确定性的,尽管可以根据它在2上执行的系统接收变换坐标的不同(任意)旋转,除非使用固定的random_state,否则它的MDS在默认情况下是随机的。random_state似乎用于初始化迭代最小化过程(scikit学习文档称random_state用于“初始化中心”3,尽管我不知道这到底意味着什么)。每个random_state都可能产生与任意旋转4略有不同的嵌入。
Stack Overflow用户
发布于 2016-08-11 23:02:00
MDS是一种概率算法,有一个参数random_state,您可以使用它来修复随机种子,如果每次都想得到相同的结果,就可以传递它。另一方面,PCA是一种确定性算法,如果使用sklearn.decomposition.PCA,每次都应该得到相同的结果。
https://stackoverflow.com/questions/38905833
复制相似问题

