R中的MLE问题
R中的MLE问题
提问于 2015-11-17 12:18:47
我是R的新手,在我所知道的其他语言的基础上自学了我对R的了解。我目前处于学生研究职位,必须使用R来寻找给定似然函数的最大似然估计:
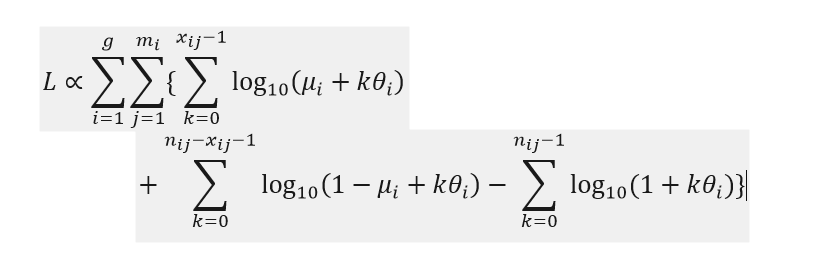
其中g,m_i,x_ij,n_ij和mu_i都是已知的。我必须最大限度地利用theta_i,但我不知道如何做到这一点,因为我大多是自学的。我知道我应该有六个θ的估计值。我试着在网上做关于使用mle的研究,但我不太了解统计,以了解网站在谈论什么。任何帮助我弄清楚我做错了什么,我们将不胜感激。我不知道如何附加excel文件,所以我很抱歉不能包含数据表。
在试图教自己这个和教授一起工作的过程中,我们会收到这样的错误:
Do.call中的错误( "minuslogl“,l):找不到函数”minuslogl“
下面是我在此之前完成的代码:
library(stats4)
#####################################################################
#Liklihood Model ####CHECK
###################################################################
BB <- function(LITTERS, responses, fetuses, mu, theta) {
total <- 0
#1
for (i in 1:6) {
firstSum <- 0
#2
for (j in 1:LITTERS) {
secondSum <- 0
#log(mu[i] + kTheta[i])
insideFirst <- 0
for (k in 0:(responses[i,j] - 1))
{
insideFirst <- insideFirst + log10(mu[i] + k * theta[i])
}
#log(1-mu[i] + kTheta[i])
insideSecond <- 0
for (k in 0:(fetuses[i,j] - responses[i,j] - 1))
{
insideSecond <- insideSecond + log10(1 - mu[i] + k * theta[i])
}
#log(1 + kTheta[i])
insideThird <- 0
for (k in 0:(fetuses[i,j] - 1))
{
insideThird <- insideThird + log10(1 + k * theta[i])
}
secondSum <- insideFirst + insideSecond - insideThird
firstSum <- firstSum + secondSum
}
total <- total + firstSum
}
return (total)
}
###################################################################
#Number of litters
LITTERS.M <- 25
doses <- c(0, 30, 45, 60, 75, 90)
#Retrieves the litter sizes (fetuses)
litterSize.dose0 <- get.Litter.Sizes(dose0, LITTERS.M)
litterSize.dose30 <- get.Litter.Sizes(dose30, LITTERS.M)
litterSize.dose45 <- get.Litter.Sizes(dose45, LITTERS.M)
litterSize.dose60 <- get.Litter.Sizes(dose60, LITTERS.M)
litterSize.dose75 <- get.Litter.Sizes(dose75, LITTERS.M)
litterSize.dose90 <- get.Litter.Sizes(dose90, LITTERS.M)
litterSize <- c(litterSize.dose0, litterSize.dose30, litterSize.dose45, litterSize.dose60, litterSize.dose75, litterSize.dose90)
litterSizes <- matrix(litterSize, nrow = 6, ncol = LITTERS.M)
#Start of Linear Regression for AB By first estimating AB
estimate.dose0 <- get.estimate.AB(dose0)
estimate.dose30 <- get.estimate.AB(dose30)
estimate.dose45 <- get.estimate.AB(dose45)
estimate.dose60 <- get.estimate.AB(dose60)
estimate.dose75 <- get.estimate.AB(dose75)
estimate.dose90 <- get.estimate.AB(dose90)
rProbR <- c(estimate.dose0, estimate.dose30, estimate.dose45, estimate.dose60,
estimate.dose75, estimate.dose90)
ab <- c(get.Log.Estimate(estimate.dose0), get.Log.Estimate(estimate.dose30), get.Log.Estimate(estimate.dose45),
get.Log.Estimate(estimate.dose60), get.Log.Estimate(estimate.dose75), get.Log.Estimate(estimate.dose90))
#Fit to Linear Regression
toFit <- data.frame(rProbR, ab)
linearRegression <- lm(ab ~ rProbR, data=toFit)
#Get Coefficients of linear regression of AB
AApproximation = linearRegression$coefficients[1]
BApproximation = linearRegression$coefficients[2]
#Get probability response for each dose group (P(D[i]))
probabilityResponse.dose0 <- get.Probability.Response.Logistic(AApproximation + BApproximation * 0)
probabilityResponse.dose30 <- get.Probability.Response.Logistic(AApproximation + BApproximation * 30)
probabilityResponse.dose45 <- get.Probability.Response.Logistic(AApproximation + BApproximation * 45)
probabilityResponse.dose60 <- get.Probability.Response.Logistic(AApproximation + BApproximation * 60)
probabilityResponse.dose75 <- get.Probability.Response.Logistic(AApproximation + BApproximation* 75)
probabilityResponse.dose90 <- get.Probability.Response.Logistic(AApproximation + BApproximation * 90)
probabilityResponses <- c(probabilityResponse.dose0, probabilityResponse.dose30, probabilityResponse.dose45, probabilityResponse.dose60, probabilityResponse.dose75, probabilityResponse.dose90)
#Generate number of responses for each litter (Responses)
litterResponses.dose0 <- rbinom(LITTERS.M, litterSize.dose0, probabilityResponse.dose0)
litterResponses.dose30 <- rbinom(LITTERS.M, litterSize.dose30, probabilityResponse.dose30)
litterResponses.dose45 <- rbinom(LITTERS.M, litterSize.dose45, probabilityResponse.dose45)
litterResponses.dose60 <- rbinom(LITTERS.M, litterSize.dose60, probabilityResponse.dose60)
litterResponses.dose75 <- rbinom(LITTERS.M, litterSize.dose75, probabilityResponse.dose75)
litterResponses.dose90 <- rbinom(LITTERS.M, litterSize.dose90, probabilityResponse.dose90)
litterResponse <- c(litterResponses.dose0, litterResponses.dose30, litterResponses.dose45, litterResponses.dose60, litterResponses.dose75, litterResponses.dose90)
litterResponses <- matrix(litterResponse, 6, LITTERS.M)
backgroundResponseProb <- get.Probability.Response.Logistic(AApproximation + BApproximation * 0)
backgroundResponseProb <- backgroundResponseProb + .001
mle(BB(LITTERS.M, litterResponses, litterSizes, probabilityResponse, theta=0))回答 1
Stack Overflow用户
发布于 2015-11-17 14:31:48
我还没有完成整个代码(您应该尝试提供最小的可重复示例),但是您所得到的错误是由于您没有正确地使用mle函数。
mle函数的第一个参数应该是另一个函数,它以候选参数作为参数,并将数据的负日志可能性作为这些参数的函数返回。mle函数的第二个参数是启动参数的命名列表。有关更多细节,请查看?mle。
下面是一个用于拟合正态分布数据的最小示例:
library(stats4)
y <- rnorm(100, 5, 3) ## Example data
mllNorm <- function(mean, log.sd) {-sum(dnorm(y, mean, exp(log.sd), log=TRUE))} ## Minus Gaussian log-likelihood
mle.fit <- mle(mllNorm, start=list(mean=1, log.sd=1)) ## MLE
print(mle.fit)作为一个更一般的提示,我强烈推荐用于MLE的maxLik包。它提供了更灵活的界面、更漂亮的输出和更多的优化选项。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/33756745
复制相关文章
相似问题

