PyMC中的负二项式混合物
PyMC中的负二项式混合物
提问于 2014-06-29 10:40:07
我正试图在PyMC中加入一种负二项式混合物。我似乎做错了什么,因为预测看上去一点也不像输入数据。问题可能是负二项式参数的先验问题。有什么建议吗?
from sklearn.cluster import KMeans
import pymc as mc
n = 3 #Number of components of the mixture
ndata = len(data)
dd = mc.Dirichlet('dd', theta=(1,)*n)
category = mc.Categorical('category', p=dd, size=ndata)
kme = KMeans(n) # This is not needed but it is to help convergence
kme.fit(data[:,newaxis])
alphas = mc.TruncatedNormal('alphas', kme.cluster_centers_[:,0], 0.1, a=0. ,b=100000 ,size=n)
means = mc.TruncatedNormal('means', kme.cluster_centers_[:,0],0.1,a=0.0 ,b=100000, size=n)
@mc.deterministic
def mean(category=category, means=means):
return means[category]
@mc.deterministic
def alpha(category=category, alphas=alphas):
return alphas[category]
obs = mc.NegativeBinomial('obs', mean, alpha, value=data, observed = True)
predictive = mc.NegativeBinomial('predictive', mean, alpha)
model = mc.Model({'dd': dd,
'category': category,
'alphas': alphas,
'means': means,
'predictive':predictive,
'obs': obs})
mcmc = mc.MCMC( model )
mcmc.sample( iter=n_samples, burn=int(n_samples*0.7))回答 1
Stack Overflow用户
回答已采纳
发布于 2014-07-17 21:44:05
您正确地实现了三种分布的混合贝叶斯估计,但是MCMC模型给出了错误的值。
问题是category没有足够快地收敛,而means、alphas和dd中的参数在category决定哪个点属于哪个分布之前就偏离了好的值。
data = np.atleast_2d(list(mc.rnegative_binomial(100., 10., size=s)) +
list(mc.rnegative_binomial(200., 1000., size=s)) +
list(mc.rnegative_binomial(300., 1000., size=s))).T
nsamples = 10000通过可视化category,您可以看到它的后缀是错误的:
G = [data[np.nonzero(np.round(mcmc.trace("category")[:].mean(axis=0)) == i)]
for i in range(0,3) ]
plt.hist(G, bins=30, stacked = True)
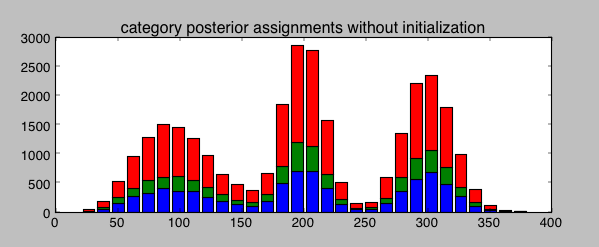
期望最大化是稳定潜在变量的经典方法,但您也可以使用快速和脏的k-均值的结果来为MCMC提供初始值:
category = mc.Categorical('category', p=dd, size=ndata, value=kme.labels_)然后,估计值收敛到看起来合理的值。
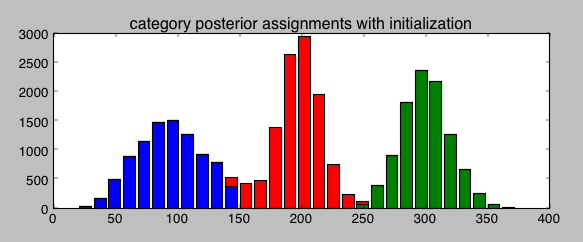
对于alpha的上级,您只需对所有这些都使用相同的发行版:
alphas = mc.Gamma('alphas', alpha=1, beta=.0001 ,size=n)这个问题并不是关于负二项分布的;正态分布的Dirichlet-混合物也是这样失败的;它是由于具有高维范畴分布而导致的,而MCMC在优化方面是不有效的。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/24475293
复制相关文章
相似问题

