利用QR分解、SVD (和Cholesky分解?)计算投影/ hat矩阵。
我试图在R中计算任意N矩阵P的投影矩阵S
P = S (S'S) ^ -1 S'我一直试图使用以下函数来执行此操作:
P <- function(S){
output <- S %*% solve(t(S) %*% S) %*% t(S)
return(output)
}但是当我使用它时,我会得到如下错误:
# Error in solve.default(t(S) %*% S, t(S), tol = 1e-07) :
# system is computationally singular: reciprocal condition number = 2.26005e-28我认为这是数值不稳定和/或不稳定的结果,在许多地方,如R-帮助和这里,但我还没有足够的经验使用SVD或QR分解来解决问题,或者将现有的代码付诸实施。我还尝试了所建议的代码,即将解决方案编写为一个系统:
output <- S %*% solve (t(S) %*% S, t(S), tol=1e-7)但还是不起作用。如有任何建议,将不胜感激。
我很肯定,我的矩阵应该是可逆的,没有任何协线性,如果我试过用一个正交的虚拟变量矩阵来测试它,它仍然不起作用。
另外,我想把它应用到相当大的矩阵中,所以我正在寻找一个简洁的通用解决方案。
回答 1
Stack Overflow用户
发布于 2016-09-02 17:38:51
虽然OP已经一年多没有激活了,但我仍然决定发布一个答复。我将使用X代替S,因为在统计学中,我们通常需要线性回归上下文中的投影矩阵,其中X是模型矩阵,y是响应向量,而H = X(X'X)^{-1}X'是hat /投影矩阵,因此Hy给出了预测值。
这个答案假定为普通最小二乘的上下文。有关加权最小二乘,请参见加权最小二乘回归QR分解的hat矩阵。
概述
solve是基于一般平方矩阵的LU分解。对于对称的X'X (应该由crossprod(X)而不是t(X) %*% X在R中计算),可以使用基于Choleksy分解的chol2inv。
然而,三角分解比QR分解更不稳定。这不难理解。如果X有条件号kappa,X'X将有条件号kappa ^ 2。这会造成很大的数值困难。您得到的错误消息:
# system is computationally singular: reciprocal condition number = 2.26005e-28只是说说而已。kappa ^ 2是关于e-28的,比e-16周围的机器精度小得多。对于容差tol = .Machine$double.eps,X'X将被视为秩亏,因此LU和Cholesky分解将崩溃。
通常,在这种情况下,我们切换到SVD或QR,但是旋转 Cholesky因式分解是另一种选择。
- SVD是最稳定的方法,但成本太高;
- QR具有较好的稳定性,计算费用适中,在实际应用中得到了广泛的应用;
- 旋转Cholesky是快速,可接受的稳定性。对于大矩阵,这是首选。
在下面,我将解释所有三种方法。
使用QR分解的
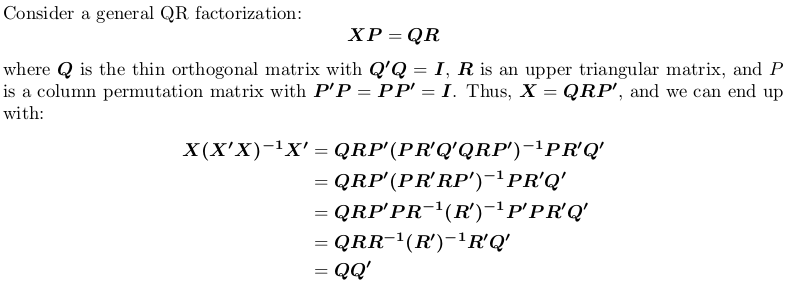
请注意,投影矩阵是与置换无关的,也就是说,我们是否执行带或不旋转的QR因式分解并不重要。
在R中,qr.default可以调用LINPACK例程DQRDC进行无轴QR因式分解,而LAPACK例程DGEQP3用于块旋转QR因式分解。让我们生成一个玩具矩阵并测试这两个选项:
set.seed(0); X <- matrix(rnorm(50), 10, 5)
qr_linpack <- qr.default(X)
qr_lapack <- qr.default(X, LAPACK = TRUE)
str(qr_linpack)
# List of 4
# $ qr : num [1:10, 1:5] -3.79 -0.0861 0.3509 0.3357 0.1094 ...
# $ rank : int 5
# $ qraux: num [1:5] 1.33 1.37 1.03 1.01 1.15
# $ pivot: int [1:5] 1 2 3 4 5
# - attr(*, "class")= chr "qr"
str(qr_lapack)
# List of 4
# $ qr : num [1:10, 1:5] -3.79 -0.0646 0.2632 0.2518 0.0821 ...
# $ rank : int 5
# $ qraux: num [1:5] 1.33 1.21 1.56 1.36 1.09
# $ pivot: int [1:5] 1 5 2 4 3
# - attr(*, "useLAPACK")= logi TRUE
# - attr(*, "class")= chr "qr"注意,对于两个对象,$pivot是不同的。
现在,我们定义了一个包装函数来计算QQ'。
f <- function (QR) {
## thin Q-factor
Q <- qr.qy(QR, diag(1, nrow = nrow(QR$qr), ncol = QR$rank))
## QQ'
tcrossprod(Q)
}我们将看到qr_linpack和qr_lapack给出了相同的投影矩阵:
H1 <- f(qr_linpack)
H2 <- f(qr_lapack)
mean(abs(H1 - H2))
# [1] 9.530571e-17基于奇异值分解的
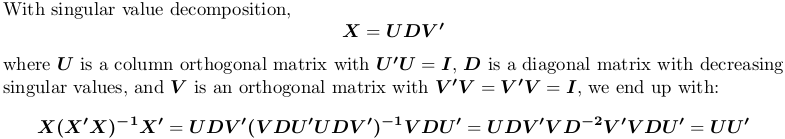
在R中,svd计算奇异值分解。我们仍然使用上面的示例矩阵X
SVD <- svd(X)
str(SVD)
# List of 3
# $ d: num [1:5] 4.321 3.667 2.158 1.904 0.876
# $ u: num [1:10, 1:5] -0.4108 -0.0646 -0.2643 -0.1734 0.1007 ...
# $ v: num [1:5, 1:5] -0.766 0.164 0.176 0.383 -0.457 ...
H3 <- tcrossprod(SVD$u)
mean(abs(H1 - H3))
# [1] 1.311668e-16同样,我们得到了同样的投影矩阵。
使用旋转Cholesky分解的
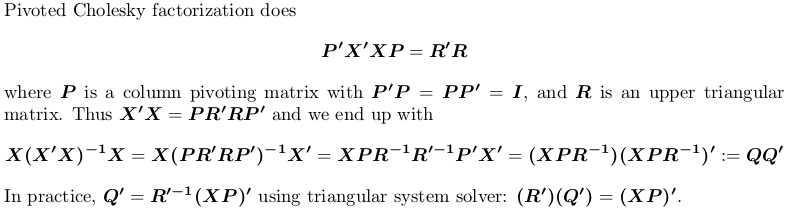
为了进行演示,我们仍然使用上面的示例X。
## pivoted Chol for `X'X`; we want lower triangular factor `L = R'`:
## we also suppress possible rank-deficient warnings (no harm at all!)
L <- t(suppressWarnings(chol(crossprod(X), pivot = TRUE)))
str(L)
# num [1:5, 1:5] 3.79 0.552 -0.82 -1.179 -0.182 ...
# - attr(*, "pivot")= int [1:5] 1 5 2 4 3
# - attr(*, "rank")= int 5
## compute `Q'`
r <- attr(L, "rank")
piv <- attr(L, "pivot")
Qt <- forwardsolve(L, t(X[, piv]), r)
## P = QQ'
H4 <- crossprod(Qt)
## compare
mean(abs(H1 - H4))
# [1] 6.983997e-17同样,我们得到了同样的投影矩阵。
https://stackoverflow.com/questions/9071020
复制相似问题

