R中的AODE机器学习
我想知道真正的AODE是否比朴素的Bayes更好,就像描述中说的那样:
https://cran.r-project.org/web/packages/AnDE/AnDE.pdf
-> "AODE通过对所有小空间进行平均来实现高度精确的分类.“
https://www.quora.com/What-is-the-difference-between-a-Naive-Bayes-classifier-and-AODE
-> "AODE是放松朴素bayes独立性假设的一种奇怪方法。它不再是一种生成模型,但它以一种与logistic回归略有不同(且不那么原则性)的方式放松独立性假设。它用二次(关于特征数)依赖于训练和测试时间来代替用于训练logistic回归分类器的凸优化问题。“
但是当我进行实验时,我发现预测结果似乎是错误的,我用以下代码实现了它:
library(gmodels)
library(AnDE)
AODE_Model = aode(iris)
predict_aode = predict(AODE_Model, iris)
CrossTable(as.numeric(iris$Species), predict_aode)
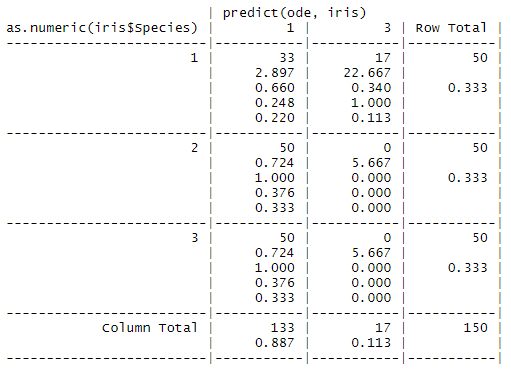
有人能跟我解释一下吗?或者有什么好的实用解决方案来实现AODE?事先谢谢你
回答 1
Stack Overflow用户
发布于 2020-03-12 13:00:01
如果您查看该函数的vignette:
列车: data.frame :培训数据。它应该是一个数据框架。AODE只工作离散数据。在将数据帧传递给此function.However之前,最好先对其进行离散化,如果不进行手工操作,则对数据进行离散化。它使用了一个称为离散化的R包。它使用了众所周知的MDL离散化技术(有时可能会失败)
默认情况下,arules的离散化函数将其分割为3,这可能对虹膜不够。因此,我首先用arules的离散化来再现结果:
library(arules)
library(gmodels)
library(AnDE)
set.seed(111)
trn = sample(1:nrow(indata),100)
test = setdiff(1:nrow(indata),trn)
indata <- data.frame(lapply(iris[,1:4],discretize,breaks=3),Species=iris$Species)
AODE_Model = aode(indata[trn,])
predict_aode = predict(AODE_Model, indata[test,])
CrossTable(as.numeric(indata$Species)[test], predict_aode)
| predict_aode
as.numeric(indata$Species)[test] | 1 | 3 | Row Total |
---------------------------------|-----------|-----------|-----------|
1 | 15 | 5 | 20 |
| 0.500 | 4.500 | |
| 0.750 | 0.250 | 0.400 |
| 0.333 | 1.000 | |
| 0.300 | 0.100 | |
---------------------------------|-----------|-----------|-----------|
2 | 11 | 0 | 11 |
| 0.122 | 1.100 | |
| 1.000 | 0.000 | 0.220 |
| 0.244 | 0.000 | |
| 0.220 | 0.000 | |
---------------------------------|-----------|-----------|-----------|
3 | 19 | 0 | 19 |
| 0.211 | 1.900 | |
| 1.000 | 0.000 | 0.380 |
| 0.422 | 0.000 | |
| 0.380 | 0.000 | |
---------------------------------|-----------|-----------|-----------|
Column Total | 45 | 5 | 50 |
| 0.900 | 0.100 | |
---------------------------------|-----------|-----------|-----------|您可以看到预测中缺少一个类。让我们把它提高到4:
indata <- data.frame(lapply(iris[,1:4],discretize,breaks=4),Species=iris$Species)
AODE_Model = aode(indata[trn,])
predict_aode = predict(AODE_Model, indata[test,])
CrossTable(as.numeric(indata$Species)[test], predict_aode)
| predict_aode
as.numeric(indata$Species)[test] | 1 | 2 | 3 | Row Total |
---------------------------------|-----------|-----------|-----------|-----------|
1 | 20 | 0 | 0 | 20 |
| 18.000 | 4.800 | 7.200 | |
| 1.000 | 0.000 | 0.000 | 0.400 |
| 1.000 | 0.000 | 0.000 | |
| 0.400 | 0.000 | 0.000 | |
---------------------------------|-----------|-----------|-----------|-----------|
2 | 0 | 10 | 1 | 11 |
| 4.400 | 20.519 | 2.213 | |
| 0.000 | 0.909 | 0.091 | 0.220 |
| 0.000 | 0.833 | 0.056 | |
| 0.000 | 0.200 | 0.020 | |
---------------------------------|-----------|-----------|-----------|-----------|
3 | 0 | 2 | 17 | 19 |
| 7.600 | 1.437 | 15.091 | |
| 0.000 | 0.105 | 0.895 | 0.380 |
| 0.000 | 0.167 | 0.944 | |
| 0.000 | 0.040 | 0.340 | |
---------------------------------|-----------|-----------|-----------|-----------|
Column Total | 20 | 12 | 18 | 50 |
| 0.400 | 0.240 | 0.360 | |
---------------------------------|-----------|-----------|-----------|-----------|只有3个错误。对我来说,这是一个在不过度适应的情况下进行谨慎处理的问题,这可能是很棘手的。
https://stackoverflow.com/questions/60647274
复制相似问题

