Caret分类阈值
我一直在使用gbm在Rstudio中的caret包中查找出现故障的概率。
我用Youden的J找到了最佳分类的阈值,即0.63。我现在如何使用这个阈值?我认为最好的方法是在gbm模型中加入caret的阈值,以获得更准确的预测,然后在训练数据上重新运行模型?目前,它默认为0.5,我找不到一个明显的方法来更新阈值。
或者,阈值是否仅用于将测试数据预测分离为正确的类?这看起来更直截了当,但是假设概率应该根据新的阈值更新,那么我如何反映ROC_AUC图中的变化呢?
任何帮助都将受到感激。谢谢
编辑:我正在处理的完整代码如下:
library(datasets)
library(caret)
library(MLeval)
library(dplyr)
data(iris)
data <- as.data.frame(iris)
# create class
data$class <- ifelse(data$Species == "setosa", "yes", "no")
# split into train and test
train <- data %>% sample_frac(.70)
test <- data %>% sample_frac(.30)
# Set up control function for training
ctrl <- trainControl(method = "cv",
number = 5,
returnResamp = 'none',
summaryFunction = twoClassSummary,
classProbs = T,
savePredictions = T,
verboseIter = F)
# Set up trainng grid - this is based on a hyper-parameter tune that was recently done
gbmGrid <- expand.grid(interaction.depth = 10,
n.trees = 20000,
shrinkage = 0.01,
n.minobsinnode = 4)
# Build a standard classifier using a gradient boosted machine
set.seed(5627)
gbm_iris <- train(class ~ .,
data = train,
method = "gbm",
metric = "ROC",
tuneGrid = gbmGrid,
verbose = FALSE,
trControl = ctrl)
# Calcuate best thresholds
caret::thresholder(gbm_iris, threshold = seq(.01,0.99, by = 0.01), final = TRUE, statistics = "all")
pred <- predict(gbm_iris, newdata = test, type = "prob")
roc <- evalm(data.frame(pred, test$class))回答 1
Stack Overflow用户
发布于 2021-01-26 13:18:32
您的代码中有几个问题。我将使用来自mlbench的PimaIndiansDiabetes数据集,因为它比iris数据集更适合。
首先,对于将数据分割成火车和测试集的代码:
train <- data %>% sample_frac(.70)
test <- data %>% sample_frac(.30)不适合,因为在火车集中出现的一些行也会出现在测试集中。
此外,避免使用函数名作为对象名称,这将节省您的许多头痛从长远来看。
data(iris)
data <- as.data.frame(iris) #bad object name举个例子:
library(caret)
library(ModelMetrics)
library(dplyr)
library(mlbench)
data(PimaIndiansDiabetes, package = "mlbench")创建培训和测试集,您可以使用基R sample来采样行或caret::createDataPartition。createDataPartition更可取,因为它试图保留响应的分布。
set.seed(123)
ind <- createDataPartition(PimaIndiansDiabetes$diabetes, 0.7)
tr <- PimaIndiansDiabetes[ind$Resample1,]
ts <- PimaIndiansDiabetes[-ind$Resample1,]这样,火车组中的行将不会出现在测试集中。
让我们创建模型:
ctrl <- trainControl(method = "cv",
number = 5,
returnResamp = 'none',
summaryFunction = twoClassSummary,
classProbs = T,
savePredictions = T,
verboseIter = F)
gbmGrid <- expand.grid(interaction.depth = 10,
n.trees = 200,
shrinkage = 0.01,
n.minobsinnode = 4)
set.seed(5627)
gbm_pima <- train(diabetes ~ .,
data = tr,
method = "gbm", #use xgboost
metric = "ROC",
tuneGrid = gbmGrid,
verbose = FALSE,
trControl = ctrl)为脱粒机创建概率向量
probs <- seq(.1, 0.9, by = 0.02)
ths <- thresholder(gbm_pima,
threshold = probs,
final = TRUE,
statistics = "all")
head(ths)
Sensitivity Specificity Pos Pred Value Neg Pred Value Precision Recall F1 Prevalence Detection Rate Detection Prevalence
1 200 10 0.01 4 0.10 1.000 0.02222222 0.6562315 1.0000000 0.6562315 1.000 0.7924209 0.6510595 0.6510595 0.9922078
2 200 10 0.01 4 0.12 1.000 0.05213675 0.6633439 1.0000000 0.6633439 1.000 0.7975413 0.6510595 0.6510595 0.9817840
3 200 10 0.01 4 0.14 0.992 0.05954416 0.6633932 0.8666667 0.6633932 0.992 0.7949393 0.6510595 0.6458647 0.9739918
4 200 10 0.01 4 0.16 0.984 0.07435897 0.6654277 0.7936508 0.6654277 0.984 0.7936383 0.6510595 0.6406699 0.9636022
5 200 10 0.01 4 0.18 0.984 0.14188034 0.6821550 0.8750000 0.6821550 0.984 0.8053941 0.6510595 0.6406699 0.9401230
6 200 10 0.01 4 0.20 0.980 0.17179487 0.6886786 0.8833333 0.6886786 0.980 0.8086204 0.6510595 0.6380725 0.9271018
Balanced Accuracy Accuracy Kappa J Dist
1 0.5111111 0.6588517 0.02833828 0.02222222 0.9777778
2 0.5260684 0.6692755 0.06586592 0.05213675 0.9478632
3 0.5257721 0.6666781 0.06435166 0.05154416 0.9406357
4 0.5291795 0.6666781 0.07134190 0.05835897 0.9260250
5 0.5629402 0.6901572 0.15350721 0.12588034 0.8585308
6 0.5758974 0.6979836 0.18460584 0.15179487 0.8288729根据首选的度量提取阈值概率。
ths %>%
mutate(prob = probs) %>%
filter(J == max(J)) %>%
pull(prob) -> thresh_prob
thresh_prob
0.74对试验数据的预测
pred <- predict(gbm_pima, newdata = ts, type = "prob")根据测试集中的响应创建数值响应(0或1),因为这是来自包ModelMetrics的函数所需要的
real <- as.numeric(factor(ts$diabetes))-1
ModelMetrics::sensitivity(real, pred$pos, cutoff = thresh_prob)
0.2238806 #based on this it is clear the threshold chosen is not optimal on this test data
ModelMetrics::specificity(real, pred$pos, cutoff = thresh_prob)
0.956
ModelMetrics::kappa(real, pred$pos, cutoff = thresh_prob)
0.2144026 #based on this it is clear the threshold chosen is not optimal on this test data
ModelMetrics::mcc(real, pred$pos, cutoff = thresh_prob)
0.2776309 #based on this it is clear the threshold chosen is not optimal on this test data
ModelMetrics::auc(real, pred$pos)
0.8047463 #decent AUC and low mcc and kappa indicate a poor choice of thresholdAuc是一种超越所有阈值的度量,因此它不需要指定截止阈值。
由于只使用了一次训练/测试分割,因此性能评估会有偏差。最好是使用嵌套重采样,这样就可以在几个训练/测试分块上评估相同的情况。Here is a way执行嵌套重采样。
编辑:回答评论中的问题。
要创建roc曲线,您不需要计算所有阈值的灵敏度和特异性,只需使用指定的包来完成此任务。其结果是概率将更值得信赖。
我更喜欢使用pROC包:
library(pROC)
roc.obj <- roc(real, pred$pos)
plot(roc.obj, print.thres = "best")
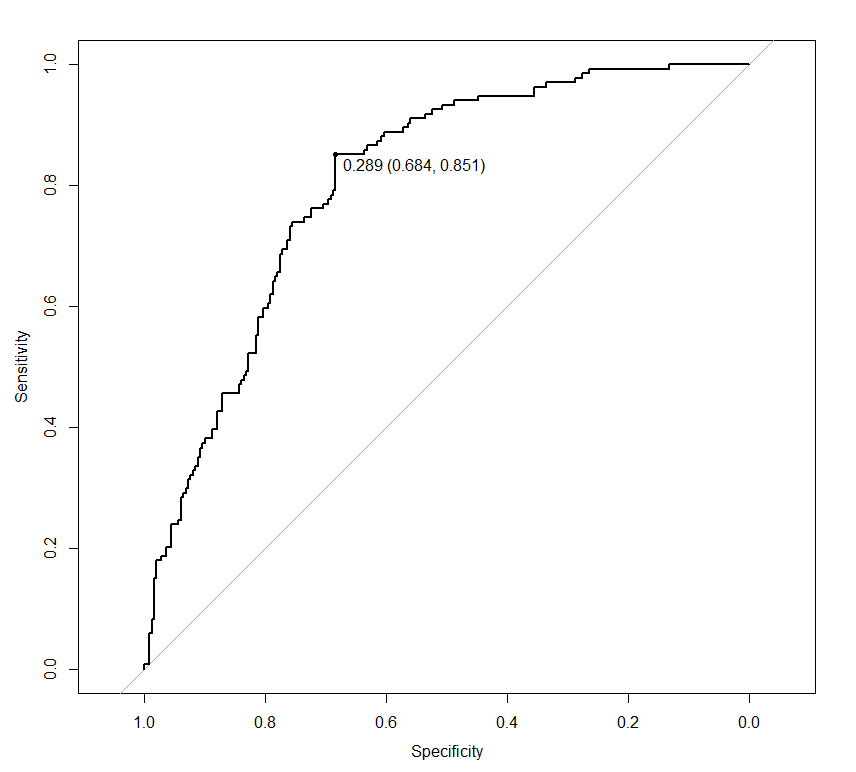
对图形的最佳阈值是对测试数据提供最高特异性+敏感性的阈值。显然,该阈值(0.289)比基于交叉验证的预测(0.74)获得的阈值低得多。这就是我说过的原因,如果你调整交叉验证的预测的阈值并使用它作为阈值成功的指标,那么就会有相当大的乐观偏见。
在上面的例子中,如果不对阈值进行调优,那么测试集的性能就会更好。对于皮马印第安人的数据集来说,这通常是正确的,或者这可能是一个不幸的火车/测试分裂的情况。所以最好使用嵌套重采样来验证这类事情。
https://stackoverflow.com/questions/65844978
复制相似问题

