Phyloseq:交换row.names in otu_table
Phyloseq:交换row.names in otu_table
提问于 2021-12-20 14:56:17
我有理由相信两个V4 16 16SrRNA序列的样品名被交换了。在我的例子中,他们是row.names of otu_table。
既然我已经有了phyloseq对象,我如何更改这些名称以对应于真正的序列?
提前谢谢克里斯蒂娜·保罗
回答 1
Stack Overflow用户
发布于 2022-01-13 21:13:27
这是一个小小的改进,但是您可以将元数据映射与样本合并到phyloseq中。您可以在excel中创建元数据映射,其中文件的名称是第一列(第一列没有标签),与这些文件对应的示例名称是第二列(图中标记为Sample_Name的列)。如果愿意,可以在不同的列中添加有关示例的其他信息。然后将其保存为excel中的.txt文件。
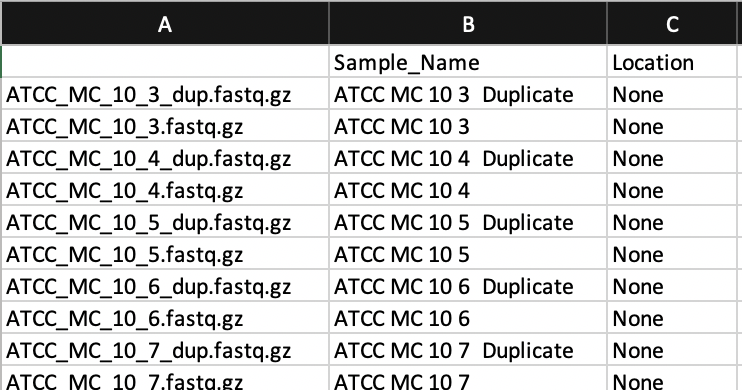
将其保存为.txt文件后,您可以将映射导入R中,如下所示:
map <-import_qiime_sample_data("~/Path_to_your_metadata_map/Metadata_Map.txt")然后,您可以将地图与phyloseq对象合并:
new_phyloseq_object <- merge_phyloseq(old_phyloseq_object, map)然后,如果以后需要制作任何call或其他图形,则可以调用您创建的Sample_Name列。就像这样:
bar_plot <- plot_bar(new_phyloseq_object, x="Sample_Name", fill="Genus")页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/70423720
复制相关文章
相似问题

