免疫组库分析12:TCR、BCR序列相似性网络分析-NAIR包介绍(1)
免疫组库分析12:TCR、BCR序列相似性网络分析-NAIR包介绍(1)
三兔测序学社
发布于 2026-04-17 16:49:26
发布于 2026-04-17 16:49:26
编者语:
在人工智能时代,其实许多R包说明书只需要上传到AI上就能马上解读含义与用法。那为什么还有翻译出来发表了?以前是人写好文章让AI校对。现在让AI写完文章,人工校对。AI是智能,我是人工。另外,这是一个自己使用过的R包,并在免疫组库相关文章中加以引用说明。其实用到的代码也不过几行而已,但当我写完这个R包的相关使用说明,却足足写了4篇文章,一遍翻译一遍学习。免疫组库实验是我开启生信分析的起点,从TCR、BCR实验方法的建立、DNA测序文库构建、高通量测序下机进行生信分析再到文章发表。因此免疫组库分析系列文章要继续更新下去,成为一件值得做的事情。
一、NAIR概述与核心功能
软件定义:NAIR是一个序列相似性网络分析R包,用于分析T细胞和B细胞的适应性免疫组库(Adaptive Immune Repertoire)序列。
主要目标: 识别特定的克隆簇(Clusters)和克隆(Clones)。 计算节点和簇的局部及全局网络属性,揭示免疫库网络的结构组织。
二、支持的数据类型
NAIR支持针对T细胞受体(TCR)或B细胞受体(BCR)的多种测序数据:
单细胞数据(Single-cell data):每一行代表一个单独的细胞。
批量数据(Bulk data):每一行代表一个独特的TCR/BCR克隆(包含V-D-J基因和核苷酸序列的独特组合),通常包含克隆丰度(如克隆计数、频率)的测量值。
三、网络构建模型:
NAIR将免疫库建模为网络图的逻辑如下:
节点定义:每个细胞(单细胞数据)或克隆(批量数据)作为一个节点。
边的建立: 基于受体序列(核苷酸或氨基酸)的相似性。
使用汉明距离(Hamming)或莱文斯坦距离(Levenshtein)衡量节点对之间的差异。 当距离低于指定阈值时,两个节点之间建立连接。
特殊处理:对于单细胞数据,可同时考虑两条链(如α链和β链)的序列来确定细胞间的相似性。
聚类分析:使用多种算法将网络图划分为密集连接的子图(簇)。
可视化:生成可自定义的网络图,节点可根据疾病状态、样本、克隆丰度等元数据着色。
四、安装与操作指南
安装方式: CRAN版本:
install.packages("NAIR")开发版本:通过devtools::install_github从GitHub源码安装。
devtools::install_github(
"mlizhangx/Network-Analysis-for-Repertoire-Sequencing-",
dependencies = TRUE,
build_vignettes = TRUE
)五、核心函数与工作流程
主函数: buildRepSeqNetwork() 或别名 buildNet()。
功能包括数据过滤、网络构建、聚类分析、属性计算及绘图。
特色分析流程: 关联簇搜索:在批量数据中寻找与二元变量(如疾病状态、治疗结果)相关的TCR/BCR簇。
公共簇搜索:识别跨样本共享的相似克隆(例如CDR3氨基酸序列差异不超过一个氨基酸)。
NAIR通过将免疫库转化为网络图,为研究者提供了一套从数据处理到可视化、从结构分析到临床关联挖掘的完整工具链,是探索适应性免疫系统复杂性的有力手段
六、具体功能举例说明
1.模拟数据下载
set.seed(42)
library(NAIR)
dir_out <- tempdir()
toy_data <- simulateToyData()
head(toy_data)
#> CloneSeq CloneFrequency CloneCount SampleID
#> 1 TTGAGGAAATTCG 0.007873775 3095 Sample1
#> 2 GGAGATGAATCGG 0.007777102 3057 Sample1
#> 3 GTCGGGTAATTGG 0.009094910 3575 Sample1
#> 4 GCCGGGTAATTCG 0.010160859 3994 Sample1
#> 5 GAAAGAGAATTCG 0.009336593 3670 Sample1
#> 6 AGGTGGGAATTCG 0.010369470 4076 Sample11.核心代码解释:
net <- buildNet(toy_data, "CloneSeq")该功能需要两个核心参数:data,即一个包含AIRR-seq数据的数据框;以及seq_col,即指定包含TCR、BCR序列的列名或列索引,用于计算序列相似度
2:过滤数据:筛选序列长度、排除无关字符
#筛选序列长度
net <- buildNet(toy_data, "CloneSeq", min_seq_length = 10)
#设定最小长度为10
#排除非标准字母/数字字符的序列,如果序列中包含连字符(-)、星号(*)、空格或其他特殊符号,这些序列都会被过滤掉。
net <- buildNet(toy_data, "CloneSeq", drop_matches = "\\W") 3、(Network Settings)的核心参数
3.1. 距离计算函数 (Distance Function) 该参数决定了如何量化两个 TCR/BCR 序列之间的差异。
默认方法:汉明距离 (Hamming Distance) 计算逻辑:计算两条等长序列在相同位置上的不同字符数量。 处理机制:如果序列长度不同,较短的序列会被填充非匹配字符以匹配较长序列的长度。 适用场景:适用于长度一致的序列比较。
替代方法:莱文斯坦距离 (Levenshtein Distance) 计算逻辑:计算将一个序列转换为另一个序列所需的最少单字符编辑次数(插入、删除、替换)。 优势:能够处理不同长度的序列,特别适合包含插入或删除突变的序列。 推荐场景:在构建 CDR-3 核苷酸序列相似性网络时,推荐使用此方法。 注意:计算复杂度显著高于汉明距离,处理大规模数据集时需谨慎。 代码示例:
# 使用莱文斯坦距离替代默认的汉明距离
net <- buildNet(toy_data, "CloneSeq", dist_type = "lev")3.2. 距离截断值 (Distance Cutoff) 该参数控制网络构建的严格程度,决定了两个节点是否建立连接。 定义:dist_type 函数计算出的距离是一个非负数值,数值越接近 0 表示相似度越高。 默认规则:默认情况下,如果两条序列的距离不超过 1,则两个节点之间会建立一条边(Edge)。
严格度控制:
低截断值:要求更高的序列相似度才能形成连接。
dist_cutoff = 0:只有当两条序列完全相同时,节点才会连接。 代码示例:
# 设置截断值为0,仅允许完全相同的序列连接
net <- buildNet(toy_data, "CloneSeq", dist_cutoff = 03.3. 孤立节点处理 (Keep/Remove Isolated Nodes) 该参数决定网络中是否保留没有连接的节点。 默认行为:drop_isolated_nodes = TRUE。默认情况下,仅保留至少与一个其他节点有边连接的节点,移除所有孤立节点。 保留设置:若设置为 FALSE,网络将保留所有原始数据中的节点,即使它们没有任何连接(孤立节点)。 代码示例:
net <- buildNet(toy_data, "CloneSeq", drop_isolated_nodes = FALSE)4.网络属性和聚类分析
buildRepSeqNetwork() 还可以执行额外的分析,包括聚类分析(将网络图划分为密集连接的子图)和网络属性计算(描述网络的结构组织)。
4.1节点级网络属性 (Node-Level Network Properties)
节点级网络属性与网络图中的单个节点相关。
- 局部属性 (Local Properties):给定节点的值仅取决于网络的一个子集。一个例子是给定节点的网络度(network degree),它代表直接通过边连接到给定节点的其他节点的数量。
- 全局属性 (Global Properties):给定节点的值取决于网络中的所有节点。一个例子是节点的权威分数(authority score),它使用整个图的邻接矩阵计算得出(
在调用 buildRepSeqNetwork() 时设置 node_stats = TRUE,或者作为单独的步骤使用 addNodeStats(),可以计算节点级网络属性
net <- buildNet(toy_data, "CloneSeq", node_stats = TRUE)4.2聚类分析 (Cluster Analysis)
聚类分析使用社区查找算法将网络图划分为簇(clusters)(密集连接的子图)。这些簇代表具有相似受体序列的克隆/细胞组。
在调用 buildRepSeqNetwork() 时设置 cluster_stats = TRUE,或者作为单独的步骤使用 addClusterStats(),可以执行聚类分析。
net <- buildNet(toy_data,"CloneSeq", cluster_stats =TRUE)每个节点的簇成员身份被记录为节点元数据中的一个变量。簇属性(如节点计数和平均序列长度)包含在输出中的独立数据框中。
5.可视化
# 构建克隆序列网络,结果赋值给net变量
net <- buildNet(toy_data, "CloneSeq", # 必选参数:输入数据toy_data,以CloneSeq列为网络节点
node_stats = TRUE, # 开启节点网络统计指标计算
color_nodes_by = c("SampleID", "transitivity", "coreness"), # 3种节点着色依据:样本ID、传递性、核数
color_scheme = c("default", "plasma-1", "mako-1"), # 对应3种配色:默认、plasma、mako
color_title = c("", "Transitivity", "Coreness"), # 对应3个图例标题
size_nodes_by = "degree", # 按节点度(连接数)调整节点大小
node_size_limits = c(0.1, 1.5), # 节点大小范围:最小0.1,最大1.5
plot_title = NULL, # 不设置主标题
plot_subtitle = NULL, # 不设置副标题
print_plots = TRUE # 运行后自动显示网络图
)
saveNetworkPlots(net$plots, outfile = file.path(dir_out, "NAIR_net_3_plots.pdf"))
#保存图片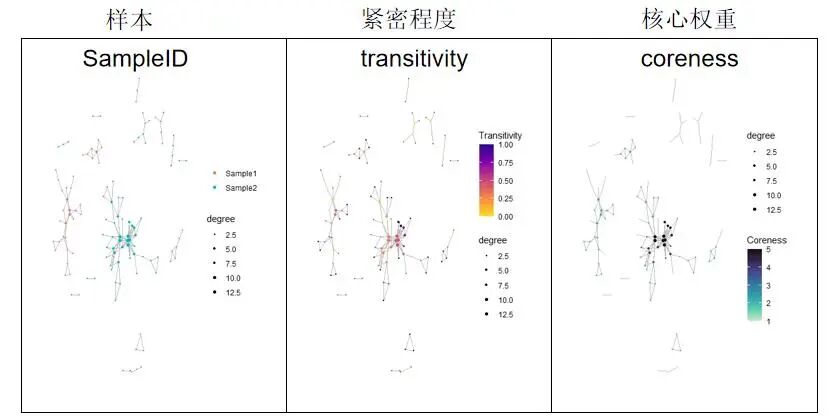
6.输出文件
函数返回一个包含以下元素的列表:
#函数返回一个包含以下元素的列表
:
names(net)
#> [1] "details" "igraph" "adjacency_matrix" "node_data"
#> [5] "plots"具体如下
#Network 元数据 :details记录调用buildRepSeqNetwork()时提供的参数值:
net$details
#> $seq_col
#> [1] "CloneSeq"
#> $dist_type
#> [1] "hamming"
#> $dist_cutoff
#> [1] 1
#> $drop_isolated_nodes
#> [1] TRUE
#> $nodes_in_network
#> [1] 122
#> $min_seq_length
#> [1] 3
#> $drop_matches
#> [1] "NULL"
#Node元数据节点_Data是包含网络节点元数据的数据,其中每一行对应网络图中的一个节点:
head(net$node_data)
#> CloneSeq CloneFrequency CloneCount SampleID degree transitivity
#> 2 GGAGATGAATCGG 0.007777102 3057 Sample1 1 NaN
#> 5 GAAAGAGAATTCG 0.009336593 3670 Sample1 3 0.3333333
#> 8 GGGGAGAAATTGG 0.006220155 2445 Sample1 2 1.0000000
#> 11 GGGGGAGAATTGC 0.012969469 5098 Sample1 4 0.6666667
#> 12 GGGGGGGAATTGC 0.009079646 3569 Sample1 10 0.3555556
#> 13 AGGGGGAAATTGG 0.014941093 5873 Sample1 5 0.1000000
#> eigen_centrality centrality_by_eigen betweenness centrality_by_betweenness
#> 2 1.977313e-17 0.00000000 0.000000 0.000000
#> 5 1.123438e-16 0.00000000 108.000000 108.000000
#> 8 4.558649e-02 0.04558649 0.000000 0.000000
#> 11 1.505537e-01 0.15055366 1.549451 1.549451
#> 12 5.269180e-01 0.52691798 73.970918 73.970918
#> 13 1.468234e-01 0.14682343 75.439560 75.439560
#> authority_score coreness page_rank
#> 2 9.011927e-19 1 0.008196721
#> 5 6.388353e-18 2 0.010578507
#> 8 4.558649e-02 2 0.003936684
#> 11 1.505537e-01 4 0.005034736
#> 12 5.269180e-01 6 0.011491588
#> 13 1.468234e-01 3 0.008703523
Cluster Metadata
names(net$cluster_data)
#> [1] "cluster_id" "node_count"
#> [3] "eigen_centrality_eigenvalue" "eigen_centrality_index"
#> [5] "closeness_centrality_index" "degree_centrality_index"
#> [7] "edge_density" "global_transitivity"
#> [9] "assortativity" "diameter_length"
#> [11] "max_degree" "mean_degree"
#> [13] "mean_seq_length" "seq_w_max_degree"#VisualPlots
#plots是一个列表,其中包含所有生成的图表,以及一个用于存储图表中节点布局的矩阵 graph_layout。每个图表均根据为节点着色所依据的变量进行命名。
names(net$plots)
#> [1] "SampleID" "transitivity" "coreness" "graph_layout"7.结果保存
7.1输出目录 若为 output_dir 参数提供目录路径,buildRepSeqNetwork() 会将其输出写入文件。若指定的输出目录不存在,将自动创建该目录。
7.2 输出文件格式
默认情况下,buildRepSeqNetwork() 返回的列表会以压缩的 RDS 格式保存。 若文件需要在不同计算机之间传输,建议使用 RData 格式,可通过指定 output_type = "rda" 启用。
saveNetwork(net, output_dir = dir_out, output_name = "net", output_type = "rda" )若需要在 R 环境以外使用分析结果,可指定 output_type = "individual"。此时列表中的每个元素将单独保存为文件,
saveNetwork(net, output_dir = dir_out, output_name = "net",output_type = "individual")格式如下: 节点数据(node_data)和聚类数据(cluster_data):.csv 格式(使用 write.csv() 保存,聚类数据设置 row.names = FALSE) 邻接矩阵(adjacency_matrix):.mtx 格式 详细信息(details)、网络图对象(igraph)和绘图布局(plots$graph_layout):.txt 格式 绘图结果(plots):.rda(RData)格式
无论 output_type 如何设置,所有绘图结果都会输出至一个 PDF 文件,每页展示一张图。可通过 plot_width 和 plot_height 参数调整每页尺寸(单位:英寸),默认宽度为 12、高度为 10。
7.3 输出文件命名 默认情况下,所有保存的文件均以 MyRepSeqNetwork 为前缀。可通过 output_name 参数(接收字符串)自定义该前缀。 当 output_type 为 "rds" 或 "rda" 时,仅保存两个文件(数据文件 + PDF 文件),文件名为自定义前缀 + 对应后缀。 示例:若设置 output_name = "NetworkABC" 且 output_type = "rds",生成的文件为 NetworkABC.rds 和 NetworkABC.pdf。 当 output_type = "individual" 时,文件命名规则为自定义前缀 + 后缀标识,规则如下: 详细信息:_Details.txt 网络图边列表:_EdgeList.txt 邻接矩阵:_AdjacencyMatrix.mtx 节点元数据:_NodeMetadata.csv 聚类元数据(若存在):_ClusterMetadata.csv 绘图列表:_Plots.rda 绘图 PDF 文件:.pdf 绘图布局:_GraphLayout.txt 示例:若设置 output_name = "NetworkABC" 且 output_type = "individual",节点元数据将保存为 NetworkABC_NodeMetadata.csv,PDF 绘图文件保存为 NetworkABC.pdf,绘图列表保存为 NetworkABC_Plots.rda,以此类推。
参考文档:
https://mlizhangx.github.io/Network-Analysis-for-Repertoire Sequencing-/articles/buildRepSeqNetwork.html
免疫组库分析合集
【生信分析】免疫组库基础分析2-V/D/J基因使用频率可视化图
【生信分析】免疫组库基础分析3-基于V/D/J使用频率的聚类分析
【生信分析】免疫组库基础分析4-VJ/VDJ组合使用频率计算及可视化
【生信分析】免疫组库基础分析6-克隆子的分布分析(优势克隆与罕见克隆)
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-04-14,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

