无需阴性对照的宏基因组跨样本污染检测工具——CroCoDeEL
无需阴性对照的宏基因组跨样本污染检测工具——CroCoDeEL
用户1075469
发布于 2026-03-25 12:30:03
发布于 2026-03-25 12:30:03
宏基因组测序在微生物组研究中应用广泛,但样本间交叉污染这个技术问题一直被严重低估。这种污染通常发生在96孔板中相邻样本之间,会导致物种丰度失真、假阳性发现,甚至影响研究结论的可靠性。现有检测方法要么依赖阴性对照(成本高且不够全面),要么基于菌株水平分析(计算量大且无法区分自然菌株共享)。研究人员开发的CroCoDeEL工具另辟蹊径,仅需物种丰度表就能准确识别污染样本及其污染源,还能估算污染比例。更重要的是,研究团队在多个高引用率研究中发现了严重的未报告污染问题,提示这可能是宏基因组领域普遍存在却被忽视的质控盲区。
摘要
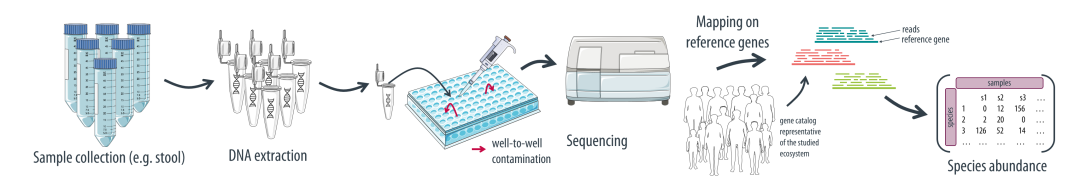
背景 宏基因组测序能深入解析微生物群落,但常受技术偏倚影响,其中交叉样本污染尤为突出。这种污染源于实验室处理过程中样本间的物质交换,会扭曲微生物谱并影响下游分析的可靠性。现有检测方法依赖阴性对照,既不方便也无法检测真实样本内部的污染。而菌株水平的生信分析方法既无法区分污染与自然菌株共享,灵敏度也不足。
结果 研究团队开发了CroCoDeEL,这是一个无需对照的交叉样本污染检测和定量工具。该工具通过线性建模和预训练的监督学习模型,识别物种丰度谱中的特异性污染模式。在三个公开数据集的基准测试中,CroCoDeEL准确检测出污染样本并识别污染源,即使在低污染率(小于0.1%)情况下也能有效工作,前提是测序深度足够。值得注意的是,研究团队在多个高引用率研究中发现了严重污染案例,这些污染可能影响了原研究的部分结论。
结论 研究证实交叉样本污染会在物种丰度谱中产生特异性的"污染线"模式,这种模式在非污染样本对中出现概率极低(少于万分之一)。CroCoDeEL通过自动检测这一模式,实现了无需阴性对照、不依赖样本位置信息的污染识别,能同时确定污染源和被污染样本,并估算污染率。工具在真实数据上达到约0.7的Matthews相关系数和95%的召回率,且计算效率高。
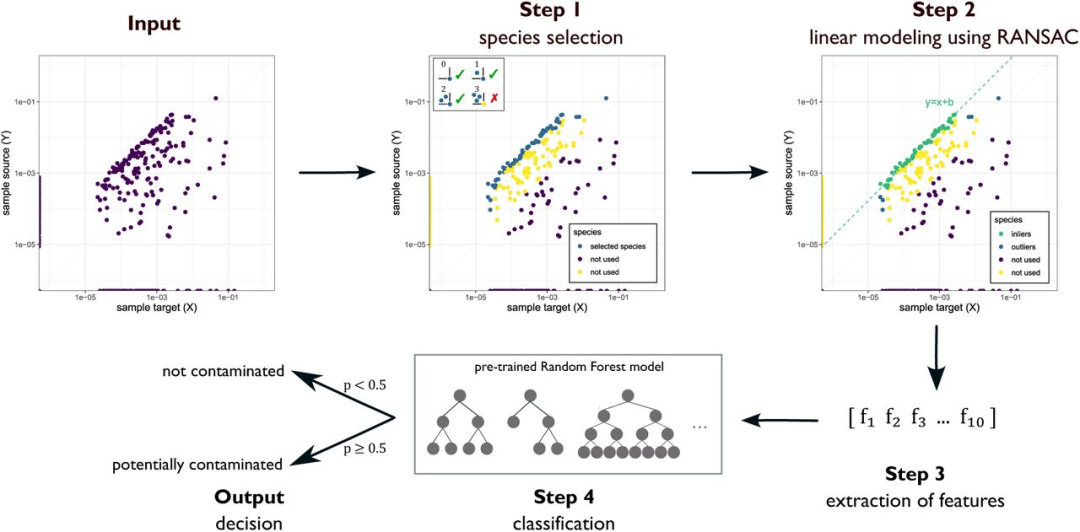
主要结果
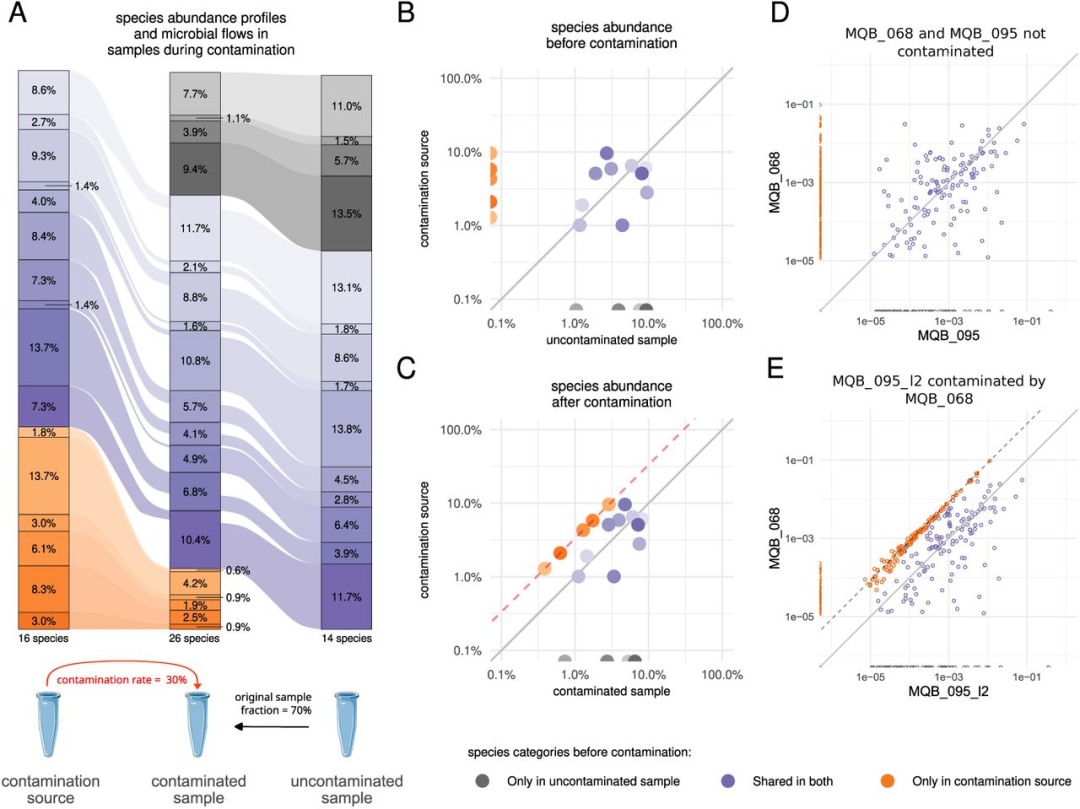
污染线的发现与验证 在真实混合样本实验中,MQB_095_l2(被MQB_068以约10%污染)的物种丰度散点图清晰展现了污染线特征(红色虚线)。所有MQB_068中丰度较高的物种都在MQB_095_l2中被检测到(y轴上无点),且部分共有物种沿一条直线排列,表明这些是污染引入的特异性物种。相比之下,两个未污染样本MQB_095和MQB_068的对比图中没有这种模式。更重要的是,MQB_095的物种丰富度(194)显著低于其污染版本MQB_095_l2(319),意味着39%的检出物种实际是污染假象。
分类器性能 在三个真实人类粪便宏基因组测试集上(样本量分别为110、128、237),CroCoDeEL表现一致。Matthews相关系数均在0.7左右,召回率平均95%,说明能检出人工专家标注的绝大多数污染案例。精确度约50%,但这里的"假阳性"值得商榷——这些案例多数污染率很低(平均0.26%),分类器给出的置信度也显著低于真阳性(概率0.73 vs 0.92,p<2.2×10^-16)。当在跨数据集的140972个样本对(理论上不可能污染)中测试时,仅检出5个假阳性,证明了在污染确实不存在时工具的高特异性。
假阴性分两类:一类是极低污染率且人工专家信心也不高的案例;另一类更棘手,是一些高污染但污染线模糊的情况,比如两个样本都被第三方污染导致的传递性相似,或者"级联污染"(一个样本污染另一个后自己又被污染)。
计算资源方面,在标准节点(双Intel Xeon E5-2680,16核256GB内存)上处理百个样本仅需数分钟,运行时间与样本对数呈线性关系,CPU并行效率约0.85,内存消耗低且稳定。
测序深度、污染率和分类器的影响 用25个半模拟样本对系统评估了影响因素。测序深度和污染率都是关键因素(p<2×10^-16)。以Meteor2为例,20%污染率时即使1M reads也能全检出,但2%污染率时需要10M reads才能达到92%召回率(1M reads仅40%)。
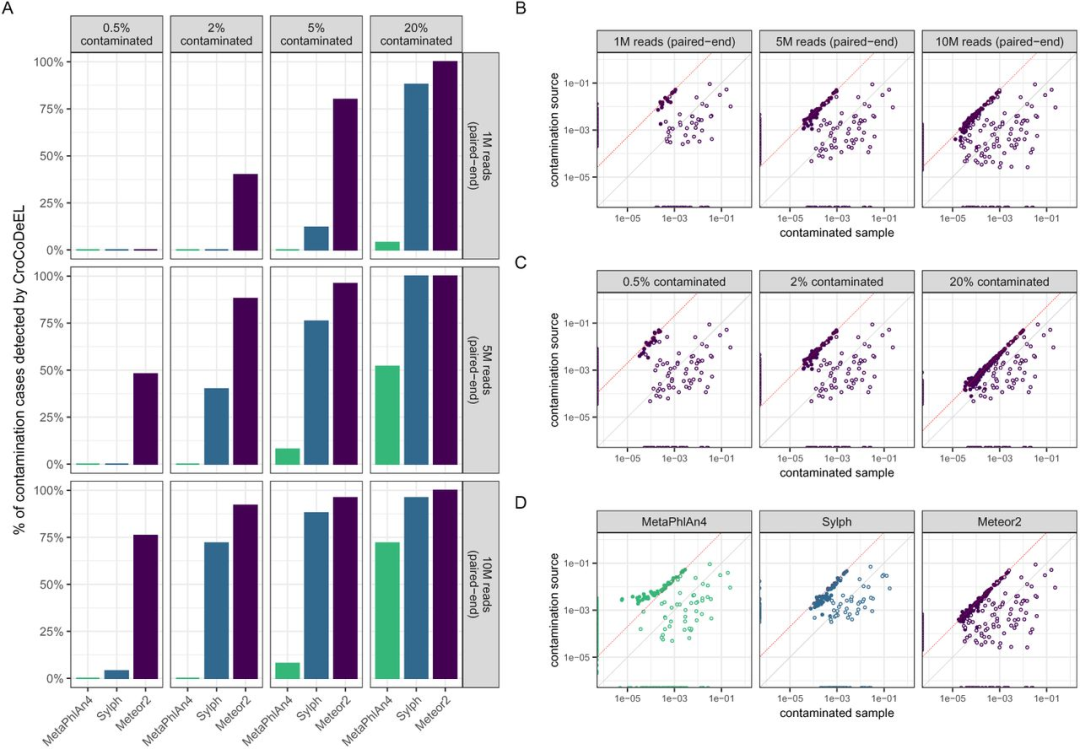
分类器选择影响巨大。在10M reads、0.5%污染率条件下,Meteor2的召回率达76%,而Sylph仅4%,MetaPhlAn4完全检测不到。原因在于Meteor2对亚优势物种的检测灵敏度更高,定量也更准确,能在污染线上产生更多物种且离散度更小。MetaPhlAn4系统性低估亚优势物种丰度,干扰了污染线检测,虽然过滤掉低丰度物种后有所改善,但Meteor2仍是低测序深度/低污染率场景的唯一有效选择。
与菌株共享方法的对比 在Lou等人的婴儿纵向队列研究(P3板)中,菌株共享方法仅识别出2个污染样本(阴性对照NC3和样本63D9),且无法确定具体污染源。CroCoDeEL则检出16个人工验证的污染事件,涉及12个污染样本。CroCoDeEL不仅确认了63D9被58D256和60D38污染(与这两个样本共享菌株数最多),还发现NC3被82D361、83D88和83D249污染而非82M。
更关键的是,CroCoDeEL检出了菌株方法无能为力的场景:同一婴儿不同时间点样本间的污染(如63D9被其后期样本63D250以70%污染)、双胞胎样本间污染(58D256污染60D38)、母婴样本污染(58M以63%污染58D7,后者物种丰富度达223远超同龄婴儿)。这些都因自然菌株传递而被菌株方法排除,但CroCoDeEL利用婴儿肠道菌群随时间演化的特点成功识别。
未检测污染导致的错误结论 在Lou等人关于婴儿肠道定植的另一项研究中,作者认为P1、P2、P5板无污染,但CroCoDeEL在P2中发现8个污染事件,包括关键案例57D8被母亲样本57M以23%污染。原研究报道的"母亲菌株在婴儿出生时定植但未持续"很可能是污染假象而非真实定植。
在Ferretti等人的高引用率婴儿研究中,182个样本中有48个被污染(26%)。原文报道的56个"瞬时出现"微生物中,80%(45个)实际来自5个被大量污染(污染率>10%)的新生儿粪便样本。原研究观察到婴儿首次采样(t1)的物种多样性显著高于后续时间点(t2: p=0.005, t3: p=0.003),但剔除高污染样本后这种差异消失(t2: p=0.12, t3: p=0.56),说明表观多样性增高只是污染假象。
在TwinsUK队列的1004个成人粪便样本中,CroCoDeEL检出202个污染样本,其中176个关联到8个相同污染源。这8个源样本彼此极相似(Spearman ρ>0.96)且物种丰富度异常高(782±8),疑似是多样本混合物的重复。污染样本间的Bray-Curtis距离(0.40)显著小于非污染样本(0.53, p<2×10^-16),物种丰富度也更高(425 vs 303, p<2×10^-16)。在至少出现于10个样本的1382个物种中,32%(440个)在污染样本中流行率显著更高(FDR≤0.01),凸显了基于该队列的众多研究需要重新评估的紧迫性。
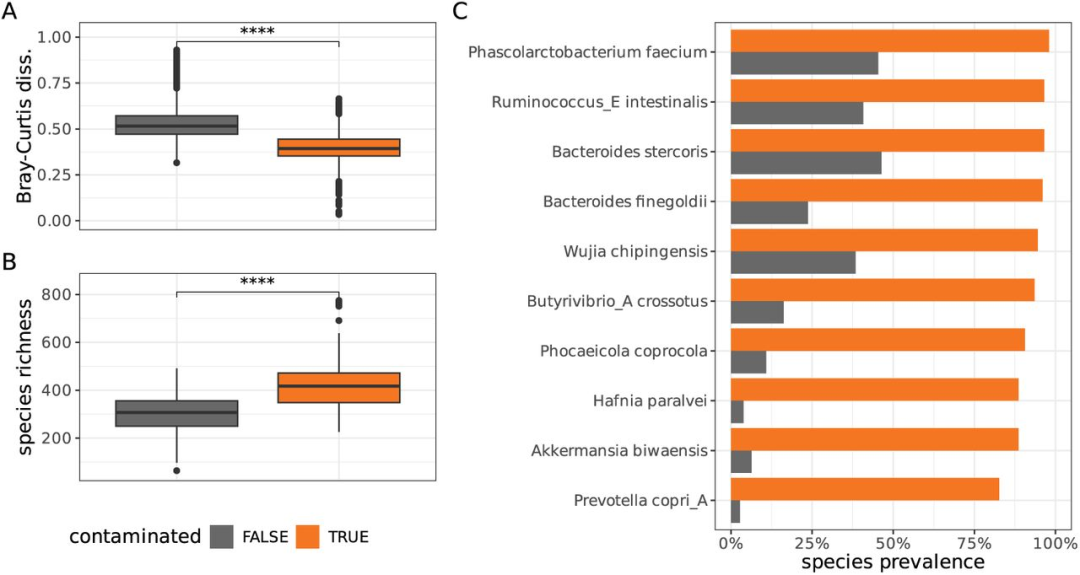
CroCoDeEL 使用说明
软件介绍
CroCoDeEL是专门检测宏基因组数据中交叉样本污染的工具。它能识别污染样本、定位污染源、估算污染率,只需要物种丰度表即可运行,不需要阴性对照或样本板位信息。
安装方式
推荐使用conda安装(最简单)
conda create --name crocodeel_env -c conda-forge -c bioconda crocodeel
conda activate crocodeel_env或使用pip安装(需要Python ≥3.12)
pip install crocodeel安装测试
crocodeel test_install这条命令会在测试数据集上运行CroCoDeEL,验证安装是否成功。加上--keep-results参数可以保留结果查看。
输入文件要求
需要准备TSV格式的物种丰度表,第一列是物种名称,其他列是各样本中的物种丰度(相对丰度)。格式示例:
species_name | sample1 | sample2 | sample3 |
|---|---|---|---|
species_1 | 0 | 0.05 | 0.07 |
species_2 | 0.1 | 0.01 | 0 |
重要提示:CroCoDeEL需要准确定量亚优势物种。强烈建议使用Meteor软件包生成丰度表,也可用MetaPhlAn4(但检测低污染能力会下降)。不建议用其他分类器,准确性达不到要求。
基本使用流程
1. 检测污染
crocodeel search_conta -s species_abundance.tsv -c contamination_events.tsv输出文件contamination_events.tsv包含检测到的所有污染事件,每个事件包括污染源、被污染样本、污染率估计值、随机森林模型打分、污染引入的特异性物种列表等信息。
如果用MetaPhlAn4生成丰度表,务必加过滤参数:
crocodeel search_conta -s species_abundance.tsv --filter-low-ab 20 -c contamination_events.tsv这个--filter-low-ab 20参数会过滤掉低丰度物种,提高灵敏度。
2. 结果可视化
crocodeel plot_conta -s species_abundance.tsv -c contamination_events.tsv -r contamination_events.pdf生成PDF报告,包含每个污染事件的对数散点图,x轴是被污染样本,y轴是污染源,红色线标出污染特异性物种。
3. 一步完成(推荐)
crocodeel easy_wf -s species_abundance.tsv -c contamination_events.tsv -r contamination_events.pdf一条命令完成污染检测和PDF报告生成。
结果解读注意事项
CroCoDeEL可能会对物种组成相似的样本误报污染(比如纵向采样、同笼饲养动物等)。即使是不相关样本,偶尔也会有假阳性。强烈建议人工检查PDF报告中的散点图,识别并剔除可能的假阳性结果。理论上,污染过程中不应有超过污染线的点。然而,有时可能会有点,尤其是在级联污染的情况下。在这种情况下,可以容忍一些细节。
例如,这里有一个级联污染的案例。样本2被样本1污染,但污染线上方有点(图a)。实际上,样本1也被另一个样本污染(样本3,图b)。这种污染解释了污染线上方的点。如果再次处理样品1(sample1_new),它不再被样品3污染(图c),污染线以上的点也消失(图d)。
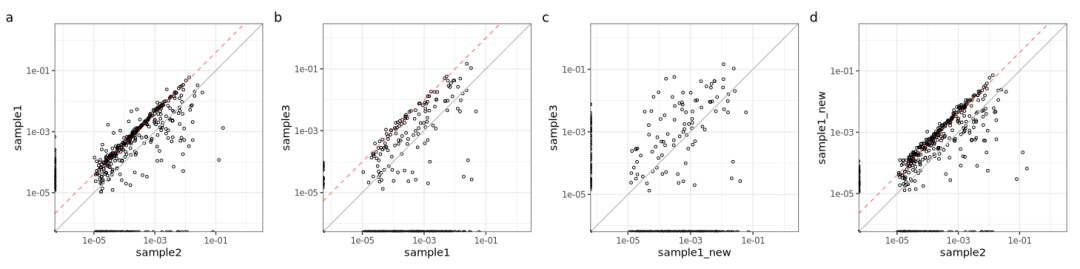
当一个箱子包含污染线以上的点时,观察污染源是否随后被其他样本污染就很有趣。
高级功能:训练自定义模型
如果有标注好的污染/非污染样本对数据集,可以训练自己的随机森林分类模型:
# 下载官方训练集(可选,用于测试)
wget --content-disposition 'https://entrepot.recherche.data.gouv.fr/api/access/datafile/:persistentId?persistentId=doi:10.57745/IBIPVG'
xz -d training_dataset.meteor.tsv.xz
# 训练新模型
crocodeel train_model -s training_dataset.meteor.tsv -m crocodeel_model.tsv -r crocodeel_model_perf.tsv
# 使用自定义模型
crocodeel search_conta -s species_ab.tsv -m crocodeel_model.tsv -c conta_events.tsv重现论文结果
论文中的训练集、验证集、测试集物种丰度表都已公开。以Lou等人数据集的P3为例:
# 下载数据
wget --content-disposition 'https://entrepot.recherche.data.gouv.fr/api/access/datafile/:persistentId?persistentId=doi:10.57745/BH1RKY'
# 运行分析
crocodeel easy_wf -s PRJNA698986_P3.meteor.tab -c PRJNA698986_P3.meteor.crocodeel.tsv -r PRJNA698986_P3.meteor.crocodeel.pdf参考文献
- • Goulet, L. et al. "CroCoDeEL: accurate control-free detection of cross-sample contamination in metagenomic data" bioRxiv (2025). https://doi.org/10.1101/2025.01.15.633153
- • Ricci, L., Heidrich, V., Punčochář, M. et al. Baby-to-baby strain transmission shapes the developing gut microbiome. Nature (2026). https://doi.org/10.1038/s41586-025-09983-z
- • https://github.com/metagenopolis/CroCoDeEL
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2026-02-08,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

