Nat. Commun. | 基因型导向的抗癌小分子生成:G2D-Diff 模型的机制与应用探索
Nat. Commun. | 基因型导向的抗癌小分子生成:G2D-Diff 模型的机制与应用探索

MindDance
发布于 2026-01-08 12:54:22
发布于 2026-01-08 12:54:22
在肿瘤异质性与药物靶点稀缺的双重挑战下,精准肿瘤学的发展始终面临瓶颈。近日,发表于 《Nature Communications》 的研究 A genotype-to-drug diffusion model for generation of tailored anti-cancer small molecules 提出了一种突破性的生成式AI模型——Genotype-to-Drug Diffusion(G2D-Diff),为个性化抗癌药物研发提供了全新范式。本文将从模型创新、技术细节、性能验证及临床价值四个维度,全面解读这一研究的核心贡献。
一、模型定位:破解传统药物研发的双重困境
当前AI驱动的药物生成方法存在两类局限:
- • 靶点依赖型方法:需预先明确疾病相关蛋白靶点,通过微调模型或强化学习生成靶向化合物,但在癌症等复杂疾病中,“最佳靶点未知”和“脱靶效应”问题突出。
- • 表型驱动型方法:聚焦药物诱导的表型结果(如基因表达变化),但现有模型多依赖临床稀缺的基因表达数据,且易受批次效应干扰,生成可靠性受限。
G2D-Diff的创新性在于:直接以癌症基因型(而非基因表达)为输入条件,通过扩散模型生成符合预期疗效的小分子结构。这种设计既规避了靶点依赖,又提升了临床适用性——基因型数据(如突变、拷贝数变异)在临床实践中更易获取且稳定性更高。
二、技术架构:多模块协同的生成式AI系统
G2D-Diff的核心架构由三个关键组件构成,形成“编码-扩散-解码”的完整流程。
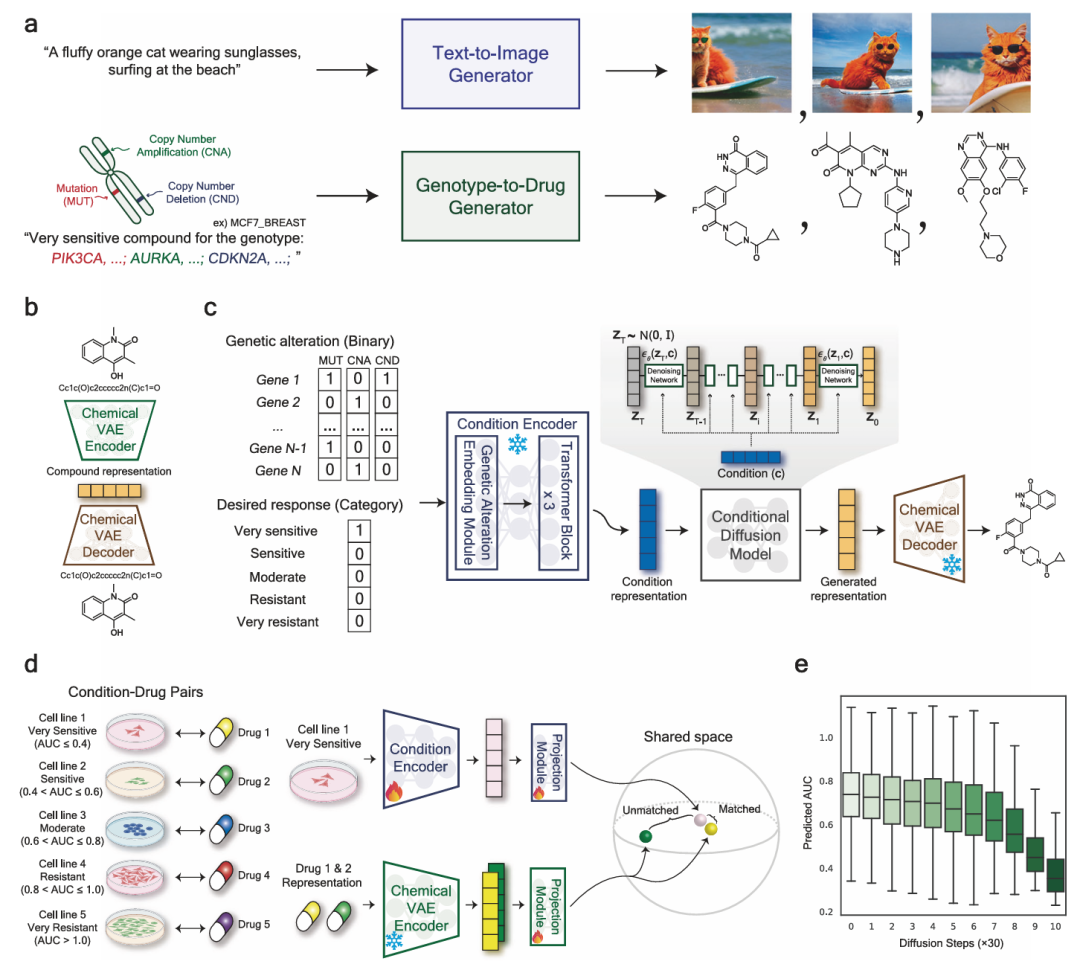
图1展示了G2D-Diff的工作流程。a图呈现了G2D-Diff与文本到图像生成器相似的一般概念;b图为化学VAE的总体架构,其能在潜在空间中实现扩散过程;c图是基因型到药物潜在扩散模型这一核心模块的工作流程;d图详细说明了条件编码器的预训练过程,包括条件-药物对数据的构建以及对比学习的应用;e图展示了在生成示例条件(MCF7,非常敏感)时,预测的AUC随扩散步骤的变化情况
图1展示了G2D-Diff的工作流程。a图呈现了G2D-Diff与文本到图像生成器相似的一般概念;b图为化学VAE的总体架构,其能在潜在空间中实现扩散过程;c图是基因型到药物潜在扩散模型这一核心模块的工作流程;d图详细说明了条件编码器的预训练过程,包括条件-药物对数据的构建以及对比学习的应用;e图展示了在生成示例条件(MCF7,非常敏感)时,预测的AUC随扩散步骤的变化情况
1. 化学变分自编码器(Chemical VAE)
- • 功能:构建分子latent空间,将SMILES格式的化学结构转换为128维向量。
- • 性能:在150万化合物训练集上,重构任务的有效性(validity)和唯一性(uniqueness)均达1.0,随机生成任务的有效性达0.86,且生成分子的类药性指标(QED、SAS、LogP)与真实药物库分布高度吻合。
- • 优势:相比传统SMILES编码,通过latent空间实现分子结构的连续化表示,为后续扩散过程提供平滑优化基础。
2. 条件编码器(Condition Encoder)
- • 输入:二元化基因型数据(718个临床相关基因的突变、拷贝数扩增/缺失)+预期疗效等级(5类:极敏感至极耐药)。
- • 创新点:
- • 采用对比学习预训练(受CLIP框架启发),使条件编码同时捕获基因型、疗效及药物结构信息。
- • transformer模块引入NeST肿瘤层级ontology约束,仅允许同系统基因间的信息交互,模拟生物通路的关联性。
- • 效果:PCA分析显示,编码向量可清晰区分疗效等级(PC1轴)和基因型差异(PC2轴),对敏感条件的药物识别准确率显著高于随机水平。
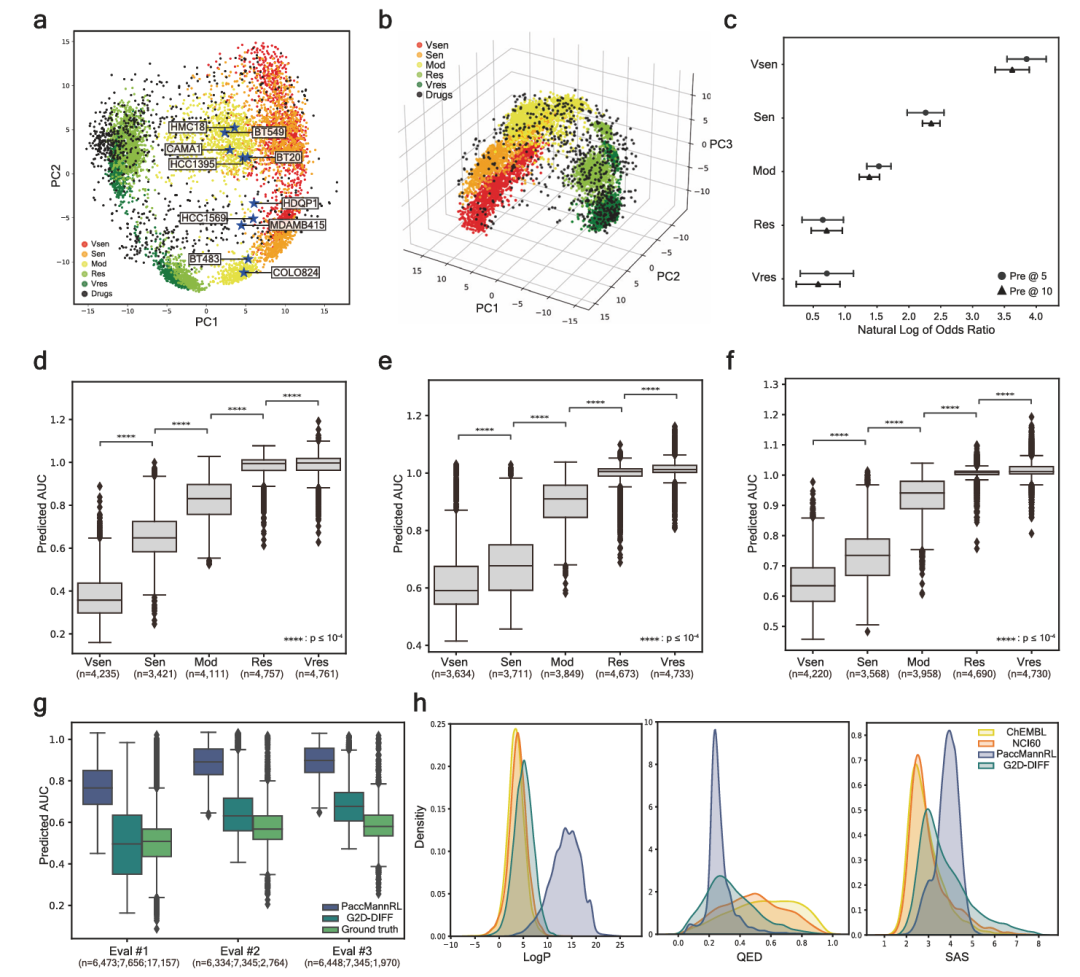
图2为G2D-Diff的综合性能评估结果。a图为共享空间中条件和药物编码的2D PCA图,不同颜色点代表不同条件,黑色点代表药物,PC1轴基于反应类别区分条件,PC2轴根据基因型差异区分条件;b图为3D PCA图,PC3轴在敏感和耐药类别内进一步分层;c图展示了精度为5(圆圈)和精度为10(三角形)时的自然对数优势比;d-f图分别为三个评估集中条件生成化合物的预测AUC分布;g图对比了PaccMannRL和G2D-Diff生成的敏感化合物的预测AUC分布;h图展示了PaccMannRL、G2D-Diff生成化合物以及ChEMBL和NCI60中随机采样化合物的LogP、QED和SAS密度
图2为G2D-Diff的综合性能评估结果。a图为共享空间中条件和药物编码的2D PCA图,不同颜色点代表不同条件,黑色点代表药物,PC1轴基于反应类别区分条件,PC2轴根据基因型差异区分条件;b图为3D PCA图,PC3轴在敏感和耐药类别内进一步分层;c图展示了精度为5(圆圈)和精度为10(三角形)时的自然对数优势比;d-f图分别为三个评估集中条件生成化合物的预测AUC分布;g图对比了PaccMannRL和G2D-Diff生成的敏感化合物的预测AUC分布;h图展示了PaccMannRL、G2D-Diff生成化合物以及ChEMBL和NCI60中随机采样化合物的LogP、QED和SAS密度
3. 潜在扩散模型(Latent Diffusion Model)
- • 机制:在化学VAE构建的latent空间中,通过300步去噪过程,逐步将随机噪声优化为符合条件的分子向量。
- • 条件注入:每步去噪均引入条件编码器输出的向量,通过自适应实例归一化(AdaIN)实现基因型与分子结构的关联。
- • 可控性:采用无分类器引导(classifier-free guidance)技术,通过调节CFG参数(实验中设为7)平衡生成多样性与条件匹配度。
三、性能验证:多维度超越现有方法
研究通过三类评估集(已知细胞系、数据稀缺细胞系、零样本细胞系),从生成质量、条件适配性和临床相关性三个层面验证了模型性能:
1. 基础生成能力
与主流方法PaccMannRL相比,G2D-Diff的优势显著:
- • 多样性:Tanimoto相似度计算显示,生成分子的平均pairwise距离达0.87(PaccMannRL为0.63)。
- • 真实性:Fréchet ChemNet距离(FCD)和最优传输距离(OTD)更接近真实药物分布,表明生成结构更符合化学规律。
- • 类药性:QED>0.8的分子占比高出PaccMannRL 15%,SAS<4.5(合成可行性高)的分子占比提升20% 。
2. 结构与功能特性分析
G2D-Diff生成的化合物在结构多样性与功能相关性上表现突出。
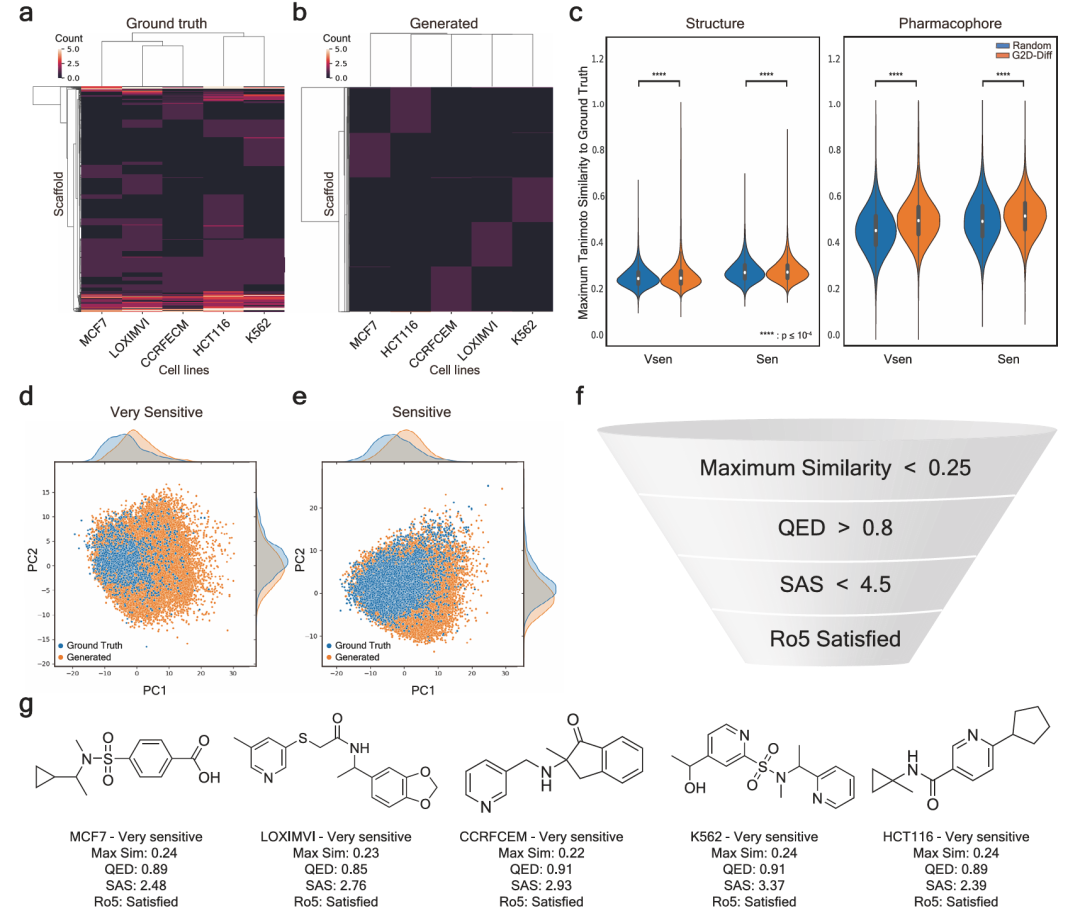
图3展示了G2D-Diff生成化合物的结构分析及潜在候选药物。a图为已知极敏感化合物的骨架频率聚类图;b图为生成的极敏感化合物的骨架频率聚类图,两图中每列代表评估集1中的一个细胞系,每行代表独特骨架的频率计数,频率越高颜色越亮;c图对比了化学VAE随机生成化合物与G2D-Diff生成化合物的最大结构和药效团相似度;d-e图分别为极敏感和敏感化合物基于理化性质的2D PCA图;f图为每个细胞系筛选潜在类药候选药物的标准;g图为与查询细胞系对应的选定潜在类药候选药物
图3展示了G2D-Diff生成化合物的结构分析及潜在候选药物。a图为已知极敏感化合物的骨架频率聚类图;b图为生成的极敏感化合物的骨架频率聚类图,两图中每列代表评估集1中的一个细胞系,每行代表独特骨架的频率计数,频率越高颜色越亮;c图对比了化学VAE随机生成化合物与G2D-Diff生成化合物的最大结构和药效团相似度;d-e图分别为极敏感和敏感化合物基于理化性质的2D PCA图;f图为每个细胞系筛选潜在类药候选药物的标准;g图为与查询细胞系对应的选定潜在类药候选药物
- • 骨架多样性:生成化合物的骨架数量与化合物总数接近,且不同响应类别间的骨架重叠极少,显著高于已知化合物的骨架多样性。
- • 药效团保留:与随机生成化合物相比,G2D-Diff生成的分子在结构相似度略高的同时,药效团相似度显著提升,表明模型能捕获关键功能特征而非单纯模仿已知结构。
- • 理化性质合理性:PCA分析显示,生成化合物的理化性质分布覆盖已知敏感化合物的全部范围,且毒性评估(ADMETlab 3.0)显示其体内毒性显著低于已知药物。
3. 条件适配性
- • 疗效匹配:生成分子的预测AUC值(通过独立模型G2D-Pred评估)随预期疗效等级呈阶梯式变化,极敏感与极耐药组的差异达统计学显著(p<10⁻⁴)。
- • 基因型特异性:对同一疗效等级的不同细胞系,生成分子的scaffolds重叠率<5%,而传统方法达30%以上。
4. 零样本泛化能力
在三阴性乳腺癌(TNBC)案例中:
- • 对未见过的HS578T细胞系,生成分子的AUC分布与已知敏感药物高度吻合,且scaffolds全新(与已知药物的Tanimoto相似度<0.25)。
- • 针对临床TNBC患者基因型,生成化合物的作用通路(如CDK相关通路)与已知有效药物(如Dinaciclib)的靶点高度一致,docking模拟显示相似结合能(-8.5 kcal/mol)。
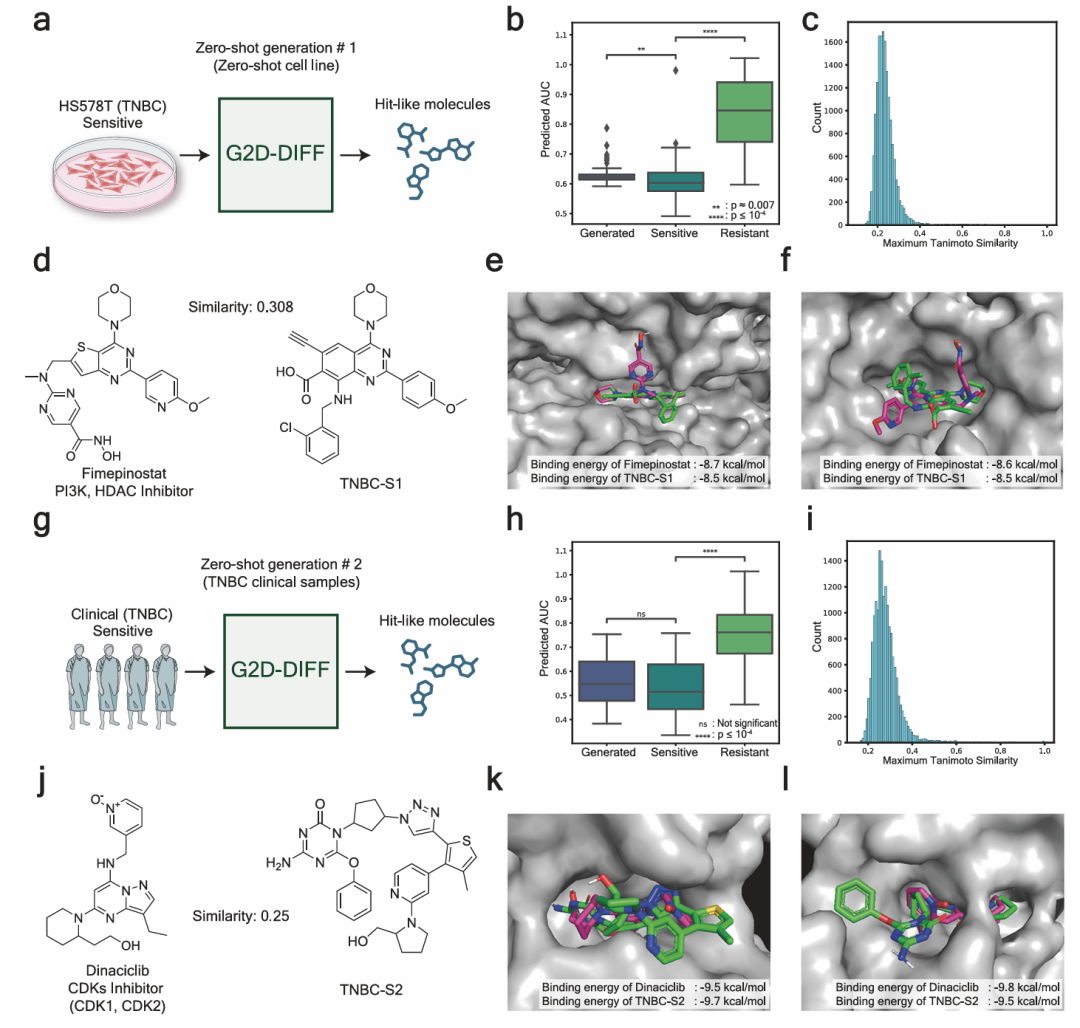
图4展示了零样本案例研究的工作流程和结果。a图为针对未见过的TNBC细胞系HS578T的第一个零样本案例研究工作流程;b图为生成化合物、已知敏感和耐药化合物的预测AUC分布;c图为生成化合物与已知敏感化合物的最大Tanimoto相似度直方图;d图为Fimepinostat和生成化合物TNBC-S1的化学结构;e-f图分别为Fimepinostat和TNBC-S1在PI3Ka和HDAC1上的对接模拟结果;g图为针对未见过的临床患者的第二个零样本案例研究工作流程;h图为生成化合物、已知敏感和耐药化合物的预测AUC分布;i图为生成化合物与已知敏感化合物的最大Tanimoto相似度直方图;j图为Dinaciclib和生成化合物TNBC-S2的化学结构;k-l图分别为Dinaciclib和TNBC-S2在CDK1和CDK2上的对接模拟结果
图4展示了零样本案例研究的工作流程和结果。a图为针对未见过的TNBC细胞系HS578T的第一个零样本案例研究工作流程;b图为生成化合物、已知敏感和耐药化合物的预测AUC分布;c图为生成化合物与已知敏感化合物的最大Tanimoto相似度直方图;d图为Fimepinostat和生成化合物TNBC-S1的化学结构;e-f图分别为Fimepinostat和TNBC-S1在PI3Ka和HDAC1上的对接模拟结果;g图为针对未见过的临床患者的第二个零样本案例研究工作流程;h图为生成化合物、已知敏感和耐药化合物的预测AUC分布;i图为生成化合物与已知敏感化合物的最大Tanimoto相似度直方图;j图为Dinaciclib和生成化合物TNBC-S2的化学结构;k-l图分别为Dinaciclib和TNBC-S2在CDK1和CDK2上的对接模拟结果
四、临床价值:从实验室到病床的转化潜力
- 1. 加速hit发现:通过严格筛选(QED>0.8、SAS<4.5、合成路径深度<4),为每个细胞系生成10-30个高潜力候选分子,且均通过retros合成分析验证可行性。
- 2. 提升研发可解释性:注意力机制可识别关键驱动通路,如在TNBC中富集PI3K/AKT/PTEN和组蛋白去乙酰化通路,为靶点验证提供方向。
- 3. 适配真实世界场景:
- • 输入数据仅需临床常规基因检测结果,无需复杂组学分析。
- • 零样本生成能力支持罕见基因型或数据稀缺癌症类型(如TNBC)的药物研发。
五、局限与展望
尽管表现优异,G2D-Diff仍存在改进空间:
- • 分子表示局限:基于SMILES的VAE可能产生无效结构,未来可整合3D分子信息或图神经网络提升表示精度。
- • 数据依赖:训练依赖大规模药物反应数据(如GDSC、CTRP),对于罕见癌种的覆盖不足。
- • 体内验证缺失:目前仅通过in silico和细胞系实验验证,需进一步开展动物模型和临床试验。
作为首个将基因型直接映射至药物结构的扩散模型,G2D-Diff为个性化抗癌药物研发提供了“从基因到分子”的端到端解决方案。其核心价值不仅在于生成效率的提升,更在于通过AI解析基因型与药物响应的复杂关联,为精准肿瘤学开辟了数据驱动的新路径。
文献来源: Kim H, et al. A genotype-to-drug diffusion model for generation of tailored anti-cancer small molecules. Nat Commun. 2025;16:5628. https://doi.org/10.1038/s41467-025-60763-9
代码链接: https://github.com/GIST-CSBL/G2D-Diff
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2025-07-06,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

