Visium HD使用Cellpose进行细胞分割-补充
原创Visium HD使用Cellpose进行细胞分割-补充
原创
生信大杂烩
发布于 2025-05-29 21:36:48
发布于 2025-05-29 21:36:48
上节我们介绍了Visium HD使用Cellpose进行细胞分割获取单细胞精度空间数据,后台有许多同学私信我一些问题,有些同学对我将详细代码贴出来很感激,因为这些分析有些公众号是需要付费才能看到,还有几个同学问了我初次尝试过程中也遇到的问题,看来大家对使用Cellpose进行细胞分割很感兴趣,这里我对比较有代表性的几个问题做些补充说明。
一. Cellpose细胞分割,超参数diameter对结果影响很大,有没有好的方法推荐?
cellpose细胞分割中有几个比较重要的参数,官方文档也有详细介绍(https://cellpose.readthedocs.io/en/latest/settings.html),其中diameter是设置细胞大小的参数,cellpose 需要用户根据自己组织类型及细胞大小做调整(细胞形状及大小不是太特别的基本上不用调整),找到合适自己的值。这里可以使用Cellpose提供的可视化界面进行设置,观察分割结果,找到合适自己组织的参数。
python -m cellpose --Zstack直接可以打开GUI
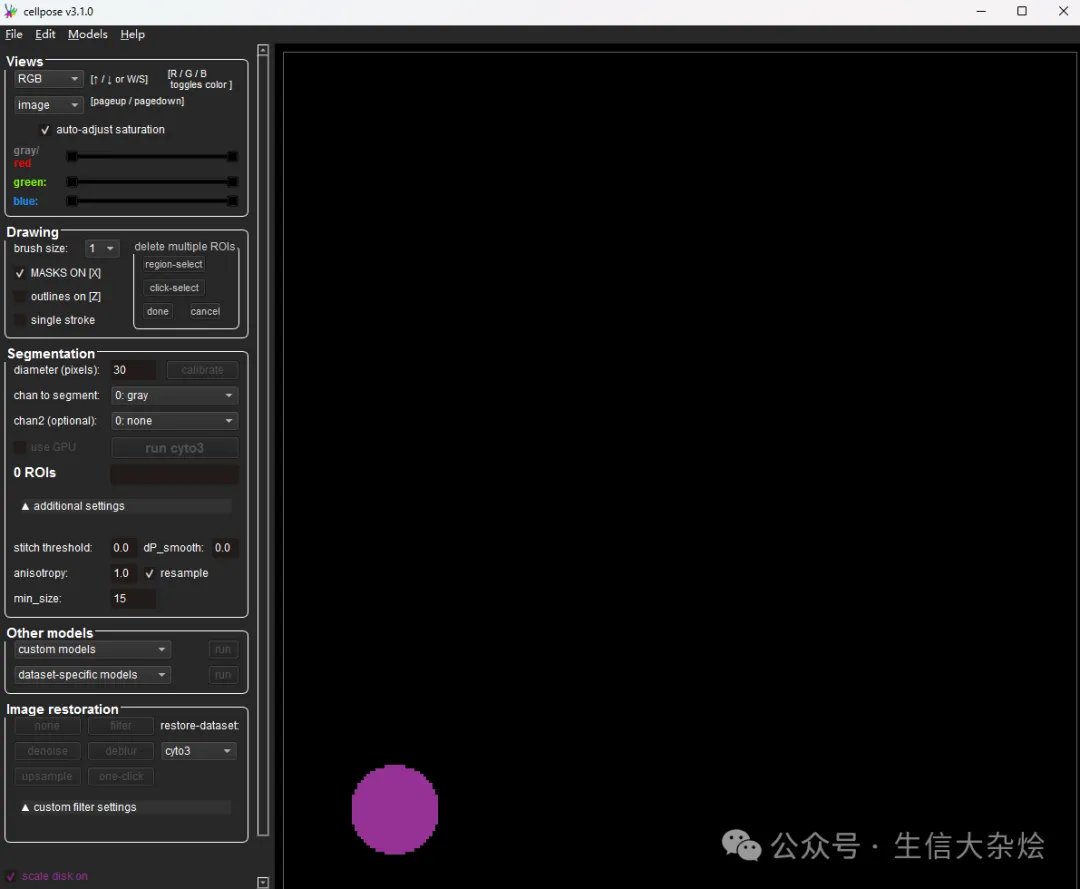
图片
导入tif图像,选择模型,调整细胞分割参数

图片
二. Cellpose分析前对输入tif文件图像处理是做什么?
我们首先对tif图像进行下采样,是为了节省计算资源,因为我的机器只有64G内存,有些项目tif太大运行卡顿,所以做了图像下采样。
三. 细胞分割后发现细胞数目太少,和H&E片子上看到的细胞数不一致怎么办?
可以使用Qupath打开tif图像,使用内置的机器学习模型或者是安装cellpose插件在自己图像上训练细胞分割模型,好处是可以实时看到分割的效果,能够及时调整参数使得分割达到较好的结果,然后将分割好的细胞边界坐标导出,再将2um bin转录本信息分配到细胞中即可。
打开tif文件
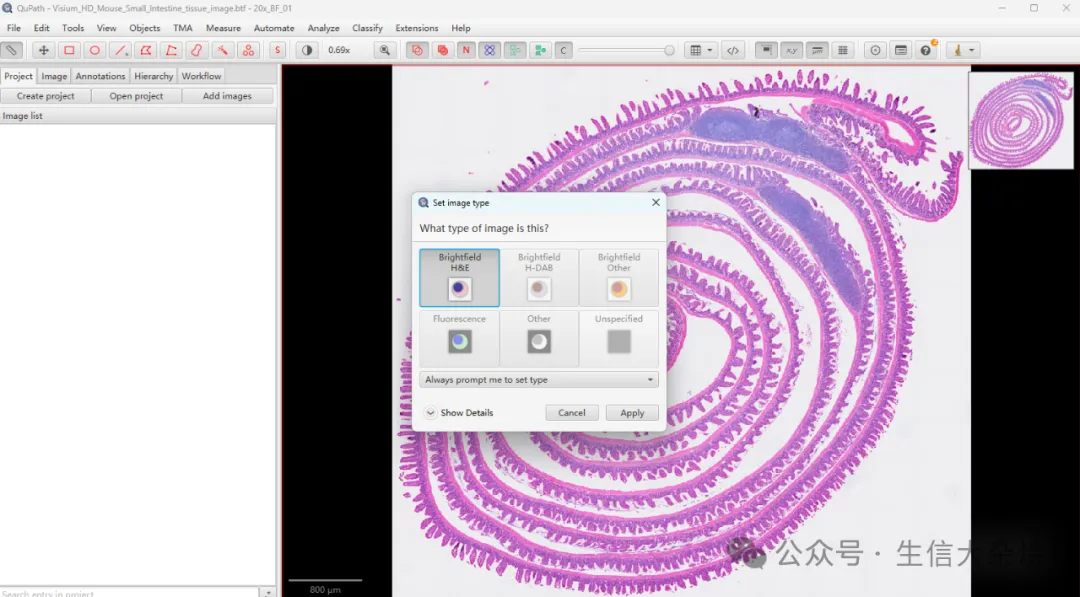
图片
使用机器学习模型分割
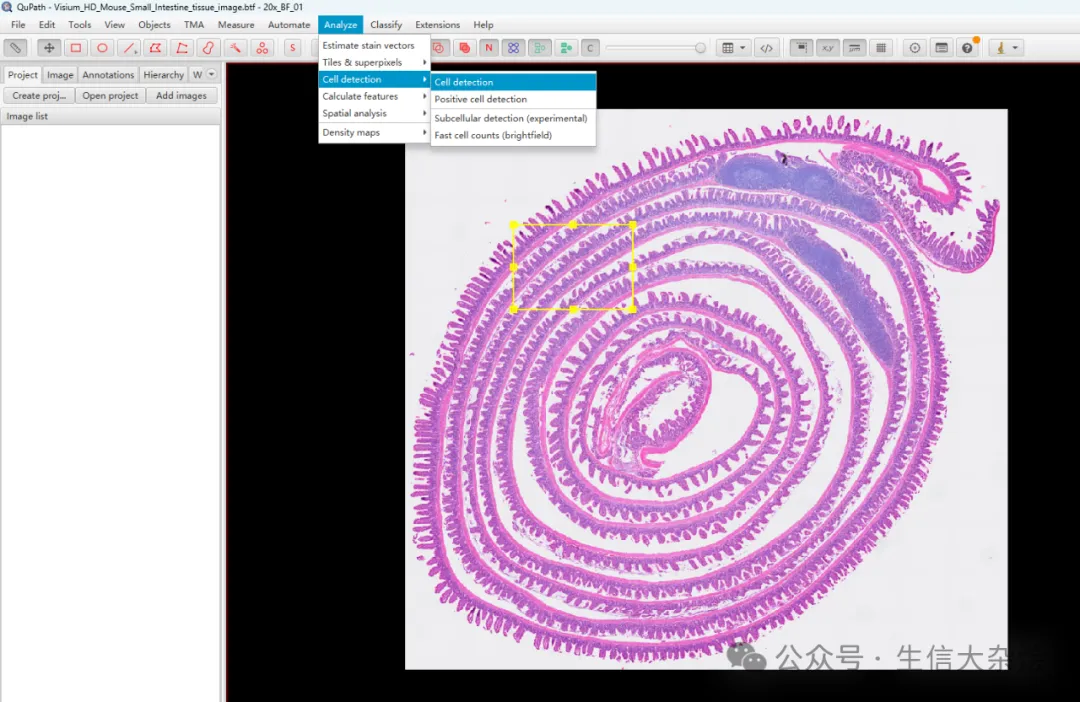
图片
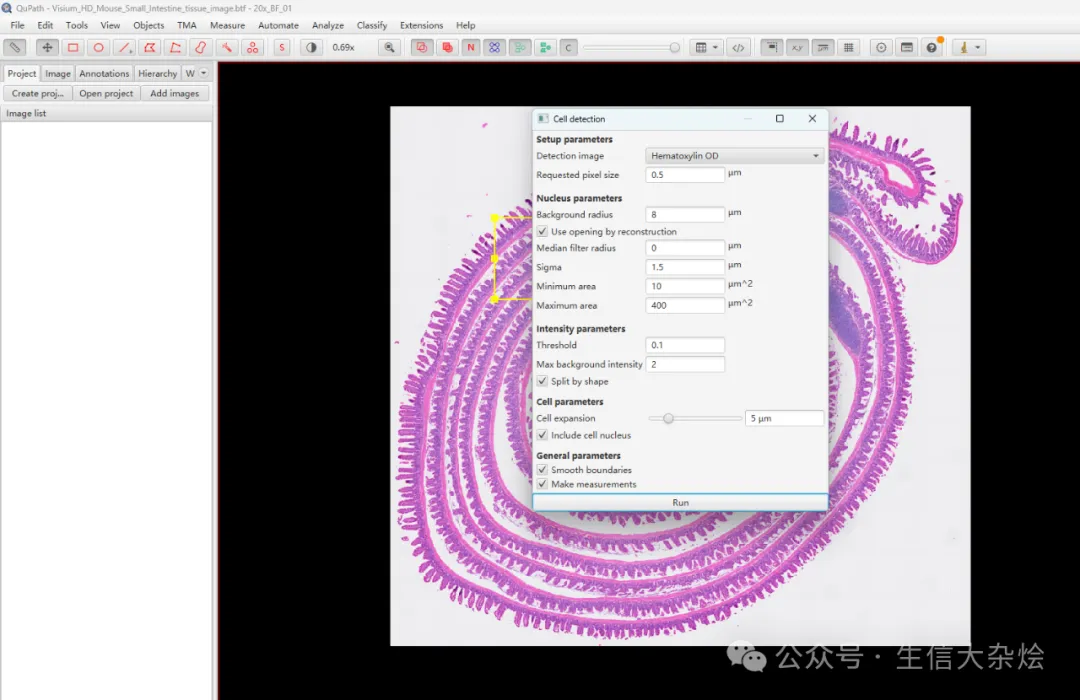
图片
分割结果展示-还可以手动调整,有些错误识别的细胞可以手动删除
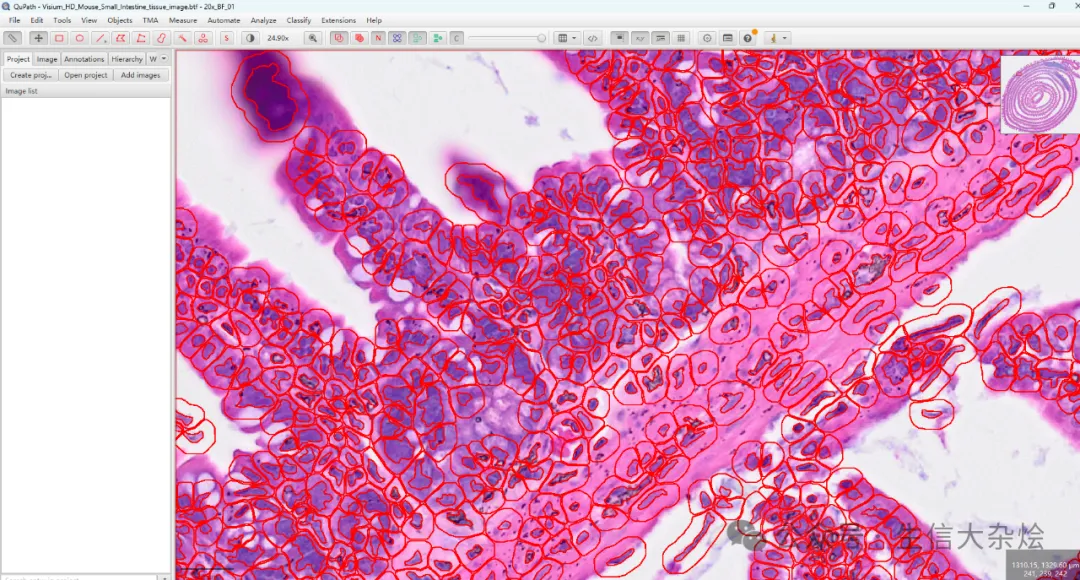
图片
导出geojson(细胞边界坐标,也可以选择只导出细胞核/细胞边界坐标)
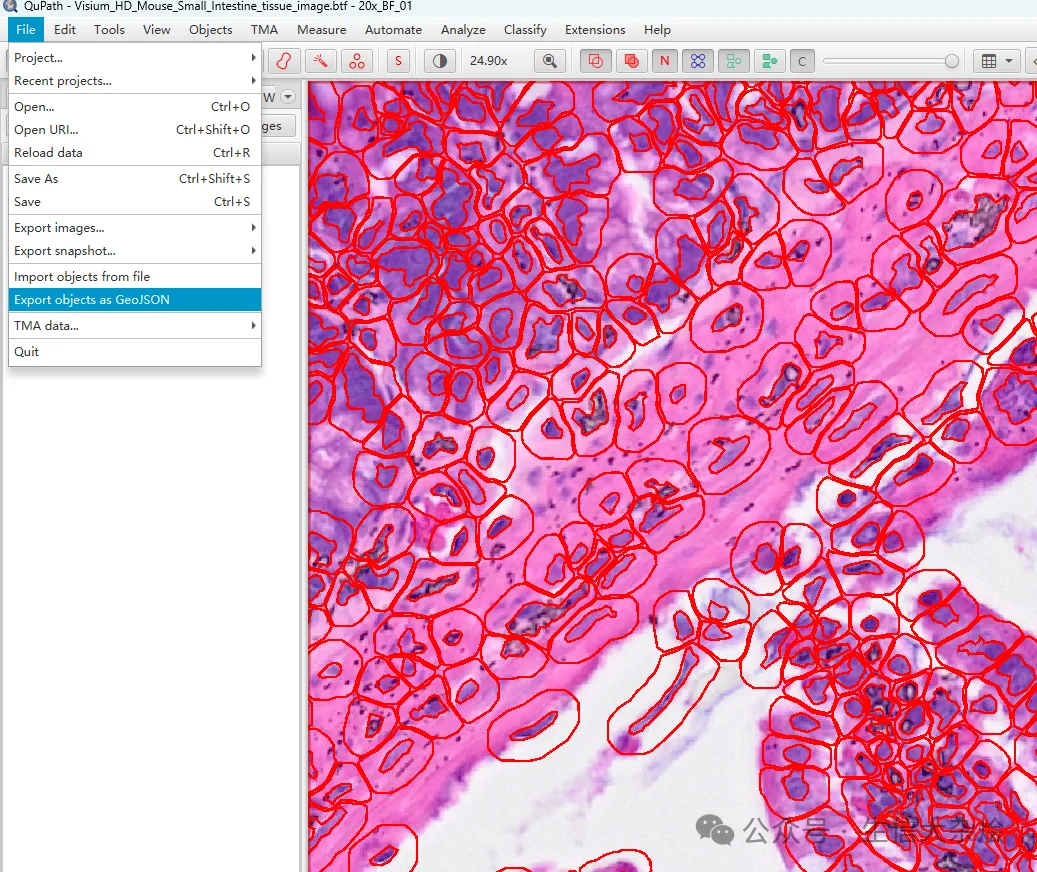
图片
安装cellpose插件,训练/使用已有模型进行细胞分割
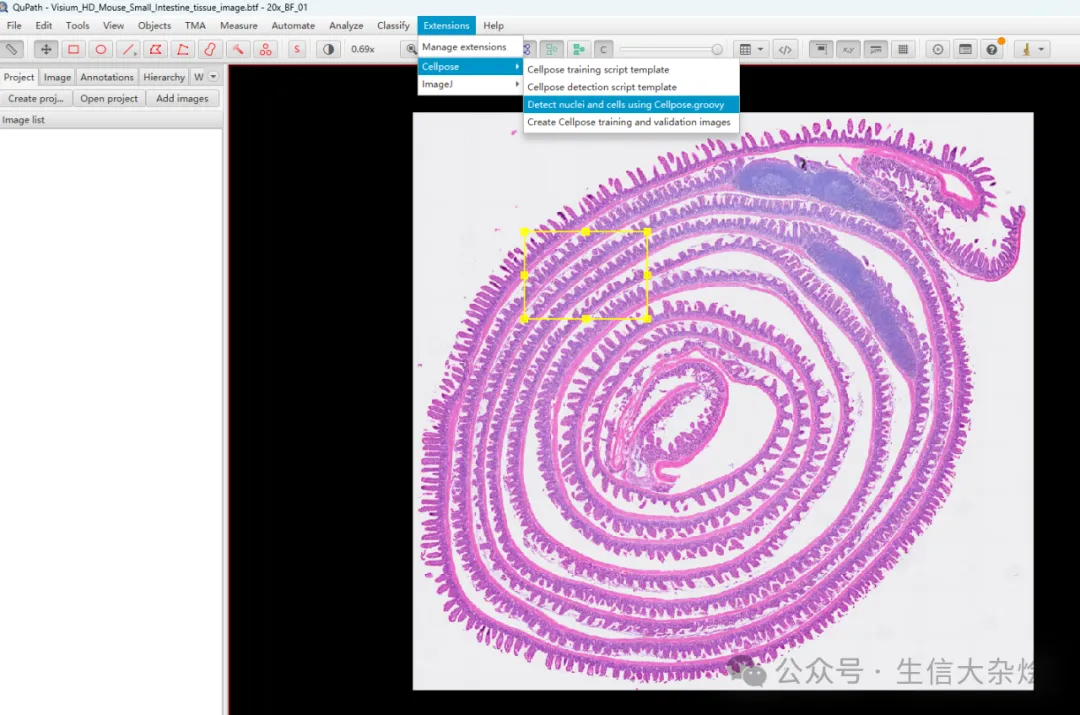
图片
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
评论
登录后参与评论
推荐阅读

