与st_crop的坐标混淆
与st_crop的坐标混淆
提问于 2019-08-06 00:59:39
我想裁剪一个sf物体。当我把物体绘制成ggplot时,我估计我想要裁剪的面积。但是,当我使用st_crop执行裁剪时,tibble有零行。为什么会这样呢?
从alberta_border.RDS下载这里
library("sf")
library("ggplot2")
alberta <- readRDS("alberta_border.RDS")
ggplot() +
geom_sf(data = alberta) +
coord_sf()
alberta_crop <- st_crop(alberta, c(xmin = -118, xmax = -112, ymin = 50, ymax = 56))
alberta_crop回答 1
Stack Overflow用户
回答已采纳
发布于 2019-08-06 07:42:57
看上去你搞错了crs。你可以告诉阿尔伯塔档案的crs:
st_crs(alberta)
#Coordinate Reference System:
#EPSG: 26911
#proj4string: "+proj=utm +zone=11 +ellps=GRS80 +towgs84=0,0,0,0,0,0,0 +units=m +no_defs"您的输入文件使用的是EPSG 26911或UTM 11N区,而您键入的坐标(c(xmin = -118, xmax = -112, ymin = 50, ymax = 56))则是lat/lng或EPSG 4326。
因此,在种植之前,我们应该将原始数据集转换为lat/lng:
library(dplyr)
library(sf)
library(ggplot2)
alberta <- alberta %>%
st_transform(4326)
alberta_crop <- st_crop(alberta, c(xmin = -118, xmax = -112, ymin = 50, ymax = 56))
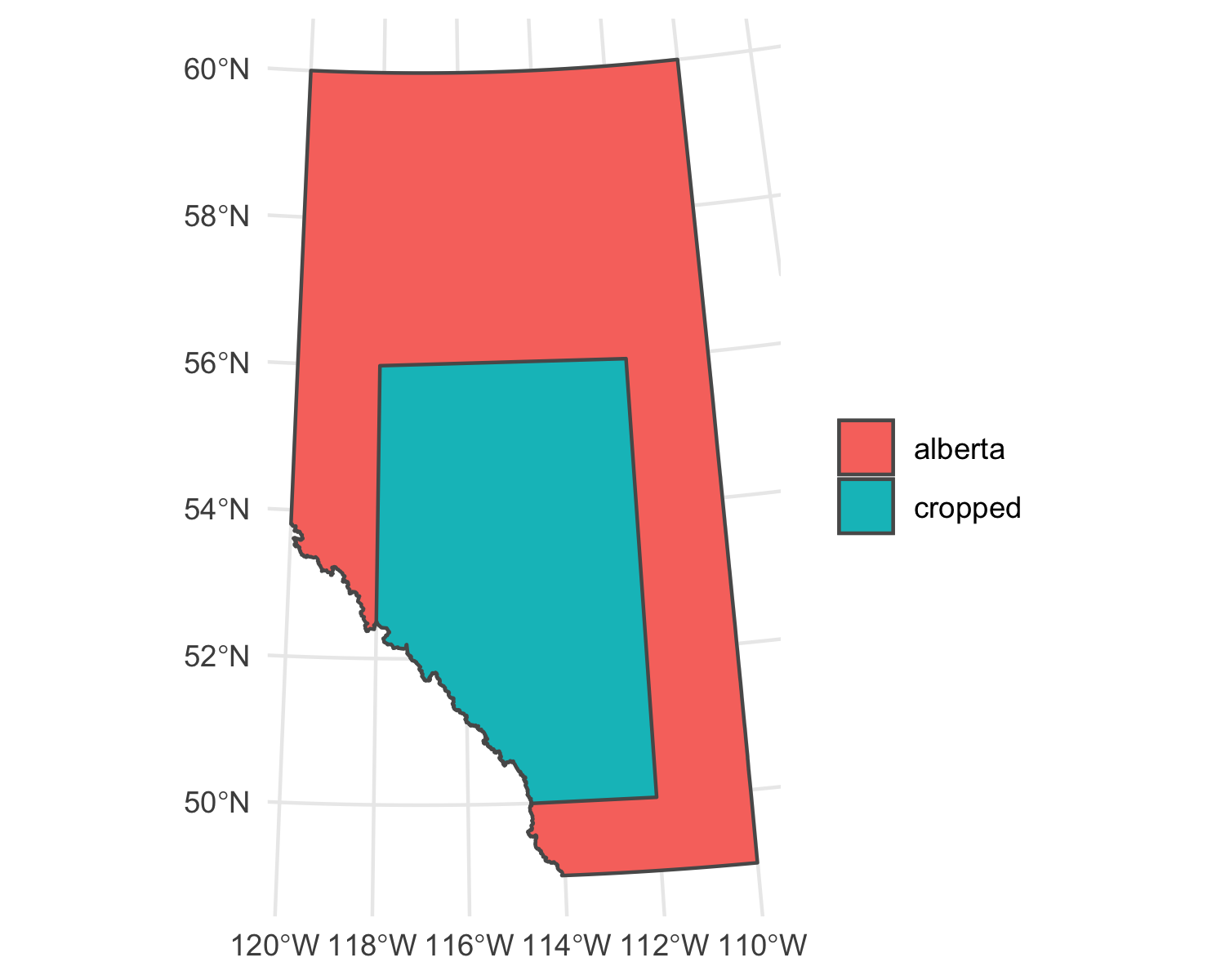
ggplot() +
geom_sf(data = alberta, aes(fill = 'alberta')) +
geom_sf(data = alberta_crop, aes(fill = 'cropped')) +
theme_minimal()
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/57367651
复制相关文章
相似问题

