如何将坐标传递给arviz / pymc3函数plot_posterior (类似于xarray.Dataset.sel)
我正在pymc3中做一些贝叶斯建模,并希望用plot_posterior (来自arviz包)绘制后验分布。产生的图形在水平轴上不对齐,我想把它移到-3和+3之间,不幸的是,我无法计算出应该传递给函数的内容来指定这一点。
arviz.plot_posterior的文档指定了参数"coords“,定义为”要绘制的var_names坐标。传递给Dataset.sel“--这大概是我需要为水平轴指定范围的东西,但它没有告诉我它期望的是什么样的值。
我已经检查了Dataset.sel的文档,它指出,它需要的第一个参数是“带有匹配标量、切片或滴答标签数组所提供的尺寸和值的键的dict”。我对此的解释是,键是与变量名称(S)匹配的字符串,值是一些可迭代的滴答符号结构。
我的变量名为'm‘,由以下代码生成:
with pymc3.Model() as m1:
m = pymc3.Normal('m', mu = 0, sigma = 1)
obs = pymc3.Normal('obs', mu = m, sigma = 1, observed = numpy.random.randn(3))
trace = pymc3.sample(1000, tune = 500, cores = 1)我猜plot_posterior所期望的是:
plot_posterior(trace, coords = {'m': [-3.0, -2,0, -1,0, 0.0, 1.0, 2.0, 3.0]})它给了我错误"ValueError:维度或多索引级别'm‘不存在“。
据推测,我是在正确的轨道上,但我只是找不出这个函数需要什么参数的更精确的定义。谢谢你能提供的任何帮助。
编辑:我已经解决了如何扩展轴本身(诀窍是ax = mpl.pyplot.axes(xlim = (-3.0,3.0)),但我仍然不知道如何扩展变量本身的绘图。
回答 1
Stack Overflow用户
发布于 2019-06-04 14:12:10
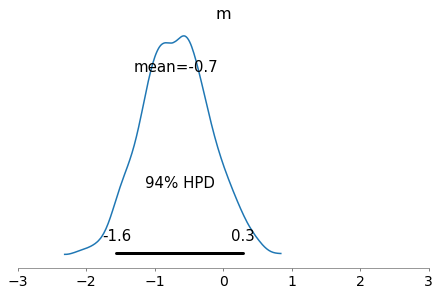
实际上,您可以直接转到matplotlib:pm.plot_posterior将返回一个轴,其中包含大多数显示属性的getter和setter:
ax, = pymc3.plot_posterior(trace)
ax.set_xlim(-3, 3)
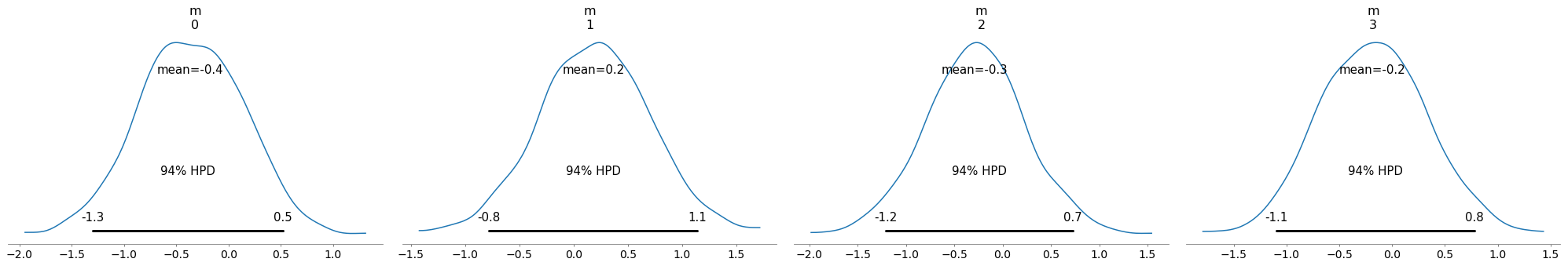
coords参数是针对多维随机变量的.如果您的模型是这样的:
with pymc3.Model() as m1:
m = pymc3.Normal('m', mu = 0, sigma = 1, shape = 4)
obs = pymc3.Normal('obs', mu = m, sigma = 1, observed = numpy.random.randn(3, 4))
trace = pymc3.sample(1000, tune = 500, cores = 1)然后,您的绘图将包含所有4个维度的m
pymc3.plot_posterior(trace)
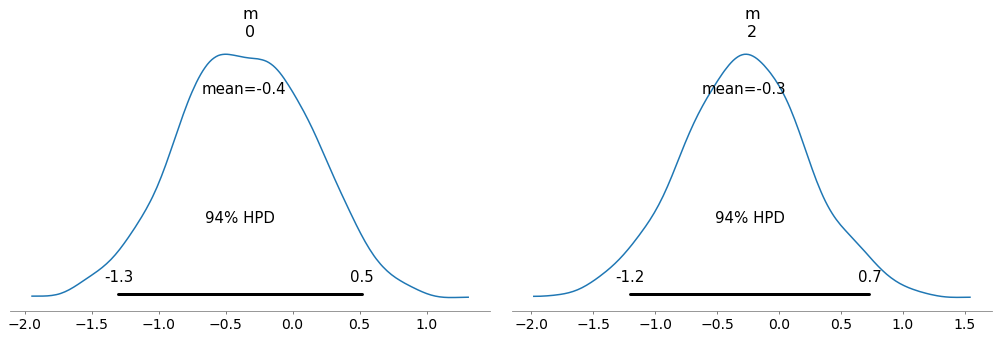
您可以使用coords来减少这种情况:
pymc3.plot_posterior(trace, coords={'m_dim_0': [0, 2]})
https://stackoverflow.com/questions/56439959
复制相似问题

