后向分布Pystan的最高密度间隔(HDI)
后向分布Pystan的最高密度间隔(HDI)
提问于 2018-12-07 14:54:21
我看到,在Pystan,HDI功能可以用来提供95%可信的间隔围绕后分布。然而,他们说,这将只适用于单峰分布。如果我的模型可能有一个多模分布(最多4个峰值),我有没有办法在Pystan找到HDI?谢谢!
回答 1
Stack Overflow用户
回答已采纳
发布于 2018-12-09 03:23:25
我不认为这是斯坦/派斯坦特有的问题。根据定义,最高密度区间是一个单一区间,因此不适合描述多峰分布。Rob,https://www.jstor.org/stable/2684423做了一项很好的工作,它将这个概念扩展到多模式分布,这已经在hdrcde包下的R中实现了。
至于Python,有PyMC语篇网站对此的探讨,建议使用Osvaldo为他的“”一书编写的函数(hpd_grid)。该函数的源在hpd.py文件中,95%的区域将用于以下
from hpd import hpd_grid
intervals, x, y, modes = hpd_grid(samples, alpha=0.05)其中,samples是一个参数的后验样本,而intervals是表示密度最高的区域的元组列表。
图例
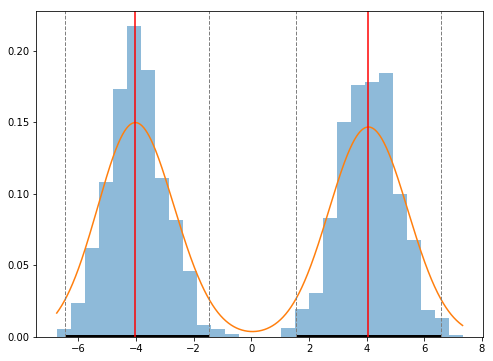
下面是一个使用假多模数据的示例图。
import numpy as np
from matplotlib import pyplot as plt
from hpd import hpd_grid
# include two modes
samples = np.random.normal(loc=[-4,4], size=(1000, 2)).flatten()
# compute high density regions
hpd_mu, x_mu, y_mu, modes_mu = hpd_grid(samples)
plt.figure(figsize=(8,6))
# raw data
plt.hist(samples), density=True, bins=29, alpha=0.5)
# estimated distribution
plt.plot(x_mu, y_mu)
# high density intervals
for (x0, x1) in hpd_mu:
plt.hlines(y=0, xmin=x0, xmax=x1, linewidth=5)
plt.axvline(x=x0, color='grey', linestyle='--', linewidth=1)
plt.axvline(x=x1, color='grey', linestyle='--', linewidth=1)
# modes
for xm in modes_mu:
plt.axvline(x=xm, color='r')
plt.show()
警告注意事项
应该注意的是,在适当建模的参数上的多模后验分布通常是罕见的,但在非收敛的MCMC抽样中却经常出现,特别是当使用多个链时(这是最好的做法)。如果一个人先验地期望多模,那么通常这会导致某种形式的混合模型,从而消除多模。如果一个人不期待多模,但无论如何,后座展示它,那么这是一个对结果表示怀疑的危险信号。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/53671925
复制相关文章
相似问题

