R stan 8学校示例faile
R stan 8学校示例faile
提问于 2018-10-09 12:58:48
我正在尝试从这个官方的教程中运行经典的r-stan示例。但我做不到,因为我得到了以下错误消息:
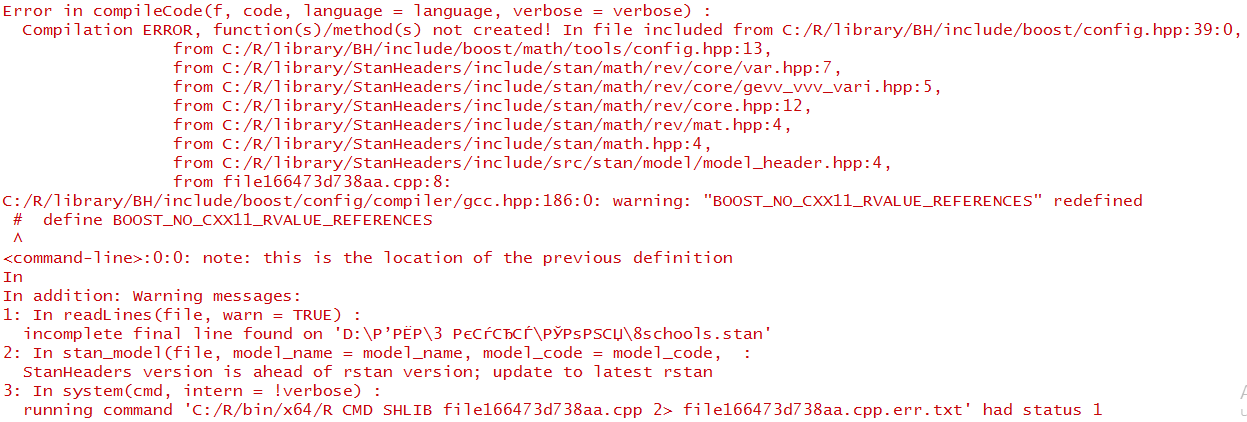
我使用的代码如下:
schools_dat <- list(J = 8,
y = c(28, 8, -3, 7, -1, 1, 18, 12),
sigma = c(15, 10, 16, 11, 9, 11, 10, 18))
fit <- stan(file = '8schools.stan', data = schools_dat,
iter = 1000, chains = 4)在8schools.stan文件中,我还创建并嵌套了以下代码:
data {
int<lower=0> J; // number of schools
real y[J]; // estimated treatment effects
real<lower=0> sigma[J]; // s.e. of effect estimates
}
parameters {
real mu;
real<lower=0> tau;
real eta[J];
}
transformed parameters {
real theta[J];
for (j in 1:J)
theta[j] = mu + tau * eta[j];
}
model {
target += normal_lpdf(eta | 0, 1);
target += normal_lpdf(y | theta, sigma);
}我想找出这个错误的原因,以及如何避免它,。
此外,我还想指出:
- 以下代码工作正常,并返回10: fx <-内联::REAL函数(签名(x=“整型”,y=“数值”),‘返回ScalarReal(整数(X)*实(Y));’) fx( 2L,5)
- 我已经安装了Rtools的最新冻结版本。
- 此外,Rtools、R和Rstudio位于没有空格的文件夹中。
- 我在Windows上工作(不是笔记本电脑)
- 我一直严格遵循安装导轨的所有步骤。
将是非常伟大的帮助!
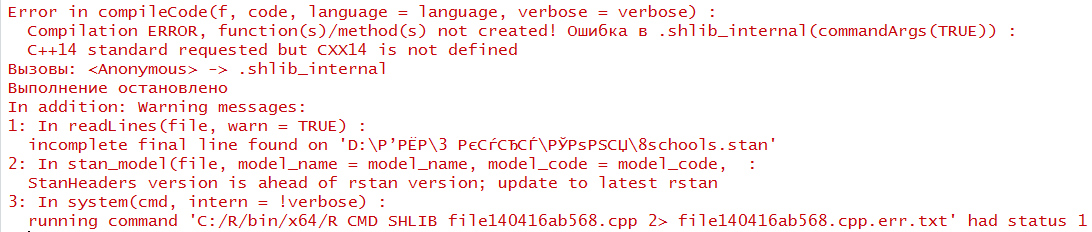
更新
我还按照Ben的建议设置了Sys.setenv(USE_CXX14=1),但现在我得到了以下错误消息
回答 1
Stack Overflow用户
发布于 2018-10-09 15:11:12
这是一个暂时的问题,因为(本周) StanHeaders R包(它需要C++14)已经在CRAN上被接受,但还没有rstan包(它使用C++14编译模型)。因此,就目前而言,您首先需要调用Sys.setenv(USE_CXX14=1),但是任何在未来阅读这篇文章的人都不太可能需要显式地这样做( rstan包将在内部完成)。
在Windows上,您需要将CXX14=g++ -std=c++1y CXX14FLAGS=-O3放到~/.R/Makevars文件中,但是在Mac上,这些行应该已经存在了。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/52721672
复制相关文章
相似问题

