如何使用XML2包解析XML文件的子路径
如何使用XML2包解析XML文件的子路径
提问于 2018-07-03 03:31:01
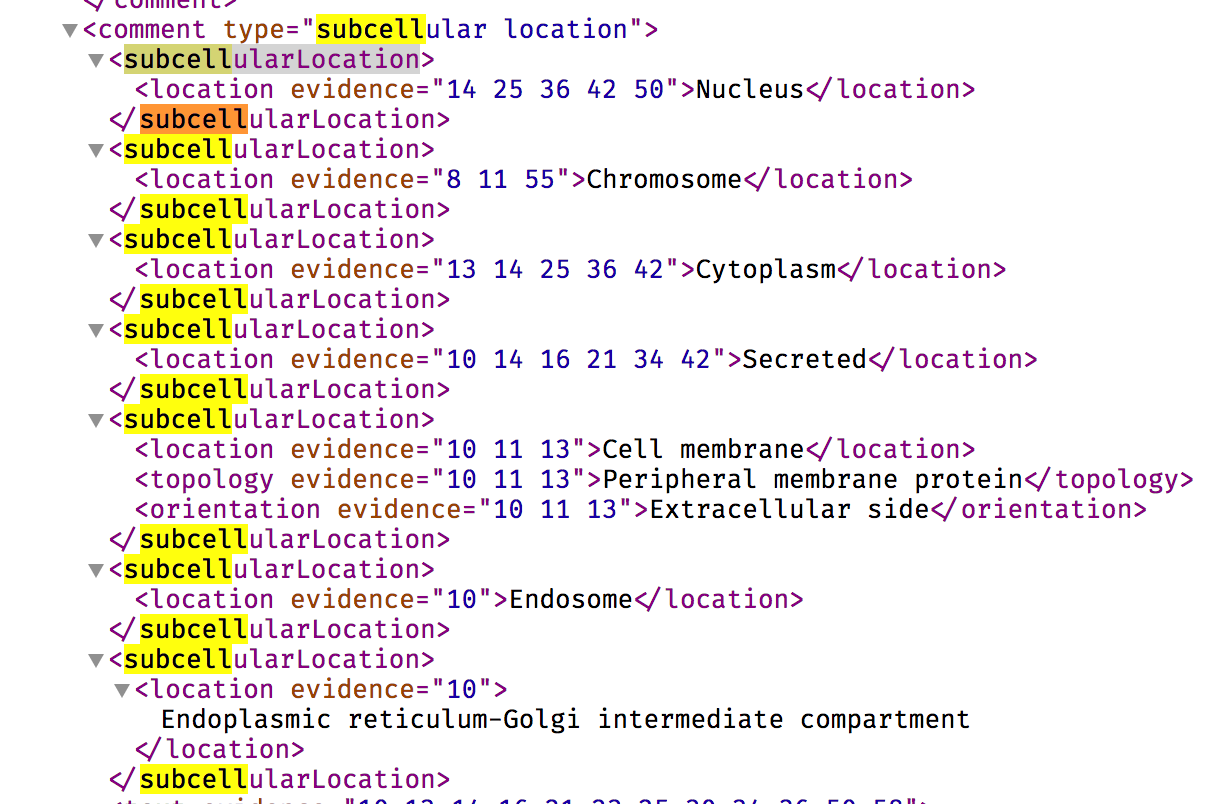
但是,使用这段代码,我无法获得subcellularLocation xpath下面的列表:
library(xml2)
xmlfile <- "https://www.uniprot.org/uniprot/P09429.xml"
doc <- xmlfile %>%
xml2::read_xml()
xml_name(doc)
xml_children(doc)
x <- xml_find_all(doc, "//subcellularLocation")
xml_path(x)
# character(0)正确的方法是什么?
更新
The desired output is a vector:
[1] "Nucleus"
[2] "Chromosome"
[3] "Cytoplasm"
[4] "Secreted"
[5] "Cell membrane"
[6] "Peripheral membrane protein"
[7] "Extracellular side"
[8] "Endosome"
[9] "Endoplasmic reticulum-Golgi intermediate compartment" 回答 2
Stack Overflow用户
回答已采纳
发布于 2018-07-03 05:04:36
使用x <- xml_find_all(doc, "//d1:subcellularLocation")
每当遇到麻烦的问题时,首先检查文档,使用?xml_find_all,您将看到这个(在页面的末尾)。
# Namespaces ---------------------------------------------------------------
# If the document uses namespaces, you'll need use xml_ns to form
# a unique mapping between full namespace url and a short prefix
x <- read_xml('
<root xmlns:f = "http://foo.com" xmlns:g = "http://bar.com">
<f:doc><g:baz /></f:doc>
<f:doc><g:baz /></f:doc>
</root>
')
xml_find_all(x, ".//f:doc")
xml_find_all(x, ".//f:doc", xml_ns(x))然后你去检查xml_ns(doc)并找到
d1 <-> http://uniprot.org/uniprot
xsi <-> http://www.w3.org/2001/XMLSchema-instance更新
xml_find_all(doc, "//d1:subcellularLocation")
%>% xml_children()
%>% xml_text()
## [1] "Nucleus"
## [2] "Chromosome"
## [3] "Cytoplasm"
## [4] "Secreted"
## [5] "Cell membrane"
## [6] "Peripheral membrane protein"
## [7] "Extracellular side"
## [8] "Endosome"
## [9] "Endoplasmic reticulum-Golgi intermediate compartment"ent"Stack Overflow用户
发布于 2018-07-03 04:56:03
如果您不介意,可以使用rvest包:
library(rvest)
a=read_html(xmlfile)%>%
html_nodes("subcellularlocation")
a%>%html_children()%>%html_text()
[1] "Nucleus" "Chromosome"
[3] "Cytoplasm" "Secreted"
[5] "Cell membrane" "Peripheral membrane protein"
[7] "Extracellular side" "Endosome"
[9] "Endoplasmic reticulum-Golgi intermediate compartment"页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/51146288
复制相关文章
相似问题

