R光栅::提取函数不按预期工作
R光栅::提取函数不按预期工作
提问于 2018-05-21 10:54:44
我试图在R中做一些多边形/光栅的工作,提取函数没有像我所期望的那样工作。下面是一个可重复的例子。
library(sf)
library(raster)
library(maptools)
raster <- download.file('https://raw.githubusercontent.com/JimShady/london_osm_canyons/master/test.tif', 'downloaded_raster')
raster <- raster('test.tif')
polygons <- read_sf('https://raw.githubusercontent.com/JimShady/london_osm_canyons/master/test2.geojson')
polygons <- st_transform(polygons, crs(raster)@projargs)
polygons$id <- 1
polygons <- as(polygons, 'Spatial')
new_polygon <- elide(polygons, rotate=-50)
proj4string(new_polygon) <- crs(raster)@projargs
polygons <- rbind(polygons, new_polygon)
plot(raster)
plot(polygons, add=T)
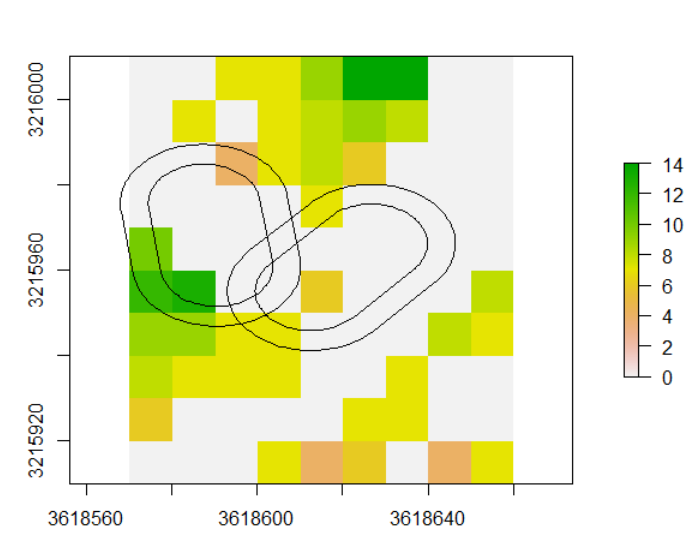
我希望得到每个多边形与之相交的单元格数,即使它们是NA,并将它们作为一列存储在多边形中。
polygons$cell_count <- extract(raster, polygons, fun = function(x,...)length(x), na.rm=F)但是,当多边形与栅格中的多个单元格相交时,这会返回多边形1的数字5。这是怎么回事?
然后我想得到加权平均值。如果有任何NA单元交叉,那么这应该‘失败’,并返回NA。我认为这是可行的,但由于上述错误,我现在对我的方法不太有信心。
polygons$mean <- round(extract(raster, polygons, fun = mean, weights=T, na.rm=F),2),我也想知道相交的细胞数量少于一个,,我不知道该怎么做。有什么好主意吗?
polygons$almost_zero <-谢谢你的帮助。
回答 2
Stack Overflow用户
发布于 2018-05-21 13:16:59
来自extract帮助:
如果单元格的中心位于多边形内,则覆盖该单元格(但请参见考虑部分覆盖单元格的权重选项;对于获得小多边形值的参数小)。
因此,您可以使用它获得单元格的数量:
data <- extract(raster, polygons, weights = T, na.rm = F)[[1]]
nrow(data)
#[1] 18其中data是:
value weight
[1,] 8 0.003610108
[2,] 6 0.025270758
[3,] 0 0.010830325
[4,] 7 0.104693141
[5,] 0 0.066787004
[6,] 0 0.088447653
[7,] 0 0.001805054
[8,] 0 0.104693141
[9,] 0 0.010830325
[10,] 0 0.093862816
[11,] 0 0.030685921
[12,] 0 0.063176895
[13,] 0 0.057761733
[14,] 0 0.063176895
[15,] 7 0.003610108
[16,] 7 0.102888087
[17,] 0 0.093862816
[18,] 0 0.074007220具有与之相交且小于1的单元格数:
sum(data[, 1] < 1)
#[1] 13编辑
在出现多个多边形的情况下,应首先使用rgeos::gUnaryUnion分解多边形。
library(rgeos)
polygons$id <- 1
polygons <- gUnaryUnion(polygons, id = polygons$id)
# As suggested by @RobertHijmans, you can also use `raster::aggregate`
# polygons <- raster::aggregate(polygons, by = "id")
plot(raster)
plot(polygons, add = T)
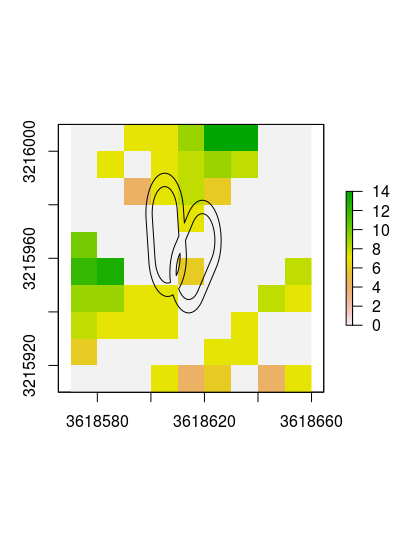
Stack Overflow用户
发布于 2018-05-21 13:51:15
提取是按照它的意思,通过寻找细胞的质心在多边形内。处理部分覆盖的一种方法是使用rasterize将多边形转换为光栅掩码。注意,在下面我分别重命名了光栅和多边形r1,以及p1。因为对对象使用函数名并不是很好的做法:
r_mask = rasterize(p1, r1, getCover=TRUE)
r_mask[r_mask==0] = NA现在,我们可以使用这个掩码获取所需的值:
r2 = mask(r1, r_mask)
cellStats(!is.na(r2), sum)
# [1] 18
cellStats(r2, mean)
# [1] 1.944444为了找出有多少个细胞小于一个,我们可以
cellStats(r2<1, sum)
# [1] 13页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/50447315
复制相关文章
相似问题

