二值分割的结果是模糊图像
二值分割的结果是模糊图像
提问于 2018-04-11 13:41:53
我正在研究一个二元分割问题,为了解决这个问题,我必须将细胞核从细胞中分割出来。我用二元交叉熵作为损失函数,用U-Net CNN模型.得到的图像有一些模糊的效果。我做实验的时代越多,就会越模糊。是什么导致了这样模糊的效果,我应该对我的模型做什么改变来消除它呢?
我附上了一个经过4个时代后产生的样品合成图像。
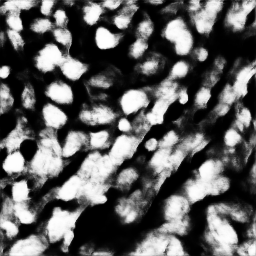
回答 1
Stack Overflow用户
回答已采纳
发布于 2018-04-11 13:54:58
最简单的解决方案是在某个阈值上对结果进行阈值化(为了方便起见,我使用了0.5 )。但是,您可以像在https://arxiv.org/abs/1608.04117中一样使用骰子丢失(可以在这里找到keras实现:https://github.com/raghakot/ultrasound-nerve-segmentation),它倾向于生成二进制输出。但是,如果最终结果优于对二进制交叉熵进行阈值处理,则输出取决于您的数据集。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/49776733
复制相关文章
相似问题

