正态分布的MLE拟合
正态分布的MLE拟合
提问于 2018-03-13 13:01:13
我试图采用this thread中提出的这个解来确定一个简单正态分布的参数。尽管修改是很小的(基于维基百科),但结果却很差。有什么不对的地方吗?
import math
import numpy as np
from scipy.optimize import minimize
import matplotlib.pyplot as plt
def gaussian(x, mu, sig):
return 1./(math.sqrt(2.*math.pi)*sig)*np.exp(-np.power((x - mu)/sig, 2.)/2)
def lik(parameters):
mu = parameters[0]
sigma = parameters[1]
n = len(x)
L = n/2.0 * np.log(2 * np.pi) + n/2.0 * math.log(sigma **2 ) + 1/(2*sigma**2) * sum([(x_ - mu)**2 for x_ in x ])
return L
mu0 = 10
sigma0 = 2
x = np.arange(1,20, 0.1)
y = gaussian(x, mu0, sigma0)
lik_model = minimize(lik, np.array([5,5]), method='L-BFGS-B')
mu = lik_model['x'][0]
sigma = lik_model['x'][1]
print lik_model
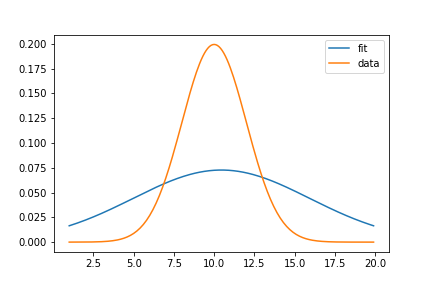
plt.plot(x, gaussian(x, mu, sigma), label = 'fit')
plt.plot(x, y, label = 'data')
plt.legend()适配的输出:
jac:数组(2.27373675e-05,2.27373675e-05)
信息:“会聚:REL_REDUCTION_OF_F_<=_FACTR*EPSMCH”
成功:是真的
x:数组(10.45000245,5.48475283)
回答 1
Stack Overflow用户
回答已采纳
发布于 2018-03-13 14:42:58
最大似然法是将一个分布的参数拟合成一组据称是随机样本的值。在lik函数中,使用x保存示例,但是x是设置为x = np.arange(1,20, 0.1)的全局变量。这绝对不是正态分布的随机样本。
由于您使用的是正态分布,所以可以使用已知的最大似然估计公式来验证您的计算: mu是样本平均值,sigma是样本标准差:
In [17]: x.mean()
Out[17]: 10.450000000000006
In [18]: x.std()
Out[18]: 5.484751589634671这些值非常接近于调用minimize的结果,因此看起来您的代码工作正常。
要修改代码以按照预期的方式使用MLE,x应该是据称来自正态分布的随机样本的值集合。注意,您的数组y不是这样的示例。它是网格上概率密度函数(PDF)的值。如果将分布拟合到PDF样本是您的实际目标,则可以使用曲线拟合函数(如scipy.optimize.curve_fit )。如果将正态分布参数拟合到随机样本实际上是您想要做的,那么为了测试您的代码,您应该使用一个来自具有已知参数的分布的相当大的样本的输入。在这种情况下,你可以
x = np.random.normal(loc=mu0, scale=sigma0, size=20)当我在您的代码中使用这样的x时,我将
In [20]: lik_model.x
Out[20]: array([ 9.5760996 , 2.01946582])正如预期的那样,解决方案中的值大约为10和2。
(如果您像我一样对示例使用x,则必须相应地更改绘图代码。)
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/49256917
复制相关文章
相似问题

