Jags中的贝叶斯滚动泊松回归(通过R2jags)
Jags中的贝叶斯滚动泊松回归(通过R2jags)
提问于 2018-02-10 17:12:59
问题
我有一个小数据集(N=100)。我需要运行泊松回归,但不包括每次一个观察(因此,滚动泊松回归)。
方程中有几个预测因子,但我关心一个(称为b.x)。我的想法是看看b.x在100款车型中的变化有多大。然后,我想用Y轴上的效应大小和X轴上的模型数来绘制这100个点的估计值。
总之,我需要以下几点:
- 在JAGS中运行滚动泊松回归(通过R2jags)。
- 在得到估计数之后,把它们画出来。
请注意,我在JAGS中的泊松模型正在运行精细的(下面是我的模型/数据的一个示例玩具)。然而,我还无法实现“滚动”版本的。
自给示例
# clear R
rm(list=ls())
cat("\014")
# load libraries
if (!require("pacman")) install.packages("pacman"); library(pacman)
p_load(R2jags)
# Toy Data
N <- 100
x <- rnorm(n=N) # standard Normal predictor
y <- rpois(n=N, lambda = 1) # Poisson DV
# model
model <- function() {
## Likelihood
for(i in 1:N){
y[i] ~ dpois(lambda[i])
log(lambda[i]) <-
mu + # intercept
b.x*x[i]
}
## Priors
mu ~ dnorm(0, 0.01) ## intercept
b.x ~ dnorm(0, 0.01)
}
# list elements
data.list <- list(N = N, y = y, x = x)
# run model
model.fit <- jags(
data=data.list,
inits=NULL,
parameters.to.save = c("b.x"),
n.chains = 1,
n.iter = 20,
n.burnin = 2,
model.file=model,
progress.bar = "none")好的。这就是模型。在model.fit中有b.x,系数必须是100倍。使用我的当前代码,我能够只获得一次,使用完整的数据集。但是,我需要第二次使用排除df的第一行,然后第三次使用排除df的第二行,以此类推。然后,绘制所有这些b.x的。
现在,为了示例起见,我将创建一个简单的表,只为了表明我需要第一个元素(b.x的系数)。
## I sourced this function below from https://raw.githubusercontent.com/jkarreth/JKmisc/master/mcmctab.R
# Function to Create Table
mcmctab <- function(sims, ci = .8, digits = 2){
require(coda)
if(class(sims) == "jags" | class(sims) == "rjags"){
sims <- as.matrix(as.mcmc(sims))
}
if(class(sims) == "bugs"){
sims <- sims$sims.matrix
}
if(class(sims) == "mcmc"){
sims <- as.matrix(sims)
}
if(class(sims) == "mcmc.list"){
sims <- as.matrix(sims)
}
if(class(sims) == "stanfit"){
stan_sims <- rstan::As.mcmc.list(sims)
sims <- as.matrix(stan_sims)
}
dat <- t(sims)
mcmctab <- apply(dat, 1,
function(x) c(Mean = round(mean(x), digits = digits), # Posterior mean
SD = round(sd(x), digits = 3), # Posterior SD
Lower = as.numeric(
round(quantile(x, probs = c((1 - ci) / 2)),
digits = digits)), # Lower CI of posterior
Upper = as.numeric(
round(quantile(x, probs = c((1 + ci) / 2)),
digits = digits)), # Upper CI of posterior
Pr. = round(
ifelse(mean(x) > 0, length(x[x > 0]) / length(x),
length(x[x < 0]) / length(x)),
digits = digits) # Probability of posterior >/< 0
))
return(t(mcmctab))
}
# this is the coefficient I need, but with different data frames.
mcmctab(model.fit)[1,1]对不起,我在这里甚至不能提供一个尝试的解决方案。提前谢谢。
回答 2
Stack Overflow用户
回答已采纳
发布于 2018-02-14 16:41:10
# clear R
rm(list=ls())
# load libraries
library(R2jags)
# Toy Data
set.seed(123) # set RNG seed for reproducibility
N <- 100
x <- rnorm(n=N) # standard Normal predictor
y <- rpois(n=N, lambda = 1) # Poisson DV
# model
model <- function() {
## Likelihood
for(i in 1:N){
y[i] ~ dpois(lambda[i])
log(lambda[i]) <-
mu + # intercept
b.x*x[i]
}
## Priors
mu ~ dnorm(0, 0.01) ## intercept
b.x ~ dnorm(0, 0.01)
}
# list elements
data.list <- list() # create empty list to fill in next line
# fill list with one data set for each step, with one row excluded per step
for(i in 1:100){
data.list[[i]] <- list(N = 99, y = y[-i], x = x[-i])
}
# Starting value for reproducibility
model.inits <- function(){
list("b.x" = 0)
}
# run model
model.fit <- list() # again, create empty list first
for(i in 1:100){ # use loop here to fit one model per data set
model.fit[[i]] <- jags(
data=data.list[[i]],
inits=NULL,
parameters.to.save = c("b.x"),
n.chains = 1,
n.iter = 20,
n.burnin = 2,
model.file=model,
progress.bar = "none")
}
# helper function for output
devtools::source_url("https://raw.githubusercontent.com/jkarreth/JKmisc/master/mcmctab.R")
# create empty data frame to be filled with estimation results per data set
tab <- data.frame(index = c(1:100), b = rep(NA, 100), lower = rep(NA, 100), upper = rep(NA, 100))
# fill with estimates, using mcmctab to extract mean & lower & upper CIs
for(i in 1:100){
tab[i, 2] <- mcmctab(model.fit[[i]])[1, 1]
tab[i, 3] <- mcmctab(model.fit[[i]])[1, 3]
tab[i, 4] <- mcmctab(model.fit[[i]])[1, 4]
}
# plot results
library(ggplot2)
p <- ggplot(data = tab, aes(x = b, y = index)) + geom_point() + geom_segment(aes(x = lower, xend = upper, yend = index))
p
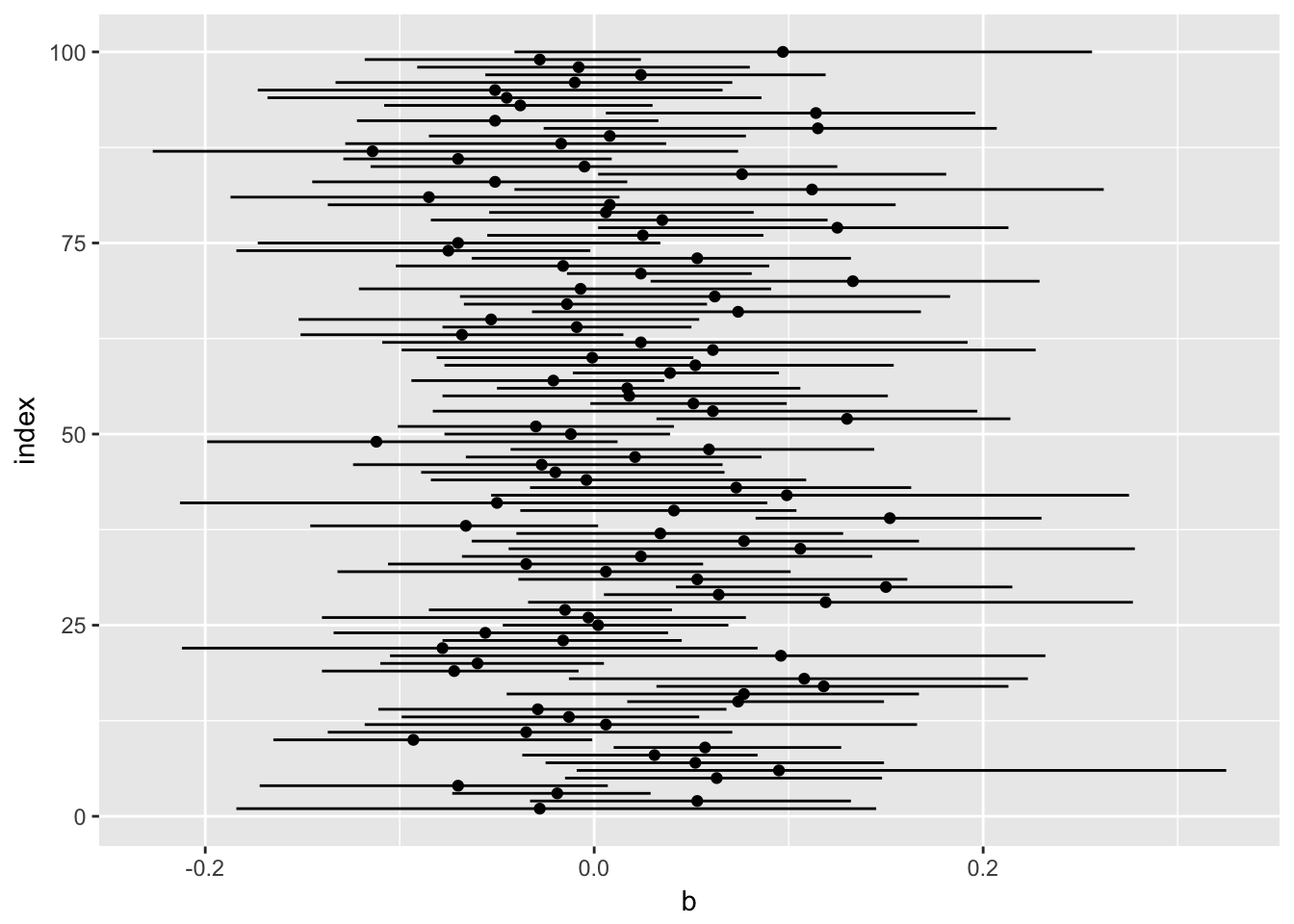
我感谢约翰·卡雷思提供了这个很好的答案。
Stack Overflow用户
发布于 2018-02-10 17:42:41
使用for-循环或apply家族成员之一一次排除一个观察:
sims <- lapply(1:100, function(i) {
data.list <- list(N = N - 1, y = y[-i], x = x[-i])
# run model
model.fit <- jags(
data=data.list,
inits=NULL,
parameters.to.save = c("b.x"),
n.chains = 1,
n.iter = 20,
n.burnin = 2,
model.file=model,
progress.bar = "none")
return(model.fit)
})然后,您可以通过循环输出来提取感兴趣的数量:
sapply(sims, function(x) x$BUGSoutput$mean$b.x)
# [1] -0.018966261 -0.053383364 -0.030193649 -0.097046841 -0.026258934
# [6] -0.005486296 0.084811315 -0.047736880 0.142379194 -0.026583145
# <snip>页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/48723408
复制相关文章
相似问题

