hclust中的错误(d,方法=方法):外部函数调用中的NA/NaN/Inf (arg 11)
hclust中的错误(d,方法=方法):外部函数调用中的NA/NaN/Inf (arg 11)
提问于 2017-11-03 23:06:29
我对RStudio非常陌生,我拼命地想要抓住这一切,所以如果这是一个愚蠢的问题,我很抱歉。我正试图使用pheatmap为我的RNA Seq数据集生成一个热图,但是我再次出现了一些错误。我的数据如下:
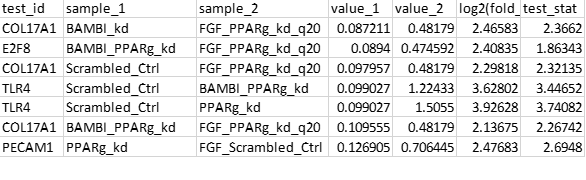
我正在尝试使用下面的代码,它是从另一个用户那里获取的。
热图编码
pheatmap(
mat = mydata,
color = inferno(10),
border_color = black,
show_colnames = FALSE,
show_rownames = FALSE,
annotation_col = mydata$sample_1,
annotation_colors = mydata$value_1,
drop_levels = TRUE,
fontsize = 10,
main = "Default Heatmap")当我将它输入系统时,我得到了以下错误:hclust中的错误(d,方法=方法):外部函数调用中的NA/NaN/Inf (arg 11)此外:警告消息: 1:在dist(mat,方法=距离):NAs被强制引入2: In dist(mat,方法=距离):NAs由强制引入
我试图寻找答案,但很难将其与我的数据联系起来。我已经查看了我的dataframe,它似乎是对这类错误的响应,但是似乎没有任何明显的原因导致我的问题。下面我已经给了你我的数据,所以你可以看到我在说什么。如果我错过了什么,请告诉我。
'data.frame': 6436 obs. of 15 variables:
$ test_id : Factor w/ 1517 levels "ABCA6","ABCA8",..: 273 370 273
$ sample_1 : Factor w/ 5 levels "BAMBI_kd","BAMBI_PPARg_kd",..: 1 2 5
$ sample_2 : Factor w/ 5 levels "BAMBI_kd","BAMBI_PPARg_kd",..: 3 3
$ status : Factor w/ 1 level "OK": 1 1 1 1 1 1 1 1 1 1 ...
$ value_1 : num 0.0872 0.0894 0.098 0.099 0.099 ...
$ value_2 : num 0.482 0.475 0.482 1.224 1.506 ...
$ log2.fold_change.: num 2.47 2.41 2.3 3.63 3.93 ...
$ test_stat : num 2.37 1.86 2.32 3.45 3.74 ...
$ p_value : num 0.00045 0.0006 0.0006 0.00005谢谢你,我期待着你的答复。
回答 1
Stack Overflow用户
发布于 2019-05-03 13:46:34
我不确定这在创建热图时是否适用,但是当我试图使用rcorr()和corrplot()创建可视化关联矩阵时,我遇到了这个错误。我没有NA、NaN或Inf,但意识到我的一个变量只有0(或所有相同的值)。通过从数据集中过滤这个变量来修正。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/47105567
复制相关文章
相似问题

