python:在生物网络上使用networkX实现定向边缘
python:在生物网络上使用networkX实现定向边缘
提问于 2017-08-02 19:07:46
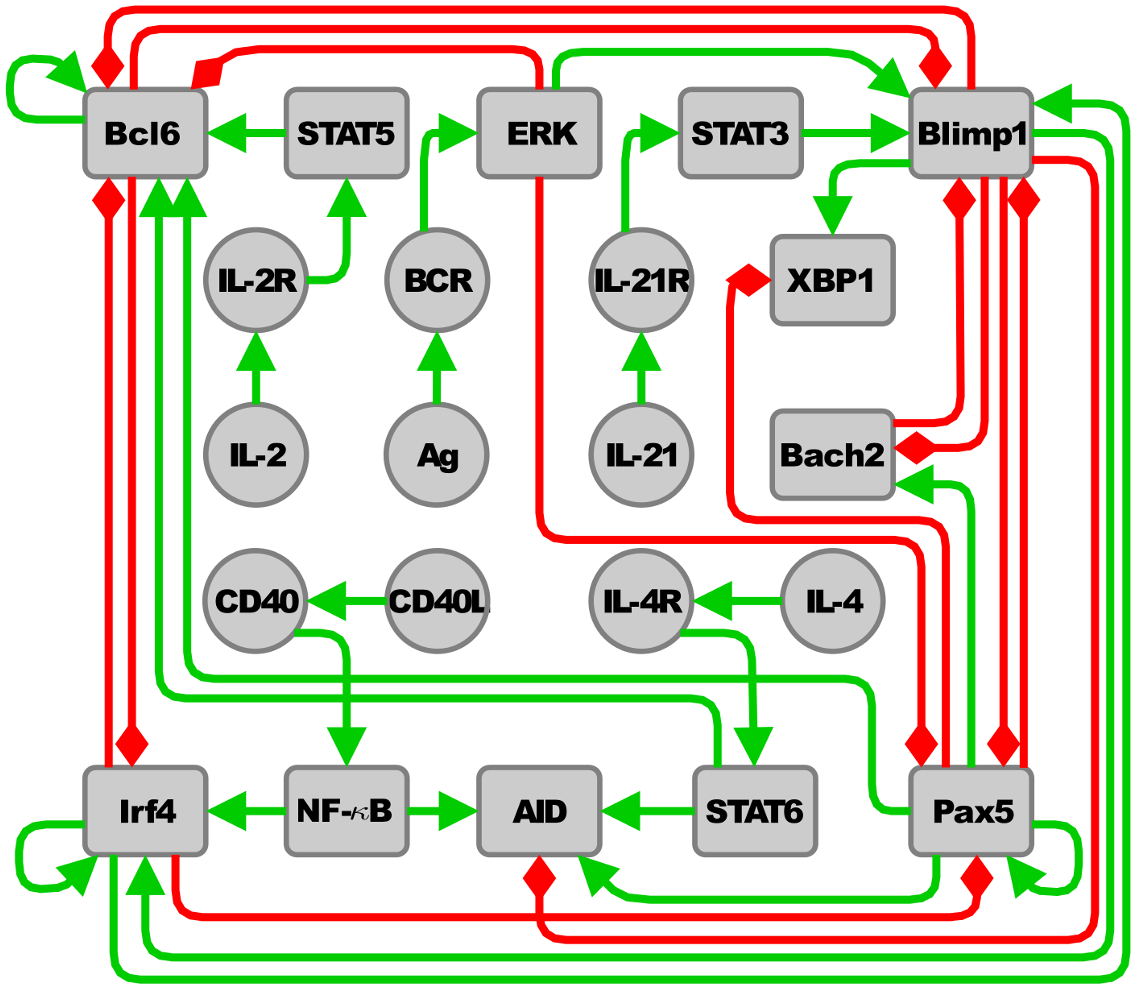
正如标题所述,我使用networkX来表示Python中的一些单元网络。因为这是一张大图片,所以网络就在这篇文章的底部。
我这么做的原因是,有些节点被认为是“输入”,而有些则被认为是“输出”,我需要能够计算每个节点参与的信号路径数(从输入到输出的路径数)。但是,我不认为networkX提供边缘方向性,我认为这是计算节点信号路径所必需的。
有没有人知道它是否有可能在networkX中增加方向,或者是否有可能在没有方向性的情况下计算信号路径?
下面是我编写的代码,直到我意识到我需要定向边缘:
import networkx as nx
import matplotlib.pyplot as plt
G=nx.Graph()
molecules = ["CD40L", "CD40", "NF-kB", "XBP1", "Pax5", "Bach2", "Irf4", "IL-4",
"IL-4R", "STAT6", "AID", "Blimp1", "Bcl6", "ERK", "BCR", "STAT3", "Ag", "STAT5",
"IL-21R", "IL-21", "IL-2", "IL-2R"]
Bcl6_edges = [("Bcl6", "Bcl6"), ("Bcl6", "Blimp1"), ("Bcl6", "Irf4")]
STAT5_edges = [("STAT5", "Bcl6")]
edges = Bcl6_edges + STAT5_edges
G.add_nodes_from(molecules)
G.add_edges_from(edges)
回答 1
Stack Overflow用户
回答已采纳
发布于 2017-08-02 19:28:28
使用G = nx.DiGraph()获取有向图。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/45469092
复制相关文章
相似问题

