如何防止分水岭算法中封闭背景区域的不准确分割?
如何防止分水岭算法中封闭背景区域的不准确分割?
提问于 2017-05-22 18:26:39
我使用分水岭算法来分割黑暗背景上的亮点。下面提供了代码以及它生成的一些图像。
在第二张图片中,我用红色的十字标记了封闭的背景区域,这些区域被分割成“细胞”(它们不是生物细胞,只是使用单词)--这是不正确的,它们是背景的一部分,只是被‘cell’所包围。我看到这造成了一个错误的最小值,有什么帮助来防止这个吗?
% Improve contrast, binarize
RFP_adjust = imadjust(RFP_blur, stretchlim(RFP_blur, 0.001));
figure, imshow(RFP_adjust), title('Contrast adjust');
RFP_binarized = imbinarize(RFP_adjust);
RFP_perimeters = bwperim(RFP_binarized);
% figure, imshow(RFP_binarized), title('Otsu thresholding');
%2B - SEGMENTATION BY WATERSHED METHOD
% Discover putative cell centroids and process
RFP_maxs = imextendedmax(RFP_adjust, 3000);
RFP_maxs = imclose(RFP_maxs, strel('disk',5));
RFP_maxs = imfill(RFP_maxs, 'holes');
RFP_maxs = bwareaopen(RFP_maxs, 5);
RFP_max_overlay = imoverlay(RFP_adjust, RFP_perimeters | RFP_maxs, [1 .3 .3]);
figure, imshow(RFP_max_overlay), title('Maxima');
% Obtain complement - maxima become low-points (required for watershed)
RFP_comp = imcomplement(RFP_adjust);
RFP_imposemin = imimposemin(RFP_comp, ~RFP_binarized | RFP_maxs);
figure, imshow(RFP_imposemin), title('Inverted Maxima');
% Apply watershed
RFP_watershed = watershed(RFP_imposemin);
mask = im2bw(RFP_watershed, 1);
overlay3 = imoverlay(RFP_adjust, mask, [1 .3 .3]);
figure, imshow(overlay3), title('Segmented cells');
% Segment
RFP_cc = bwconncomp(RFP_watershed);
RFP_label_matrix = labelmatrix(RFP_cc);
whos labeled;
RFP_label = label2rgb(RFP_label_matrix, @spring, 'c', 'shuffle');
figure, imshow(RFP_label), title('Cells segmented');图像0-结果的图像标题为‘极大值’(即调整的原始图像与最大值和轮廓覆盖)。

图像1-图像标题为“倒排最大值”的结果
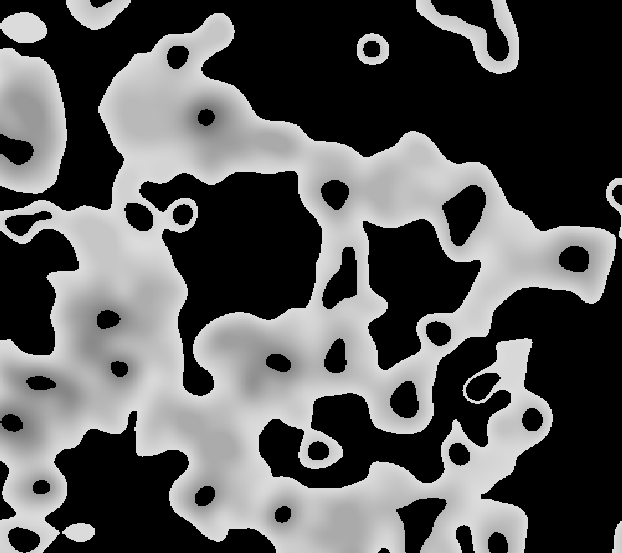
图像2-图像标题为“单元分割”的结果

回答 2
Stack Overflow用户
回答已采纳
发布于 2017-05-22 19:27:44
我建议类似于在 function中所做的事情:使用背景掩码将这些像素设置为Inf,执行分水岭操作,然后将结果中的背景像素设置为0。我相信您可以像这样更改代码的分水岭部分,以实现以下目标:
% Apply watershed
RFP_watershed = RFP_imposemin; % Added
RFP_watershed(~RFP_binarized) = Inf; % Added
RFP_watershed = watershed(RFP_watershed); % Modified
RFP_watershed(~RFP_binarized) = 0; % Added
mask = im2bw(RFP_watershed, 1);
overlay3 = imoverlay(RFP_adjust, mask, [1 .3 .3]);
figure, imshow(overlay3), title('Segmented cells');Stack Overflow用户
发布于 2017-05-22 19:20:35
没有魔法子弹,只有一些你可以尝试的东西。
一种是用一个很大的圆形圆盘过滤图像,创建一个看起来像背景的模糊图像。然后从原始图像中减去它。这往往会迫使实际背景为零。
另一种是Otsu阈值,将前景和背景分开。它创建了一个二进制图像。然后,使用设计成像实际细胞的掩膜进行形态学开放操作。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/44119709
复制相关文章
相似问题

