R中具有多个解释变量的细菌生长曲线(logistic/sigmoid)
R中具有多个解释变量的细菌生长曲线(logistic/sigmoid)
提问于 2017-05-02 00:39:46
目标:我想获得多元处理生长曲线的回归曲线(g-图曲线和模型参数)。
我有细菌培养C={a,b,c,d}在营养来源N={x,y}上生长的数据。
他们的理想生长曲线(每小时测量细胞培养的浊度)如下所示:
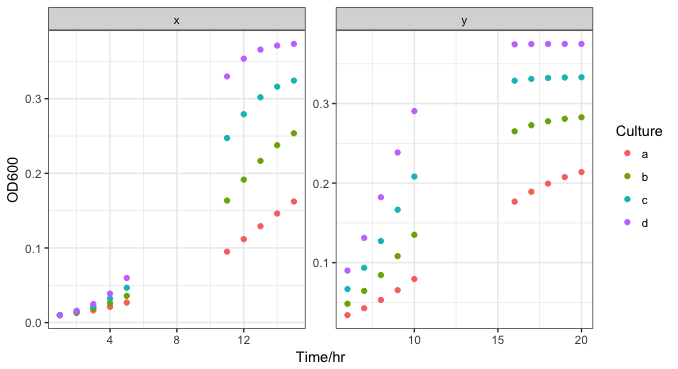
有8种不同的曲线可以得到系数和曲线。对于我的数据框架,如何能一次做到这一点,将不同的处理方式作为非线性回归的不同组来进行?
谢谢!
这个问题类似于这里发布的一个未回答的问题。
(理想化数据的源代码,抱歉它不优雅,因为我不是计算机科学家):
a<-1:20
a[1]<-0.01
for(i in c(1:19)){
a[i+1]<-1.3*a[i]*(1-a[i])
}
b<-1:20
b[1]<-0.01
for(i in c(1:19)){
b[i+1]<-1.4*b[i]*(1-b[i])
}
c<-1:20
c[1]<-0.01
for(i in c(1:19)){
c[i+1]<-1.5*c[i]*(1-c[i])
}
d<-1:20
d[1]<-0.01
for(i in c(1:19)){
d[i+1]<-1.6*d[i]*(1-d[i])
}
sub.data<-cbind(a,b,c,d)
require(reshape2)
data<-melt(sub.data, value.name = "OD600")
data$nutrition<-rep(c("x", "y"), each=5, times=4)
colnames(data)[1:2]<-c("Time", "Culture")
ggplot(data, aes(x = Time, y = OD600, color = Culture, group=nutrition)) +
theme_bw() + xlab("Time/hr") + ylab("OD600") +
geom_point() + facet_wrap(~nutrition, scales = "free")回答 1
Stack Overflow用户
回答已采纳
发布于 2017-09-06 20:55:12
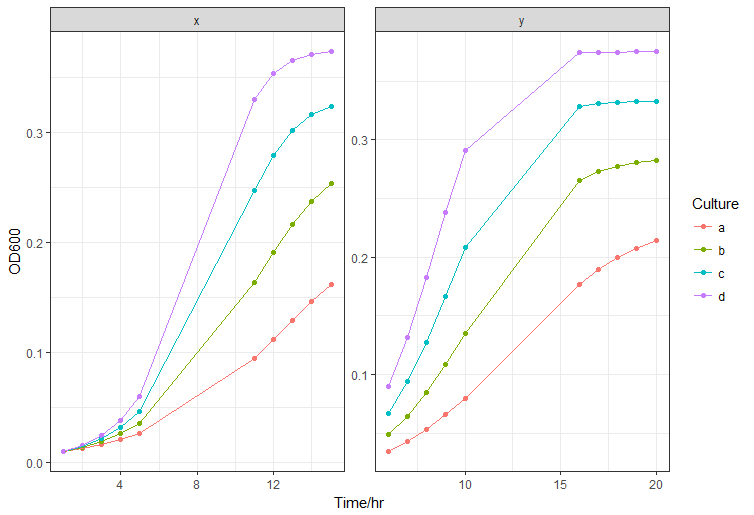
如果您熟悉来自dplyr的dplyr函数(包括在tidyverse中),那么您可以根据文化和营养对数据进行分组,并使用broom为每个组创建模型。我认为这个格列奈特正在达到你想要达到的目标。下面是一段代码:
library(tidyverse)
library(broom)
library(mgcv) #For the gam model
data %>%
group_by(Culture, nutrition) %>%
do(fit = gam(OD600 ~ s(Time), data = ., family=gaussian())) %>% # Change this to whatever model you want (e.g., non-linear regession, sigmoid)
#do(fit = lm(OD600 ~ Time, data = .,)) %>% # Example using linear regression
augment(fit) %>%
ggplot(aes(x = Time, y = OD600, color = Culture)) + # No need to group by nutrition because that is broken out in the facet_wrap
theme_bw() + xlab("Time/hr") + ylab("OD600") +
geom_point() + facet_wrap(~nutrition, scales = "free") +
geom_line(aes(y = .fitted, group = Culture))如果你一次都没问题,就把%>%拆开,以便更好地理解。我用的是GAM,它适用于这里,但是你可以用你想要的任何型号来代替它,包括sigmoid。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/43728424
复制相关文章
相似问题

