sklearn.decomposition.PCA特征向量的简单图
我试图了解Principal Component Analysis是如何工作的,我正在sklearn.datasets.load_iris数据集上测试它。我理解每个步骤是如何工作的(例如标准化数据、协方差、特征值排序、使用K选择的维度将原始数据转换为新的轴)。
下一步是可视化这些eigenvectors在dataset上的投影位置(在PC1 vs. PC2 plot上,对吗?)
有人能解释如何在降维数据集的三维图上绘制PC1、PC2、PC3特征向量吗?
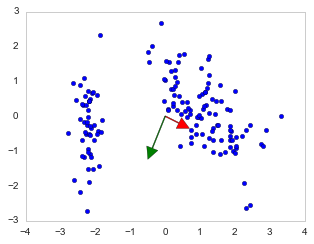
另外,我是否正确地绘制了这个2D版本?我不知道为什么我的第一个特征向量有更短的长度。我应该乘以特征值吗?
这里是我为实现这一目标所做的一些研究:
下面的PCA方法来自:https://plot.ly/ipython-notebooks/principal-component-analysis/#Shortcut---PCA-in-scikit-learn (尽管我不想使用plotly )。我想坚持使用pandas, numpy, sklearn, matplotlib, scipy, and seaborn)
我一直在遵循本教程来绘制特征向量,这看起来很简单:Basic example for PCA with matplotlib,但我似乎无法用数据复制结果。
我发现了这一点,但是对于我想要做的事情来说,这似乎太复杂了,我不想创建一个FancyArrowPatch:plotting the eigenvector of covariance matrix using matplotlib and np.linalg
--我试图使我的代码尽可能简单地遵循其他教程:
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
from sklearn.datasets import load_iris
from sklearn.preprocessing import StandardScaler
from sklearn import decomposition
import seaborn as sns; sns.set_style("whitegrid", {'axes.grid' : False})
%matplotlib inline
np.random.seed(0)
# Iris dataset
DF_data = pd.DataFrame(load_iris().data,
index = ["iris_%d" % i for i in range(load_iris().data.shape[0])],
columns = load_iris().feature_names)
Se_targets = pd.Series(load_iris().target,
index = ["iris_%d" % i for i in range(load_iris().data.shape[0])],
name = "Species")
# Scaling mean = 0, var = 1
DF_standard = pd.DataFrame(StandardScaler().fit_transform(DF_data),
index = DF_data.index,
columns = DF_data.columns)
# Sklearn for Principal Componenet Analysis
# Dims
m = DF_standard.shape[1]
K = 2
# PCA (How I tend to set it up)
M_PCA = decomposition.PCA(n_components=m)
DF_PCA = pd.DataFrame(M_PCA.fit_transform(DF_standard),
columns=["PC%d" % k for k in range(1,m + 1)]).iloc[:,:K]
# Plot the eigenvectors
#https://stackoverflow.com/questions/18299523/basic-example-for-pca-with-matplotlib
# This is where stuff gets weird...
data = DF_standard
mu = data.mean(axis=0)
eigenvectors, eigenvalues = M_PCA.components_, M_PCA.explained_variance_ #eigenvectors, eigenvalues, V = np.linalg.svd(data.T, full_matrices=False)
projected_data = DF_PCA #np.dot(data, eigenvectors)
sigma = projected_data.std(axis=0).mean()
fig, ax = plt.subplots(figsize=(10,10))
ax.scatter(projected_data["PC1"], projected_data["PC2"])
for axis, color in zip(eigenvectors[:K], ["red","green"]):
# start, end = mu, mu + sigma * axis ### leads to "ValueError: too many values to unpack (expected 2)"
# So I tried this but I don't think it's correct
start, end = (mu)[:K], (mu + sigma * axis)[:K]
ax.annotate('', xy=end,xytext=start, arrowprops=dict(facecolor=color, width=1.0))
ax.set_aspect('equal')
plt.show()
回答 1
Stack Overflow用户
发布于 2016-06-22 20:02:50
我想你问错问题了。特征向量是主成分(PC1、PC2等)。因此,绘制PC1,PC2,PC3三维图中的特征向量就是简单地绘制该图的三个正交轴。
你可能想要可视化特征向量在你原来的坐标系中的样子。这是您的第二个链接:Basic example for PCA with matplotlib中讨论的内容。
https://stackoverflow.com/questions/37976564
复制相似问题

