用ggplot2和drc绘制剂量响应曲线
在生物学中,我们经常想要绘制剂量反应曲线。R包'drc‘是真正有用的,基本图形可以轻松处理'drm模型’。但是,我想将我的drm曲线添加到一个ggplot2中。
我的数据集:
library("drc")
library("reshape2")
library("ggplot2")
demo=structure(list(X = c(0, 1e-08, 3e-08, 1e-07, 3e-07, 1e-06, 3e-06,
1e-05, 3e-05, 1e-04, 3e-04), Y1 = c(0, 1, 12, 19, 28, 32, 35,
39, NA, 39, NA), Y2 = c(0, 0, 10, 18, 30, 35, 41, 43, NA, 43,
NA), Y3 = c(0, 4, 15, 22, 28, 35, 38, 44, NA, 44, NA)), .Names = c("X",
"Y1", "Y2", "Y3"), class = "data.frame", row.names = c(NA, -11L
))使用基本图形:
plot(drm(data = reshape2::melt(demo,id.vars = "X"),value~X,fct=LL.4(),na.action = na.omit),type="bars")产生了一个很好的4参数剂量反应图。
为了在ggplot2中绘制同样的情节,我偶然发现了两个问题。
- 没有直接添加drm模型曲线的方法。我需要将4-PL重写为一个函数,并以stat_function的形式添加它,这至少是很麻烦的。 ggplot(repe2::id.vars = "X")、aes(X,value)+ geom_point() +stat_function(stat_function= function(x){ drm_y=function(x,drm){ drm_y=function}+ drm_y(x,drm =drm)(数据=repe2::stat_function(演示),( id.vars = "X"),值~X,fct=LL.4(),na.action =na.omit)}
- 如果这还不够的话,只有在scale_x是连续的情况下,它才能起作用。如果我想添加
scale_x_log10(),我得到:Warning message: In log(x): NaNs produced。
我意识到了log10(0) = -Inf,但是有办法处理这件事。无论是(和plot.drc一样),x=0值都是在x轴上绘制的,基本上是前最低x值的1/100。(demo$X[which.min(demo$X)+1]/100)或在GraphPad棱镜中,在剂量反应曲线中完全忽略了0。
我的问题是:
- 有没有一种在ggplot2中直接绘制数字版权管理模型的方法?
- 如何将数据集与其相应的4-PL曲线链接起来,以便将其绘制成相同的颜色?
回答 3
Stack Overflow用户
发布于 2016-05-05 06:21:28
来自近期论文包作者的drc包含了提取参数以供ggplot2使用的说明。它们不在ggplot2中工作,而是从模型中提取数据。这是应用于您的数据的解决方案。
demo1 <- reshape2::melt(demo,id.vars = "X") # get numbers ready for use.
demo.LL.4 <- drm(data = demo1,value~X,fct=LL.4(),na.action = na.omit) # run model.predict函数可以从drm模型中提取参数。它与使用curveid的多条曲线不兼容。
# predictions and confidence intervals.
demo.fits <- expand.grid(conc=exp(seq(log(1.00e-04), log(1.00e-09), length=100)))
# new data with predictions
pm <- predict(demo.LL.4, newdata=demo.fits, interval="confidence")
demo.fits$p <- pm[,1]
demo.fits$pmin <- pm[,2]
demo.fits$pmax <- pm[,3]他们建议转移零浓度以避免与coord_trans有关的问题。
demo1$XX <- demo1$X
demo1$XX[demo1$XX == 0] <- 1.00e-09然后是绘制曲线,省略geom_ribbon会阻止绘制错误。
ggplot(demo1, aes(x = XX, y = value)) +
geom_point() +
geom_ribbon(data=demo.fits, aes(x=conc, y=p, ymin=pmin, ymax=pmax), alpha=0.2) +
geom_line(data=demo.fits, aes(x=conc, y=p)) +
coord_trans(x="log")
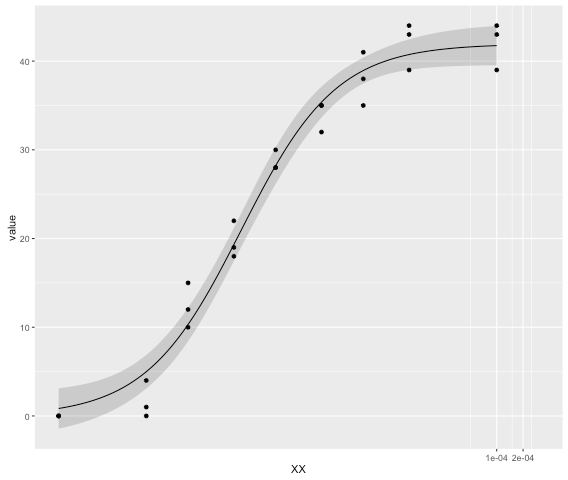
若要将多条曲线绘制在一起,则可以重复此过程。向每组添加ID。
demo.fits_1 <- data.frame(label = "curve1", demo.fits)然后使用rbind组合所有提取的参数。从那起,ggplot就可以处理颜色了。
Stack Overflow用户
发布于 2016-04-29 20:34:31
我将回答我自己的问题,希望这将有助于其他面临同样问题的人。
当然,用ggplot2绘制剂量响应曲线是可能的,如果在线性尺度上绘图,则可以简单地添加geom_或stat_smooth (method=drm, fct=LL.4(),se=FALSE),或者如果添加scale_x_log10(),则绘制geom_或stat_smooth (method=drm, fct=L.4(),se=FALSE)。
为了能够使用log10刻度,我将数据转换为:
demo <- demo %>%
mutate(X =
ifelse(X == 0,
yes = (sort(demo$X[which.min(sort(demo$X)) + 1]/100)),
no = X
)
) #looks for the pre-lowest value in X and divides it by 100在本例中,我将X=0替换为前一个X值的1/100(在本例中为1e-10)。但是,您可以像Prism一样,完全从dataset中省略0值,从而很容易地删除混淆对数绘图的0值。需要注意的一点是,正如我所发现的那样,ggplot首先缩放轴,然后添加数据,这就是为什么代码在尝试log10(0)时中断的原因。
另一个微妙之处是,stat_smooth函数完全能够使用method = drm处理drm模型,但它不知道如何适应'SE‘置信区间。因此,选择se = FALSE可以进行绘图,在我看来,这样可以减少混乱的情节--只需添加错误栏即可。
最后,将fct = LL.4()更改为fct = L.4()允许在log10标度上进行绘图,因为第一次选择标度,然后再进行匹配。因此,即使轴值是非对数的,ggplot实际上已经将数据集转换为log10,因此拟合函数现在只需要logit-4P (即L.4()),而不是logit 4p (LL.4())。
geom_smooth()和stat_smooth()函数将自然采用与数据集相同的颜色,无需调整拟合函数的颜色以与数据点的颜色相对应。
总结如下:
demo <- demo %>%
mutate(X =
ifelse(X == 0,
yes = (sort(demo$X[which.min(sort(demo$X)) + 1]/100)),
no = X
)
)
demo.long <- reshape2::melt(demo,id.vars = "X") #reshapes the demo dataset to long format
ggplot(data = demo.long,
aes(x = X, y = value, col = variable)
) +
geom_point() +
geom_smooth(method = drm, fct = L.4(), se = FALSE) +
scale_x_log10() #plots out the dataset with the corresponding 4-parameter log-logit dose response curvesStack Overflow用户
发布于 2022-01-07 19:27:07
最新的答案:geom_smooth(method = drm, method.args = list(fct = L.4()), se = FALSE)是超级有用的!
https://stackoverflow.com/questions/36780357
复制相似问题

