在R(控制图)的qcc包中使用ewma时隐藏点
在R(控制图)的qcc包中使用ewma时隐藏点
提问于 2016-01-23 12:35:55
尝试了两次q5[4]<-NULL,因为它们保存了我想要去掉的点的值,但是我得到了一个错误,表示'x‘和'y’长度不同。
我想在下面的图表中隐藏"+“点:
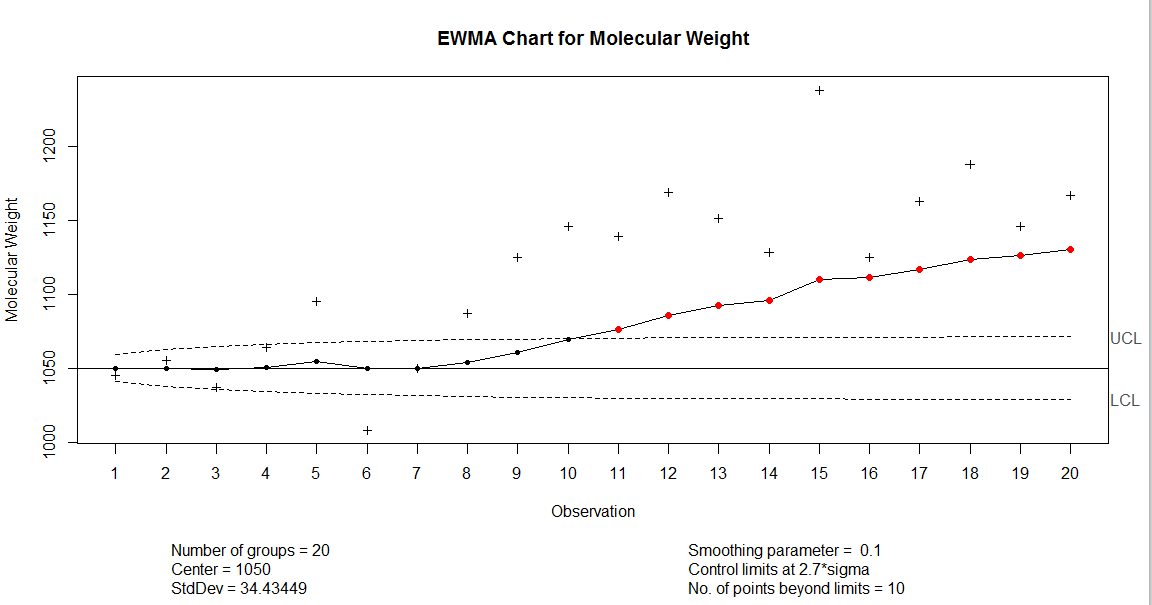
下面是代码:
q5data<-structure(list(x = c(1045L, 1055L, 1037L, 1064L, 1095L, 1008L,
1050L, 1087L, 1125L, 1146L, 1139L, 1169L, 1151L, 1128L, 1238L,
1125L, 1163L, 1188L, 1146L, 1167L)), .Names = "x", class = "data.frame",row.names = c(NA,
-20L))
library(qcc)
qcc.options(bg.margin = "transparent")
q5<-ewma(q5data, center=1050,nsigmas=2.7,lambda=0.1,ylab="Molecular Weight",xlab="Observation",title="EWMA Chart for Molecular Weight")回答 1
Stack Overflow用户
回答已采纳
发布于 2016-01-23 23:08:28
查看plot.ewma.qcc的代码,要删除这些点,您必须通过注释掉行points(indices, statistics, pch = 3, cex = 0.8)来破解函数。然后将修改后的函数来源于您的工作区。最后,告诉R使用您刚刚创建的版本:
assignInNamespace("plot.ewma.qcc", plot.ewma.qcc, pos = "package:qcc")然后运行您的q5 <- ewma(...)命令,您将需要传递一个显式的ylim,如果没有,plot.ewma.qcc也会计算一个,并且它们在其范围计算中包含了这些点的值(这在您的绘图中留下了很多空白)。
如何获得代码的副本:转到像这个一这样的CRAN镜像。在左边,选择“包”,然后选择第二个链接“可用包表,按名称排序”。向下滚动到"qcc“并单击该链接。单击“包源”的链接,当前为"qcc_2.6.tar.gz“,并下载到您的计算机。打开它,它会给你一个文件夹。查找该文件夹中的R文件夹,然后查找ewma.R。在文本编辑器中打开该文件夹,搜索plot.ewma.qcc,如果要定期使用该函数,您可能希望将整个函数复制到新文件夹中。然后按照上面描述的方式编辑它。确保你得到了整个函数,一直到结束支撑。看起来像是221-353行。虽然这是访问任何包的代码的过程,但您也可以直接访问包页面,如:http://cloud.r-project.org/package=qcc
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/34963524
复制相关文章
相似问题

