序列图及其逆补图的绘制
我是一名生物信息专家,最近开始学习蟒蛇,我对绘制图形感兴趣,我有一组节点和边缘。
节点
set(['ACG', 'ATC', 'GAT', 'CGG', 'CGT', 'AAT', 'ATT', 'GGA', 'TTC', 'CCG', 'TCC', 'GAA'])边缘
[('ACG', 'CGG'), ('CGG', 'GGA'), ('GGA', 'GAA'), ('GAA', 'AAT'), ('AAT', 'ATC'), ('GAT', 'ATT'), ('ATT', 'TTC'), ('TTC', 'TCC'), ('TCC', 'CCG'), ('CCG', 'CGT')]当我利用上述信息构造正规图时,得到了12个节点和10个边,即使用以下函数构造的两个不连通图。
def visualize_de_bruijn():
""" Visualize a directed multigraph using graphviz """
nodes = set(['ACG', 'ATC', 'GAT', 'CGG', 'CGT', 'AAT', 'ATT', 'GGA', 'TTC', 'CCG', 'TCC', 'GAA'])
edges = [('ACG', 'CGG'), ('CGG', 'GGA'), ('GGA', 'GAA'), ('GAA', 'AAT'), ('AAT', 'ATC'), ('GAT', 'ATT'), ('ATT', 'TTC'), ('TTC', 'TCC'), ('TCC', 'CCG'), ('CCG', 'CGT')]
dot_str = 'digraph "DeBruijn graph" {\n'
for node in nodes:
dot_str += ' %s [label="%s"] ;\n' % (node, node)
for src, dst in edges:
dot_str += ' %s -> %s ;\n' % (src, dst)
return dot_str + '}\n'在生物学中,我们有一个互补碱基配对的概念,其中A=T,T=A,G=C,C=G,所以'ACG‘是'TGC’,相反是'ACG‘= 'CGT’,即我们反转补语。
在节点列表中,我们看到12个节点,其中6个节点是反向互补的,即
ReverseComplement('ACG') = CGT
ReverseComplement('CGG') = CCG
ReverseComplement('GGA') = TCC
ReverseComplement('GAA') = TTC
ReverseComplement('AAT') = ATT
ReverseComplement('ATC') = GAT现在我想构造一个有六个节点的图,一个节点应该有它自己的值,它的反向补值和总共10个边,即图不应该断开。如何在python中使用graphviz可视化这个图?如果除了graphviz之外,还有什么可以帮助我可视化这种图形的话,请告诉我。?
回答 1
Stack Overflow用户
发布于 2015-10-15 11:18:05
我不太清楚你想在这里完成什么(所以请注意,你可能有一个XY问题),但让我们拿出你的问题,看看它能给我们带来什么。)
节点应该有它自己的值和它的反向补值。
所以我们需要一些对象来存储一个序列和这个序列的反向补充。
有序列反向补码的不同方法。作为一名生物信息专家,您确实应该使用一个适合生物信息学的库,即BioPython。
然后进行反向补语,如下所示:
from Bio.Seq import Seq
seq = 'ATCG'
print str(Seq(seq).reverse_complement()) # CGAT但是生成Seq对象可能会导致这个问题,所以我只使用下面的标准字典。我们还希望比较Node对象和其他对象,因此需要重写__eq__。而且,由于我们希望生成一个由唯一的set对象组成的Node,所以我们也需要实现__hash__。对于漂亮的打印,我们还实现了__str__。
class Node(object):
def __init__(self, seq):
self.seq = seq
self.revcompl = self.revcompl()
def revcompl(self):
complement = {'A': 'T', 'C': 'G', 'G': 'C', 'T': 'A'}
return "".join(complement.get(base, base) for base in reversed(self.seq))
def __eq__(self, other):
return self.seq == other.seq or self.revcompl == other.seq
def __hash__(self):
return hash(self.seq) ^ hash(self.revcompl)
def __str__(self):
return '({}, {})'.format(self.seq, self.revcompl)因此,现在我们可以将集合或原始节点转化为新节点列表,并将它们反向补充。
nodes = set(['ACG', 'ATC', 'GAT', 'CGG', 'CGT', 'AAT', 'ATT', 'GGA', 'TTC', 'CCG', 'TCC', 'GAA'])
newnodes = set(Node(seq) for seq in nodes)
assert len(newnodes) == 6现在我们需要连接节点。你并没有在你的问题中真正说明你是如何生成带边的列表的。您发布的内容的可视化看起来确实与您所描述的一样:两个断开连接的图形。
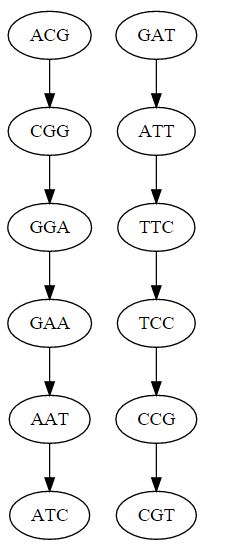
但是,当我创建一个DeBruijn图时,我会对所有序列进行配对比较,看看它们之间是否有任何重叠,创建一个邻接列表,并由此生成图形的DOT代码。
from itertools import product
def suffix(seq, overlap):
return seq[-overlap:]
def prefix(seq, overlap):
return seq[:overlap]
def has_overlap_seq(seq1, seq2, overlap=2):
if seq1 == seq2:
return False
return suffix(seq1, overlap) == prefix(seq2, overlap)
def get_adjacency_list_seqs(sequences, overlap=2):
for seq1, seq2 in product(sequences, repeat=2):
if has_overlap_seq(seq1, seq2, overlap):
yield seq1, seq2
def make_dot_plot(adjacency_list):
"""Creates a DOT file for a directed graph."""
template = """digraph "DeBruijn graph"{{
{}
}}""".format
edges = '\n'.join('"{}" -> "{}"'.format(*edge) for edge in adjacency_list)
return template(edges)如果我这么做是为了你原来的nodes,
seq_adjacency_list = get_adjacency_list_seqs(nodes)
print make_dot_plot(seq_adjacency_list)我得到一个连通图:
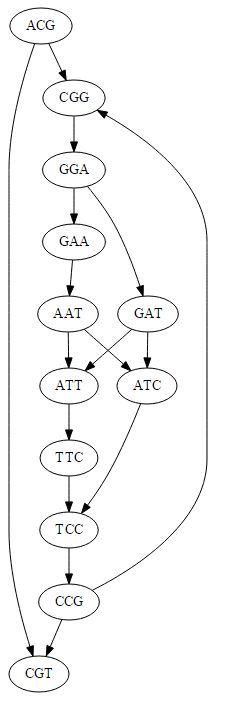
因此,我不确定在生成edges列表的原始实现中是否出现了错误,或者您是否试图完全执行其他操作。
现在,我们可以对前面的序列字符串代码进行调整,以处理我们之前创建的Node对象。
def has_overlap_node(node1, node2, overlap=2):
if node1 == node2:
return False
return suffix(node1.seq, overlap) == prefix(node2.seq, overlap) or \
suffix(node1.seq, overlap) == prefix(node2.revcompl, overlap) or \
suffix(node1.revcompl, overlap) == prefix(node2.seq, overlap) or \
suffix(node1.revcompl, overlap) == prefix(node2.revcompl, overlap)
def get_adjacency_list_nodes(nodes, overlap=2):
for node1, node2 in product(nodes, repeat=2):
if has_overlap_node(node1, node2, overlap):
yield node1, node2应用这个
nodes_adjacency_list = get_adjacency_list_nodes(newnodes)
print make_dot_plot(nodes_adjacency_list)生成
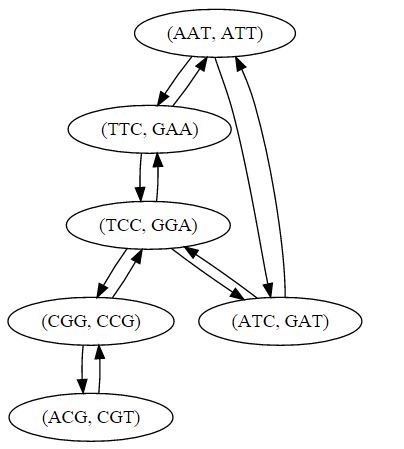
它确实有6个节点,但不是请求的10个边,而是12个节点。
https://stackoverflow.com/questions/33101105
复制相似问题

