在R中使用生成图
在R中使用生成图
提问于 2014-11-22 01:06:57
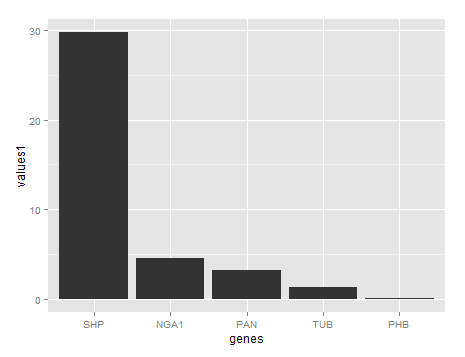
我试图用qRT-聚合酶链反应(QRT)值在x轴上制作一个条形图,比较y轴的归一化折叠诱导(例如,最大的诱导基因是SHP,归一化折叠诱导值为30,然后是SHP....PHB,等等)。我挣扎了很久,在R里做不到这个数字,有人能帮我一把吗?非常感谢。
代表-SHP-NGA1 1-平底锅-浴缸-PHB
Rep1 _
Rep2 _
回答 1
Stack Overflow用户
回答已采纳
发布于 2014-11-22 01:32:29
我想这就是你想要的
library(ggplot2) #load library
genes<-factor(c('SHP', 'NGA1', 'PAN', 'TUB', 'PHB'))
values1<-c(29.77,4.55,3.23,1.28,0.06)
values2<-c(30.37,3.43,2.07,0.81,4.93)
df<- data.frame(genes,values1,values2) #put your data in dataframe
ggplot(data=df,aes(x=genes,y=values1)) + geom_bar(stat='identity') + #plot with ggplot2
scale_x_discrete(limits=df$genes[order(levels(df$genes))]) #order your data descending我绘制了x轴上的名称和y轴上的值1的数据。如果需要,可以使用上述代码,如值2所示。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/27072933
复制相关文章
相似问题

