R 3.1.1中p值的局部FDR
R 3.1.1中p值的局部FDR
提问于 2014-10-06 16:14:12
我正在试图找到一个包来计算Efron的本地FDR来进行一系列测试。我有超过1000个协变量,所以多次修正是肯定的。
查找本地FDR将看到locfdr包在CRAN上不再可用。知道为什么会被移除吗?这似乎与当地FDR的原始出版物有着最密切的关系。
我确实找到了fdrtool,但它不能从p值计算本地FDR。我发现的其他软件包在3.1.1-LocalFDR、LocalFDR、kerfdr、twilight中是不可用的。当然,所有这些包使用的方法略有不同。即使我能找到他们,该选哪一个呢?
回答 1
Stack Overflow用户
回答已采纳
发布于 2014-10-30 11:00:19
twilight包可以这样做(正如注释中所建议的那样)。它很容易使用,如下图所示,生物导体上也有相当清晰的微缩体。
首先,我们安装软件包。
# Install twilight
source("http://bioconductor.org/biocLite.R")
biocLite("twilight")接下来,我们模拟了一些测试分数和p值.
# Simulate p p-values
set.seed(1)
p <- 10000 # Number of "genes"
prob <- 0.2 # Proportion of true alternatives
# Simulate draws from null (=0) or alternatives (=1)
null <- rbinom(p, size = 1, prob = prob)
# Simulate some t-scores, all non-null genes have an effect of 2
t.val <- (1-null)*rt(p, df = 15) + null*rt(p, df = 15, ncp = 2)
# Compute p-values
p.val <- 2*pt(-abs(t.val), df = 15)
# Plot the results
par(mfrow = c(1,2))
hist(t.val, breaks = 70, col = "grey",
xlim = c(-10, 10), prob = TRUE, ylim = c(0, .35))
hist(p.val, breaks = 70, prob = TRUE)
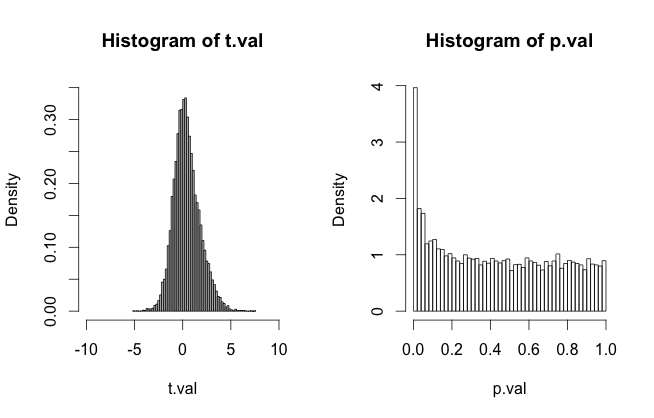
接下来,我们加载库并运行fdr分析:
library(twilight)
ans <- twilight(p.val)我们看到,对实际替代比例的估计是相当好的:
print(1 - ans$pi0)
#[1] 0.1529
print(prob)
#[1] 0.2包按递增顺序重新排序p值、q值和fdr值,所以我们做了一个技巧来重建原来的顺序。
o <- order(order(p.val))
fdr <- ans$result$fdr[o]
plot(p.val, fdr, pch = 16, col = "red", cex = .2)
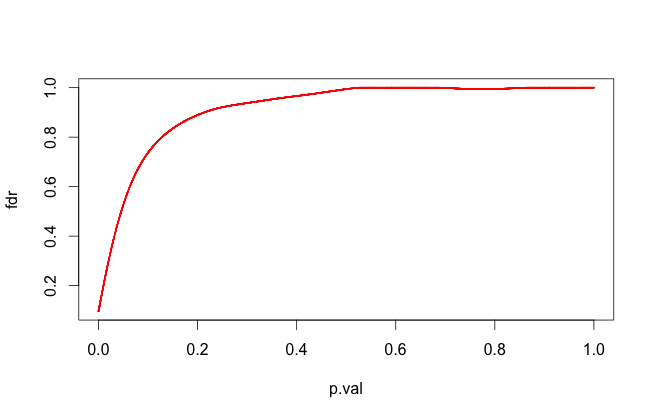
最后,我们可以把重要的与真实的交叉起来:
table(estimate = fdr < 0.5, truth = as.logical(null))
# truth
#estimate FALSE TRUE
# FALSE 7564 1172
# TRUE 368 896因此,我们有一个84.6 %的准确性在这个玩具-例子。我希望这能帮到你。twilight函数还为fdr提供了引导CIs功能,您可以在?twilight中找到它,并提供进一步的参考资料。
编辑看起来fdrtool包(它在CRAN上)实际上可以从p值计算本地fdr。在我们的例子中,我们做了以下工作:
library("fdrtool")
fdr <- fdrtool(p.val, statistic="pvalue")
fdr$lfdr # The local fdr values页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/26220379
复制相关文章
相似问题

