Python中的clustering和kmeans2聚类问题
Python中的clustering和kmeans2聚类问题
提问于 2014-08-14 06:31:20
我有一个关于kmeans和kmeans2的问题。我有一套1700长的数据点。我想在空间上把它们聚成100个。然而,在使用kmeans和kmeans2时,我得到了截然不同的结果。你能解释一下为什么吗?我的密码在下面。
首先,我加载数据并绘制坐标。看上去都是对的。
import pandas as pd, numpy as np, matplotlib.pyplot as plt
from scipy.cluster.vq import kmeans, kmeans2, whiten
df = pd.read_csv('data.csv')
df.head()
coordinates = df.as_matrix(columns=['lon', 'lat'])
plt.figure(figsize=(10, 6), dpi=100)
plt.scatter(coordinates[:,0], coordinates[:,1], c='c', s=100)
plt.show()
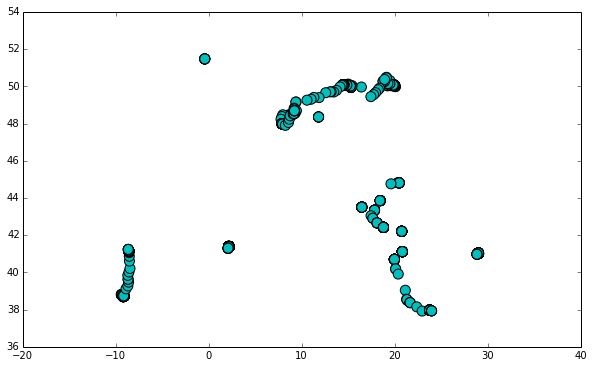
接下来,我将数据白化,并运行kmeans()和kmeans2()。当我从kmeans()绘制质心图时,它看起来是正确的--即大约100个点,它们或多或少地代表了整个1700点数据集的位置。
N = len(coordinates)
w = whiten(coordinates)
k = 100
i = 20
cluster_centroids1, distortion = kmeans(w, k, iter=i)
cluster_centroids2, closest_centroids = kmeans2(w, k, iter=i)
plt.figure(figsize=(10, 6), dpi=100)
plt.scatter(cluster_centroids1[:,0], cluster_centroids1[:,1], c='r', s=100)
plt.show()
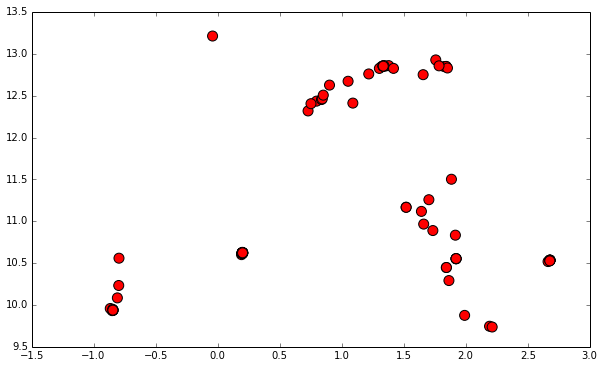
然而,当我下一次从kmeans2()中画出质心时,在我看来它完全不稳定。我希望kmeans和kmeans2的结果非常相似,但它们完全不同。虽然kmeans的结果似乎只是表示我的完整数据集,但来自kmeans2的结果看起来几乎是随机的。
plt.figure(figsize=(10, 6), dpi=100)
plt.scatter(cluster_centroids2[:,0], cluster_centroids2[:,1], c='r', s=100)
plt.show()
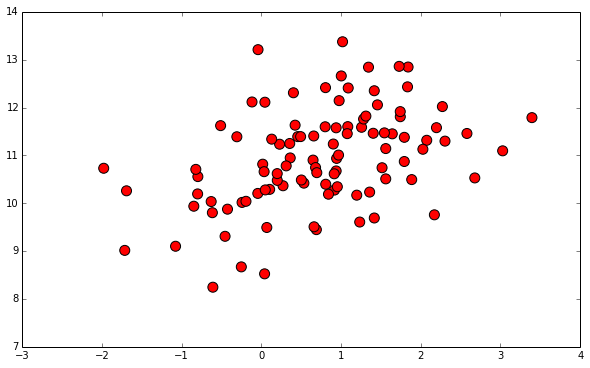
下面是我的k和N的值,以及kmeans()和kmeans2()产生的数组的大小:
print 'k =', k
print 'N =', N
print len(cluster_centroids1)
print len(cluster_centroids2)
print len(closest_centroids)
print len(np.unique(closest_centroids))输出:
k = 100
N = 1759
96
100
1759
17- 为什么
len(cluster_centroids1)不等于k? len(closest_centroids)等于N,这似乎是正确的。但是为什么len(np.unique(closest_centroids))不等于klen(cluster_centroids2)等于k,但是在绘制图形时,cluster_centroids2似乎并不像cluster_centroids1那样表示原始数据集。
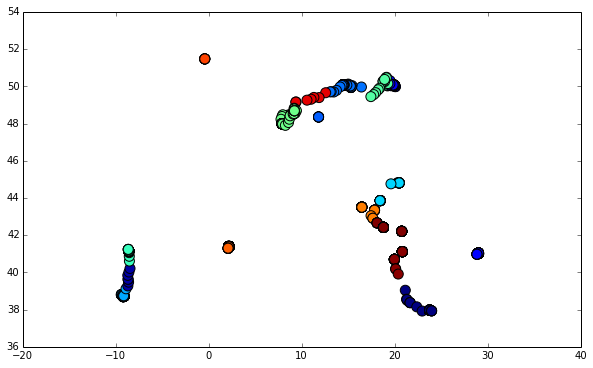
最后,我绘制了我的全部坐标数据集,用集群着色。
plt.figure(figsize=(10, 6), dpi=100)
plt.scatter(coordinates[:,0], coordinates[:,1], c=closest_centroids, s=100)
plt.show()你可以在这里看到:
回答 1
Stack Overflow用户
回答已采纳
发布于 2014-08-14 07:49:08
谢谢你的好问题与样例代码和图像!这是个很好的新手问题。
大多数的特点可以通过仔细阅读文档来解决。有几件事:
- 当比较原始的点集和产生的集群中心时,您应该尝试用相同的维度(即
w与结果相同)将它们绘制在相同的图中。例如,像您所做的那样,用大点绘制集群中心,并在上面画一些小点的原始数据。 kmeans和kmeans2从不同的情况出发。kmeans2从点的随机分布开始,由于数据分布不均匀,kmeans2收敛到一个非理想的结果。您可以尝试添加关键字minit='points'并查看结果是否更改。- 由于最初的质心选择是错误的,在最初的100个质心中,只有17个实际上有属于它们的点(这与图的随机外观密切相关)。
- 似乎
kmeans中的一些质心可能会彼此塌陷,如果这给出最小的失真。(这似乎没有记录在案。)因此,你只能得到96个质心。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/25301466
复制相关文章
相似问题

