快速、优雅的经验/样本协方差函数计算方法
如果可能的话,有没有人知道用Python计算经验/样本协方差函数的好方法?
这是一个书的屏幕截图,其中包含了covariagram的一个很好的定义:

如果我正确地理解了它,对于给定的滞后/宽度h,我应该得到由h(或小于h)分隔的所有对点,乘以它的值,并对每一个点计算它的平均值,在这种情况下,它被定义为m(x_i)。然而,根据m(x_{i})的定义,如果要计算m( x1 ),则需要得到距离x1在h以内的值的平均值。这看起来是一个非常密集的计算。
首先,我是否正确理解了这一点?如果是这样的话,假设是二维空间,什么是计算这个的好方法呢?我试着用Python (使用numpy和熊猫)来编写这个代码,但是它需要几秒钟时间,我甚至不确定它是否正确,这就是为什么我不在这里发布代码的原因。下面是另一次非常幼稚的实现尝试:
from scipy.spatial.distance import pdist, squareform
distances = squareform(pdist(np.array(coordinates))) # coordinates is a nx2 array
z = np.array(z) # z are the values
cutoff = np.max(distances)/3.0 # somewhat arbitrary cutoff
width = cutoff/15.0
widths = np.arange(0, cutoff + width, width)
Z = []
Cov = []
for w in np.arange(len(widths)-1): # for each width
# for each pairwise distance
for i in np.arange(distances.shape[0]):
for j in np.arange(distances.shape[1]):
if distances[i, j] <= widths[w+1] and distances[i, j] > widths[w]:
m1 = []
m2 = []
# when a distance is within a given width, calculate the means of
# the points involved
for x in np.arange(distances.shape[1]):
if distances[i,x] <= widths[w+1] and distances[i, x] > widths[w]:
m1.append(z[x])
for y in np.arange(distances.shape[1]):
if distances[j,y] <= widths[w+1] and distances[j, y] > widths[w]:
m2.append(z[y])
mean_m1 = np.array(m1).mean()
mean_m2 = np.array(m2).mean()
Z.append(z[i]*z[j] - mean_m1*mean_m2)
Z_mean = np.array(Z).mean() # calculate covariogram for width w
Cov.append(Z_mean) # collect covariances for all widths但是,现在我已经确认代码中有一个错误。我知道,因为我用变异函数来计算协变函数(协方差图(H)=协方差函数(0)-变异函数(H)),我得到了一个不同的图:
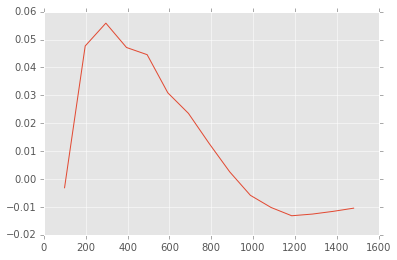
它应该是这样的:
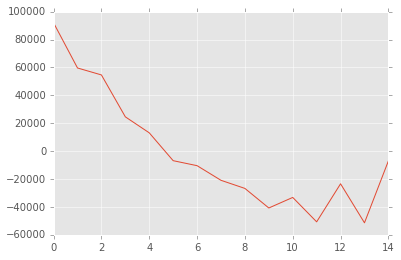
最后,如果你知道一个Python/R/MATLAB库来计算经验协变函数,请告诉我。至少这样我就能证实我做了什么。
回答 1
Stack Overflow用户
发布于 2014-06-04 17:49:55
我们可以使用scipy.cov,但是如果直接进行计算(这非常容易),有更多的方法来加快速度。
首先,制作一些具有一定空间相关性的假数据。我首先要做的是做空间相关性,然后使用使用它生成的随机数据点,其中数据是根据底层地图定位的,并且还接受底层地图的值。
编辑1:
我改变了数据点生成器,使位置是纯粹随机的,但z值与空间地图成正比。而且,我改变了地图,使左右两面相对于彼此移动,从而在大范围的h中产生负相关性。
from numpy import *
import random
import matplotlib.pyplot as plt
S = 1000
N = 900
# first, make some fake data, with correlations on two spatial scales
# density map
x = linspace(0, 2*pi, S)
sx = sin(3*x)*sin(10*x)
density = .8* abs(outer(sx, sx))
density[:,:S//2] += .2
# make a point cloud motivated by this density
random.seed(10) # so this can be repeated
points = []
while len(points)<N:
v, ix, iy = random.random(), random.randint(0,S-1), random.randint(0,S-1)
if True: #v<density[ix,iy]:
points.append([ix, iy, density[ix,iy]])
locations = array(points).transpose()
print locations.shape
plt.imshow(density, alpha=.3, origin='lower')
plt.plot(locations[1,:], locations[0,:], '.k')
plt.xlim((0,S))
plt.ylim((0,S))
plt.show()
# build these into the main data: all pairs into distances and z0 z1 values
L = locations
m = array([[math.sqrt((L[0,i]-L[0,j])**2+(L[1,i]-L[1,j])**2), L[2,i], L[2,j]]
for i in range(N) for j in range(N) if i>j])这意味着:
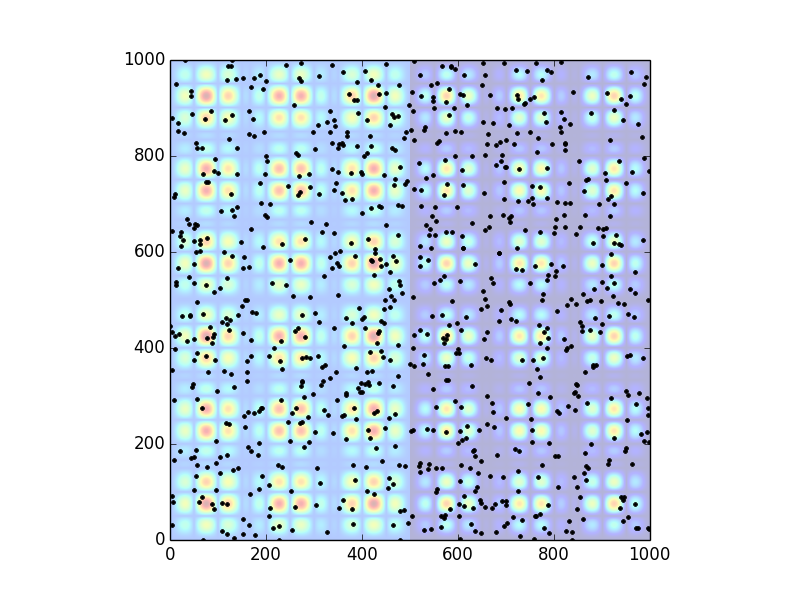
以上只是模拟的数据,我没有尝试优化它的生产,等等。我假设这是OP开始的地方,下面的任务,因为数据已经存在于实际情况中。
现在计算“协变函数”(这比生成假数据容易得多,顺便说一下)。这里的想法是通过h对所有对和相关值进行排序,然后使用ihvals对它们进行索引。也就是说,对索引ihval的求和是方程中N(h)上的和,因为这包括了hs低于所需值的所有对。
编辑2:
正如下面的注释中所建议的,N(h)现在只是h-dh和h之间的对,而不是0和h之间的所有对( dh是ihvals中h-values的间距--即下面使用的S/1000 )。
# now do the real calculations for the covariogram
# sort by h and give clear names
i = argsort(m[:,0]) # h sorting
h = m[i,0]
zh = m[i,1]
zsh = m[i,2]
zz = zh*zsh
hvals = linspace(0,S,1000) # the values of h to use (S should be in the units of distance, here I just used ints)
ihvals = searchsorted(h, hvals)
result = []
for i, ihval in enumerate(ihvals[1:]):
start, stop = ihvals[i-1], ihval
N = stop-start
if N>0:
mnh = sum(zh[start:stop])/N
mph = sum(zsh[start:stop])/N
szz = sum(zz[start:stop])/N
C = szz-mnh*mph
result.append([h[ihval], C])
result = array(result)
plt.plot(result[:,0], result[:,1])
plt.grid()
plt.show()
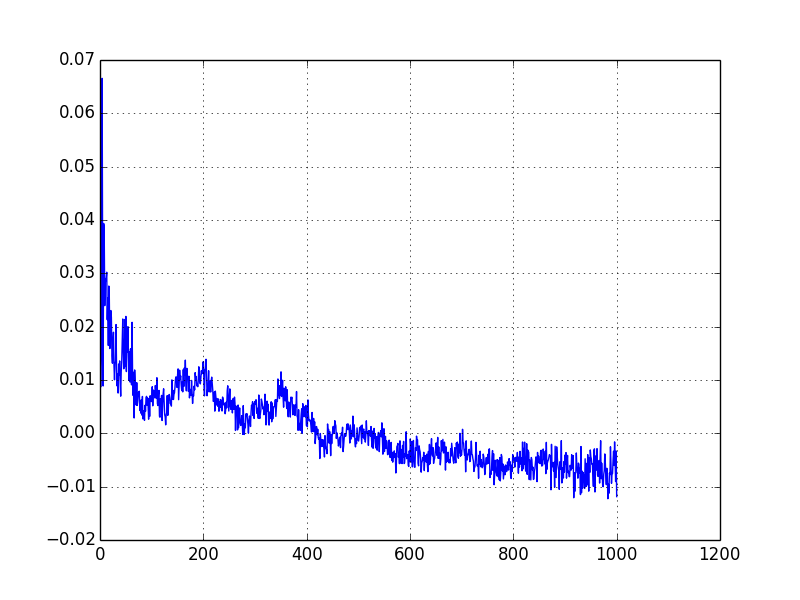
这在我看来是合理的,因为人们可以在h值的预期值处看到颠簸或低谷,但我没有仔细检查。
scipy.cov的主要加速是可以预先计算所有的产品,zz。否则,就会将zh和zsh输入到cov中,每一个新的h,并且所有的产品都将被重新计算。这个计算可以通过在每一个时间步长( ihvals[n-1] )到ihvals[n] (从n )进行部分求和来加速,但我怀疑这是必要的。
https://stackoverflow.com/questions/23943301
复制相似问题

