BioConductor IRanges覆盖率计数和识别段
BioConductor IRanges覆盖率计数和识别段
提问于 2014-04-15 03:40:39
我有一组制造电路的区间信息数据集。
df <- data.frame(structure(list(circuit = structure(c(2L, 1L, 2L, 1L, 2L, 3L,
1L, 1L, 2L), .Label = c("a", "b", "c"), class = "factor"), start = structure(c(1393621200,
1393627920, 1393628400, 1393631520, 1393650300, 1393646400, 1393656000,
1393668000, 1393666200), class = c("POSIXct", "POSIXt"), tzone = ""),
end = structure(c(1393626600, 1393631519, 1393639200, 1393632000,
1393660500, 1393673400, 1393667999, 1393671600, 1393677000
), class = c("POSIXct", "POSIXt"), tzone = ""), id = structure(1:9, .Label = c("1001",
"1002", "1003", "1004", "1005", "1006", "1007", "1008", "1009"
), class = "factor")), .Names = c("circuit", "start", "end",
"id"), class = "data.frame", row.names = c(NA, -9L)))
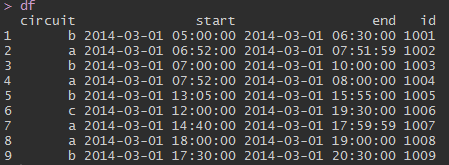
- 电路:电路标识符
- 启动:电路开始运行的时间
- Finish:电路停止运行的时间
- Id:行的唯一标识符
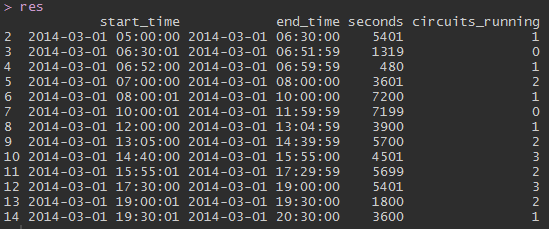
我能够创建一个新的数据集来统计重叠间隔的数量:
ir <- IRanges(start = as.numeric(df$start), end = as.numeric(df$end), names = df$id)
cov <- coverage(ir)
start_time <- as.POSIXlt(start(cov), origin = "1970-01-01")
end_time <- as.POSIXlt(end(cov), origin = "1970-01-01")
seconds <- runLength(cov)
circuits_running <- runValue(cov)
res <- data.frame(start_time,end_time,seconds,circuits_running)[-1,]
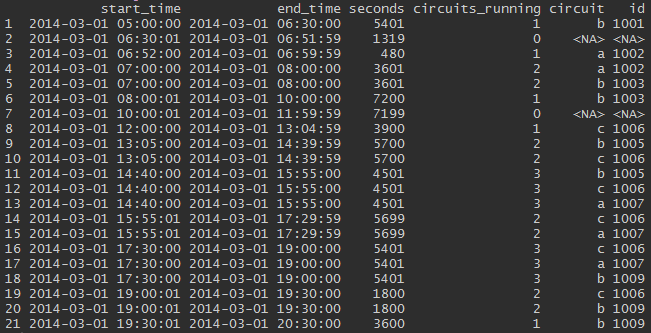
但我真正需要的是更像这样的东西:
sqldf("select
res.start_time,
res.end_time,
res.seconds,
res.circuits_running,
df.circuit,
df.id
from res left join df on (res.start_time between df.start and df.end)")
问题是,在我的完整数据集中,使用不等式联接的sqldf方式速度慢得令人难以忍受。
单独使用IRanges 如何获得类似的东西?
我怀疑这与RangedData有关,但我一直未能看到如何得到我想要的东西。这是我试过的..。
rd <- RangedData(ir, circuit = df$circuit, id = df$id)
coverage(rd) # works but seems to lose the circuit/id info回答 1
Stack Overflow用户
回答已采纳
发布于 2014-04-15 13:03:07
覆盖范围可以表示为范围,删除第一个范围(范围从1970年到第一个起点)。
cov <- coverage(ir)
intervals <- ranges(cov)[-1]您的查询是查找每个电路间隔的开始,因此我将间隔缩小到它们的起始坐标并查找重叠(第一个参数是' query ',第二个参数是'subject')。
olaps <- findOverlaps(narrow(intervals, width(intervals)), ir)在特定时间间隔内运行的电路数目为
tabulate(queryHits(olaps), queryLength(olaps))实际电路是
df[subjectHits(olaps), c("circuit", "id")]也许,这些碎片可以编织在一起。
df1 <- cbind(uid=seq_along(intervals),
as.data.frame(intervals),
circuits_running=tabulate(queryHits(olaps), queryLength(olaps)))
df2 <- cbind(uid=queryHits(olaps),
df[subjectHits(olaps), c("circuit", "id")])
merge(df1, df2, by="uid", all=TRUE)范围可以以协调的方式与可访问和子集的“元数据”相关联,因此data.frame和Ranges之间的连接不必如此松散和特殊。相反,我可能
ir <- IRanges(start = as.numeric(df$start), end = as.numeric(df$end))
mcols(ir) <- DataFrame(df)
## ...
mcols(ir[subjectHits(olaps)])也许是用as.data.frame()做的,当用IRanges land。
最好在生物导体IRanges上问你关于邮寄名单的问题,不需要订阅。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/23074264
复制相关文章
相似问题

