使用另一个子矩阵的值的子集HDF5矩阵
使用另一个子矩阵的值的子集HDF5矩阵
提问于 2014-03-18 08:55:19
我一直在处理HDF5文件,并且能够在rhdf5中做一些子设置。有三个文件:.经度、纬度和ColumnAmountNO2Trop。在一年中的所有日子里,我都把它提取为“文件”中的一个列表。
files <- list.files(pattern = ".he5", full.names = TRUE)
attribute <- "/HDFEOS/SWATHS/ColumnAmountNO2/Data Fields/ColumnAmountNO2Trop"
attribute2<-"/HDFEOS/SWATHS/ColumnAmountNO2/Geolocation Fields/Longitude"
attribute3<-"/HDFEOS/SWATHS/ColumnAmountNO2/Geolocation Fields/Latitude"子文件如下:
out.list <- lapply(files, h5read, attribute)
Lon <- lapply(files, h5read, attribute2)
Lat<-lapply(files, h5read, attribute3)但是,我需要根据纬度和经度值来子集out.list(它包含一年中所有日子的“ColumnAmountNO2Trop”),以缩小我的地理参考区域。我能够使用行号和列号对它们进行子集:
lapply(out.list, function(x) x[2:8,2:8]) 然而,第一天2,2的地理位置可能与第二天不一样。我试图将经度和纬度值定义为下面的子集,但它返回了一条错误消息。
Lond<-c(2,9)
Latd<-c(2,9)
lonKeep <- which(Lon > Lond[1] & Lon < Lond[2])
latKeep <- which(lat> latRan[1] & lat< latRan[2]) 请问如何对Lon 2-9和Lat 2-9进行“out.list”子集?
回答 1
Stack Overflow用户
回答已采纳
发布于 2014-03-18 23:02:24
您将找到其他方法,可能会有更接近您需要的解决方案。使用hdf5和光栅的一个选项是从hdf5文件中提取相关数据,构建光栅,将其裁剪到ROI并获取该区域的值。
我会这样做:
library(raster)
library(maptools)
source("http://bioconductor.org/biocLite.R")
biocLite("rhdf5")
library(rhdf5)
library(latticeExtra)
my_wd <- './Stackoverflow/22474417'
files <- list.files(path = my_wd, pattern = ".he5", full.names = F)
files
#[1] "M1.he5" "M2.he5"
attribute <- "/HDFEOS/SWATHS/ColumnAmountNO2/Data Fields/ColumnAmountNO2Trop"
attribute2<- "/HDFEOS/SWATHS/ColumnAmountNO2/Geolocation Fields/Longitude"
attribute3<- "/HDFEOS/SWATHS/ColumnAmountNO2/Geolocation Fields/Latitude"读取单个文件
m1 <- h5read(file.path(my_wd, files[1]), name = attribute)
dim(m1) # file dimension
# [1] 60 54
prod(dim(m1))
# [1] 3060在从rasterLayer和atribute3中提取地理范围之后,我们将使用它来构建一个atribute2
Lon <- h5read(file.path(my_wd, files[1]) , attribute2)
Lat <- h5read(file.path(my_wd, files[1]) , attribute3)
xmin <- min(Lon[1:prod(dim(m1))]) # Min. Longitude
# [1] -7.141283
xmax <- max(Lon[1:prod(dim(m1))]) # Max. Longitude
ymin <- min(Lat[1:prod(dim(m1))]) # Min. Longitude
ymax <- max(Lat[1:prod(dim(m1))]) # Max. Longitude我们可以用上面的信息建立一个光栅
m1m <- matrix(m1, nrow = 60)
m1r <- raster(m1m, xmn = xmin, xmx = xmax,
ymn = ymin, ymx = ymax)获取一些空间数据以覆盖
data(wrld_simpl)
spdata <- wrld_simpl[which(wrld_simpl@data$NAME %in% c('Nigeria', 'Cameroon', 'Benin',
'Togo', 'Ghana',"Cote d'Ivoire",
'Gabon', 'Equatorial Guinea')), ] 来自非洲海岸30米
delta <- readOGR(dsn = './africa_shoreline_30m',
layer = 'nigeria_delta')建立一个ROI范围
frm <- extent(c(2, 9, 2, 9))
pfrm <- as(frm, 'SpatialPolygons')图谋
spplot(m1r,scales = list(draw = TRUE), ylim=c(-1, 10)) +
latticeExtra::layer(sp.polygons(stp, fill = NA, col = 'blue'))+
latticeExtra::layer(sp.polygons(pfrm, fill = NA, col = 'red'))
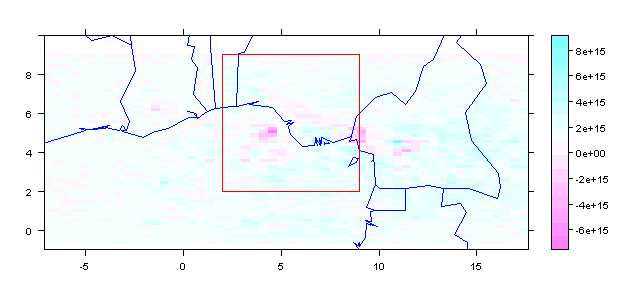
从ROI中获取值
m1rf <- crop(m1r, frm)
spplot(m1rf, scales = list(draw = TRUE), xlim = c(1, 10), ylim=c(1, 10)) +
latticeExtra::layer(sp.lines(delta, fill = NA, col = 'blue'))+
latticeExtra::layer(sp.polygons(pfrm, fill = NA, col = 'red'))
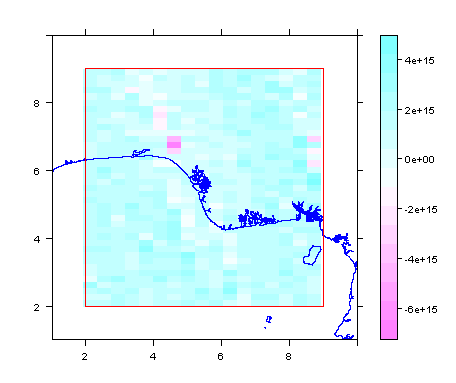
summary(m1rf)
layer
Min. -6.528723e+15
1st Qu. 9.437798e+14
Median 1.440395e+15
3rd Qu. 1.896734e+15
Max. 4.232078e+15
NA's 0.000000e+00
m1vals <- getValues(m1rf)一旦您同意这一点,就很容易遍历您的文件文件夹并获取您的数据。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/22474417
复制相关文章
相似问题

