复制间相关性的可视化
复制间相关性的可视化
提问于 2013-10-02 13:54:24
通过计算每个细胞系的生物复制对的Pearson相关系数来检验生物复制的质量。
A<-data.frame(A1=rnorm(100), A2=rnorm(100),
A3=rnorm(100), B1=rnorm(100),
B2=rnorm(100))有些情况下,数据有两个副本,而其他情况是三个,并且不包含缺少的值。如何获得这样的图解来比较复制品呢?
回答 2
Stack Overflow用户
回答已采纳
发布于 2013-10-02 15:22:45
有一种可能的方法。不过,也许有一种更简洁的方法可以做到这一点。
首先,找出哪些列是复制的。
fullnames<-colnames(A)
basenames<-substr(fullnames,1,nchar(fullnames)-1)
repnum<-as.integer(substr(fullnames,nchar(fullnames),nchar(fullnames)))现在计算相关矩阵,并提取所需的数据:
ca<-cor(A)
corMask<-upper.tri(ca) & basenames[col(ca)]==basenames[row(ca)]
corSub<-ca[corMask]
nameSub<-basenames[row(ca)[corMask]]
repnumSub<-apply(cbind(repnum[row(ca[corMask]],repnum[col(ca[corMask]]),1,paste,collapse="-")然后画出情节:
require(ggplot2)
plotdata<-data.frame(name=nameSub,cor=corSub,replicas=repnumSub)
ggplot(plotdata,aes(x=name,y=cor,pch=replicas))+geom_point()下面是下面的示例数据集:
set.seed(123)
A<-data.frame(A1=rnorm(100), A2=rnorm(100),A3=rnorm(100),
B1=rnorm(100),B2=rnorm(100),
C1=rnorm(100),C2=rnorm(100),C3=rnorm(100))
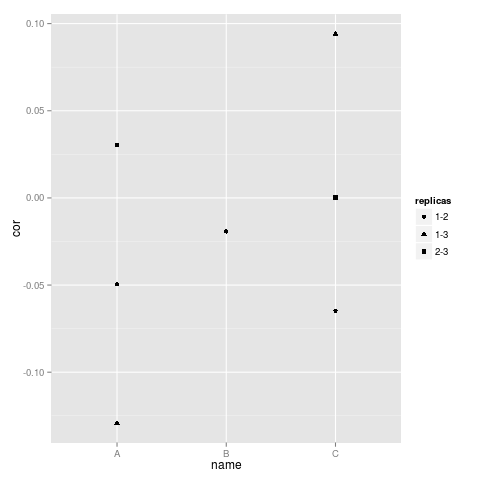
然后,您可以添加颜色或更改情节限制等,以使它看起来像你想要的方式。
Stack Overflow用户
发布于 2013-10-02 14:42:45
我建议更好的表现方式是使用热图。热图显示了复制体之间的关联。因此,从同一批细胞复制将显示出更高的相关性比其他细胞株。所以,最终你会在你的热图中的细胞对角线上看到接近1.0的值。热图还显示了不同细胞株复制体之间的相关性较差。要执行这样的绘图功能,可以使用{gplot}包中的heatmap.2。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/19138619
复制相关文章
相似问题

