基于百分位数的颜色编码点
基于百分位数的颜色编码点
提问于 2013-08-27 18:58:23
我有一些非常大的文件,其中包含一个基因组位置(位置)和相应的群体遗传统计(值)。我已经成功地绘制了这些值,并希望对值的前5% (蓝色)和1% (红色)进行颜色编码。我想知道在R中是否有一个简单的方法可以做到这一点。
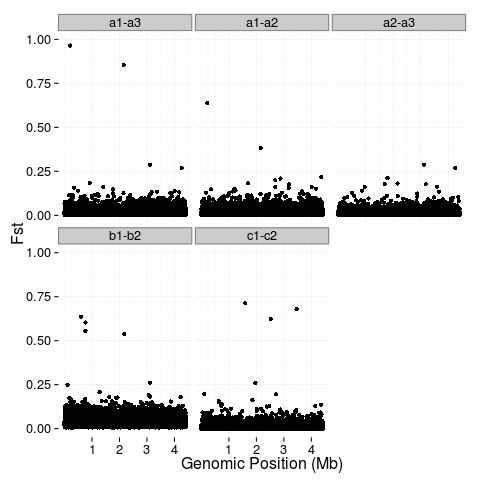
我已经探索过编写一个定义分位数的函数,但是,其中许多都不是唯一的,因此导致函数失败。我也研究过stat_quantile,但只成功地用它绘制了一条标有95%和99%的线(其中一些线是对角线,对我来说没有任何意义)。(对不起,我是R.)
任何帮助都将不胜感激。
这是我的代码:(文件非常大)
########Combine data from multiple files
fst <- rbind(data.frame(key="a1-a3", position=a1.3$V2, value=a1.3$V3), data.frame(key="a1-a2", position=a1.2$V2, value=a1.2$V3), data.frame(key="a2-a3", position=a2.3$V2, value=a2.3$V3), data.frame(key="b1-b2", position=b1.2$V2, value=b1.2$V3), data.frame(key="c1-c2", position=c1.2$V2, value=c1.2$V3))
########the plot
theme_set(theme_bw(base_size = 16))
p1 <- ggplot(fst, aes(x=position, y=value)) +
geom_point() +
facet_wrap(~key) +
ylab("Fst") +
xlab("Genomic Position (Mb)") +
scale_x_continuous(breaks=c(1e+06, 2e+06, 3e+06, 4e+06), labels=c("1", "2", "3", "4")) +
scale_y_continuous(limits=c(0,1)) +
theme(plot.background = element_blank(),
panel.background = element_blank(),
panel.border = element_blank(),
legend.position="none",
legend.title = element_blank()
)
p1回答 3
Stack Overflow用户
回答已采纳
发布于 2013-08-28 01:24:59
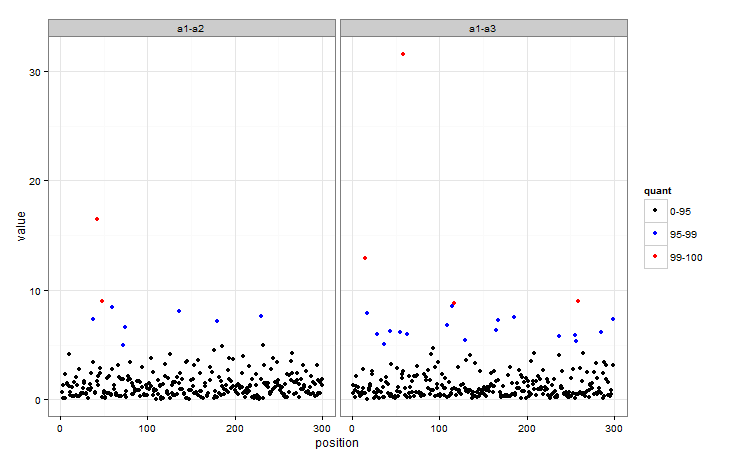
这就是我处理它的方法--基本上是创建一个因子,定义每个观察在哪个组中,然后将colour映射到该因子。
首先,一些需要处理的数据!
dat <- data.frame(key = c("a1-a3", "a1-a2"), position = 1:100, value = rlnorm(200, 0, 1))
#Get quantiles
quants <- quantile(dat$value, c(0.95, 0.99))有很多方法可以获得一个因素来确定每个观察属于哪一组,这里有一个:
dat$quant <- with(dat, factor(ifelse(value < quants[1], 0,
ifelse(value < quants[2], 1, 2))))因此,quant现在指示一个观察是在95-99还是99+组中。然后,绘图中的点的颜色可以很容易地映射到quant。
ggplot(dat, aes(position, value)) + geom_point(aes(colour = quant)) + facet_wrap(~key) +
scale_colour_manual(values = c("black", "blue", "red"),
labels = c("0-95", "95-99", "99-100")) + theme_bw()
Stack Overflow用户
发布于 2014-11-11 12:55:06
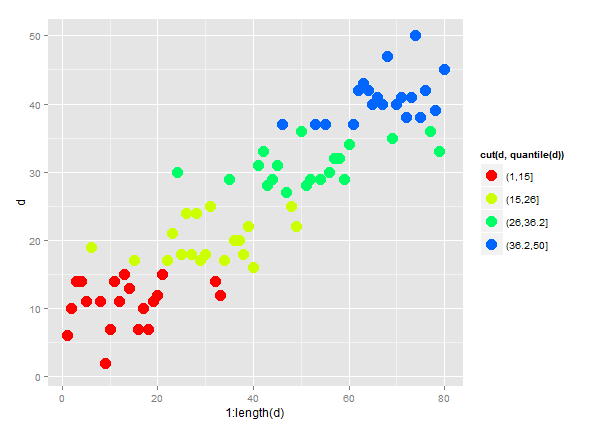
通过将quantile和cut合并到aes颜色表达式中,您可以稍微更优雅地实现这一点。例如,本例中的col=cut(d,quantile(d)):
d = as.vector(round(abs(10 * sapply(1:4, function(n)rnorm(20, mean=n, sd=.6)))))
ggplot(data=NULL, aes(x=1:length(d), y=d, col=cut(d,quantile(d)))) +
geom_point(size=5) + scale_colour_manual(values=rainbow(5))
我还为美丽的传说标签创建了一个有用的工作流,可能有人会发现它很方便。
Stack Overflow用户
发布于 2013-08-27 21:49:56
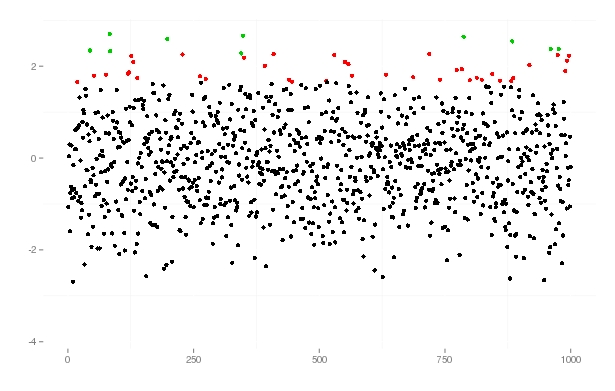
我不知道这是不是你想要的,但也许这会有帮助:
# a little function which returns factors with three levels, normal, 95% and 99%
qfun <- function(x, qant_1=0.95, qant_2=0.99){
q <- sort(c(quantile(x, qant_1), quantile(x, qant_2)))
factor(cut(x, breaks = c(min(x), q[1], q[2], max(x))))
}
df <- data.frame(samp=rnorm(1000))
ggplot(df, aes(x=1:1000, y=df$samp)) + geom_point(colour=qfun(df$samp))+
xlab("")+ylab("")+
theme(plot.background = element_blank(),
panel.background = element_blank(),
panel.border = element_blank(),
legend.position="none",
legend.title = element_blank()) 结果我得到了
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/18473382
复制相关文章
相似问题

