交互地处理xy点图簇--r中的组操作
交互地处理xy点图簇--r中的组操作
提问于 2013-05-11 15:15:48
我有大量的X和Y变量以及它们的集群成员列。聚类成员(组)可能并不总是正确的(在完善聚类算法方面的局限性),我希望交互地可视化集群,并将聚类成员关系操作到识别点。
我尝试了rggobi,下面是我能够达到的要点(我并不是说我需要使用rggobi / ggobi,如果有更好的选项,欢迎您提出建议)。
# data
set.seed (1234)
c1 <- rnorm (40, 0.1, 0.02); c2 <- rnorm (40, 0.3, 0.01)
c3 <- rnorm (40, 0.5, 0.01); c4 <- rnorm (40, 0.7, 0.01)
c5 <- rnorm (40, 0.9, 0.03)
Yv <- 0.3 + rnorm (200, 0.05, 0.05)
myd <- data.frame (Xv = round (c(c1, c2, c3, c4, c5), 2), Yv = round (Yv, 2),
cltr = factor (rep(1:5, each = 40)))
require(rggobi)
g <- ggobi(myd)
display(g[1], vars=list(X="Xv", Y="Yv"))
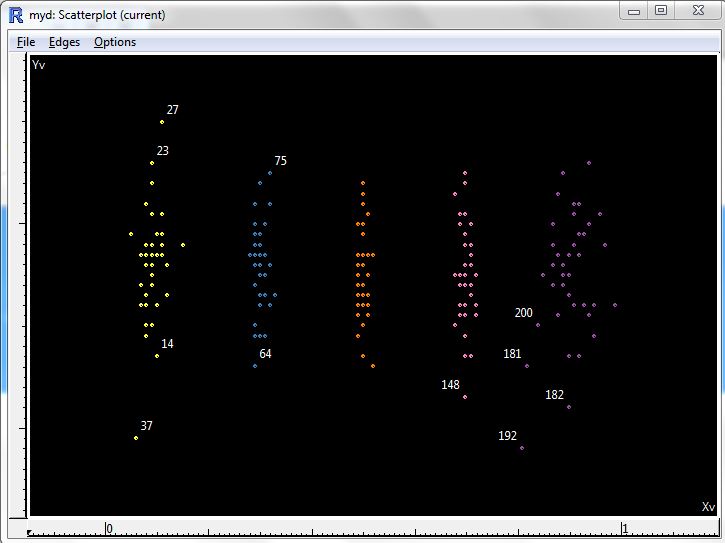
您可以看到五个集群,使用cltr变量的颜色不同。我手动地确定了点是异常值,我想使它们的值在cltr变量中变为NA。是他们的任何一种简单的方式来解除这种成员关系并写入文件。
回答 1
Stack Overflow用户
回答已采纳
发布于 2013-05-11 15:29:02
您可以尝试identify手动获取这些点的索引:
## use base::plot
plot(myd$Xv, myd$Yv, col=myd$cltr)
exclude <- identify(myd$Xv, myd$Yv) ## left click on the points you want to exclude (right click to stop/finish)
myd$cltr[exclude] <- NA页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/16498605
复制相关文章
相似问题

