群体间分布的视觉比较:规模如何修正为“不对称图”?
群体间分布的视觉比较:规模如何修正为“不对称图”?
提问于 2012-11-26 18:09:42
最近,我遇到了R包配方图,并提供了在一个小区(特殊不对称图)中绘制两个子组分布的可能性。您可以在统计软件杂志和cran.r-project.org中找到该包的描述。
我使用下面的代码生成了一个不对称的图标
library(psych)
library(beanplot)
var1 <-c(20,33,NA,39,NA,40,34,33,NA,38,NA,8,7,NA,NA,40,34,24,25,36,40,37,34,NA,35)
var2 <- c(1,0,1,1,1,0,1,0,1,NA,1,0,0,0,0,1,1,0,1,0,1,1,NA,0,1)
mydata<-data.frame(var1,var2)
table(mydata)
par(lend = 1, mai = c(0.8, 0.8, 0.5, 0.5))
beanplot(var1 ~ var2, data= mydata, side = "both",log="",
what=c(1,1,1,0), border = NA, col = list("black", c("grey", "white")))
legend("bottomleft", fill =c("black", "grey"), legend = c("no", "yes"))所生成的地块很好地显示了这两个子组分布的不同形状。
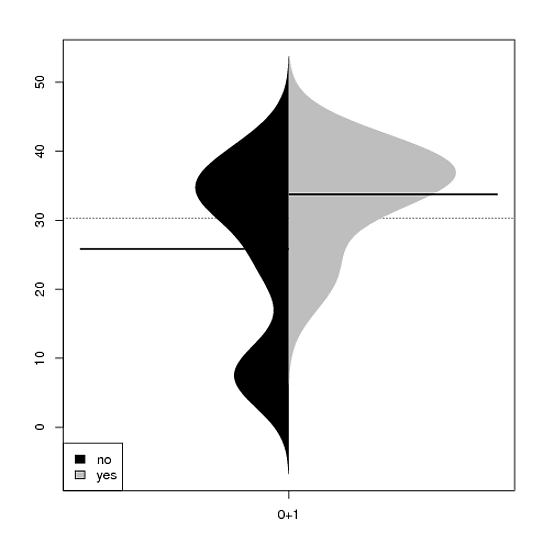
问题
因变量是以7到40为尺度来衡量的。然而,y轴似乎从-1到+55.
如果有人能解释如何修改比额表,即这里实际绘制的是什么,那就太好了。有没有办法用原始比例尺来绘制分布图?
非常感谢!
回答 1
Stack Overflow用户
回答已采纳
发布于 2012-11-26 18:20:37
beanplot使用density。估计的密度可以给超过观测数据范围的区域提供质量。您可以尝试这样做,以了解密度是什么-plot(density(1:2)),并且您应该看到它只是以数据点为中心的高斯密度的平均值(注意,您可以使用不同的内核,因为beanplot允许您指定内核参数)。它如何选择该高斯的方差取决于您,但在默认情况下,它似乎是使用bw.SJ和"dpi“方法来选择带宽。
您可以使用剪刀和最大的控制范围,比恩图实际绘制,但这并没有真正改变密度估计。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/13570629
复制相关文章
相似问题

