如何用ggplot2绘制非标准化数据?
如何用ggplot2绘制非标准化数据?
提问于 2012-10-09 06:03:52
我用ggplot2绘制虹膜数据。ggplot2似乎会自动将数据标准化为(0.1)间隔。如何在没有任何标准化操作的情况下绘制数据?
library(ggplot2)
p <- ggpcp(iris, vars = names(iris[1:4]))
p + geom_line(aes(color = Species)) + ylim(0,8)我不是以英语为母语的人,我很抱歉弄得模棱两可。实际上,虹膜数据从0到8不等。我想绘制的数据准确地反映了真实值,而不是标准化值(将原始数据转换为(0,1)间隔)。
回答 2
Stack Overflow用户
回答已采纳
发布于 2012-10-09 06:32:09
也许:
library(ggplot2)
p <- ggpcp(iris, vars = names(iris[1:4]))
iris2 <- data.frame(id=1:nrow(iris), iris)
dat <- reshape2::melt(iris2,id.var = c("id", "Species"))
ggplot(aes(y=value, x=variable, group=id, color=Species), data=dat) + geom_path()
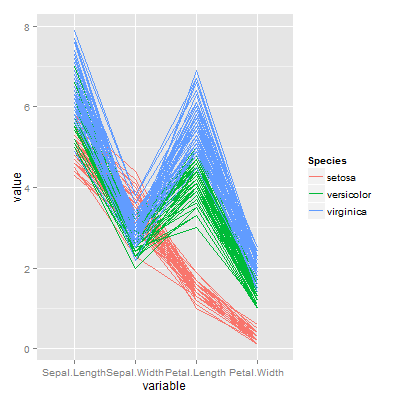
虽然可能有更好的方法。从来没这么做过所以尝试很有趣。
Stack Overflow用户
发布于 2012-10-09 07:28:28
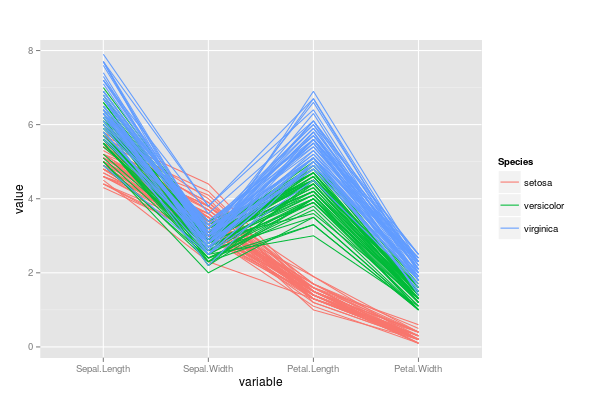
最直接的方法可能是使用GGally包。这允许您执行以下操作:
library(GGally)
ggparcoord(iris, columns = 1:4, groupColumn = 5, scale = "globalminmax")其结果是:
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/12793717
复制相关文章
相似问题

