基于Matlab的模糊C均值肿瘤分割方法
基于Matlab的模糊C均值肿瘤分割方法
提问于 2012-03-01 06:43:33
我有个肝节段。我要切掉里面的肿瘤。我用了FCM方法。这是一个三级FCM阈值。当我将其应用到图像中时,我需要单独对肿瘤区域(比其余部分更暗的区域)进行分割。但我的情况正好相反。肿瘤周围的所有区域都被分割。请帮帮我。程序有两个文件,testfcmthresh.m和一个函数fcmthresh.m。
输入的“分割肝脏(使用区域生长)”和FCM输出图像:
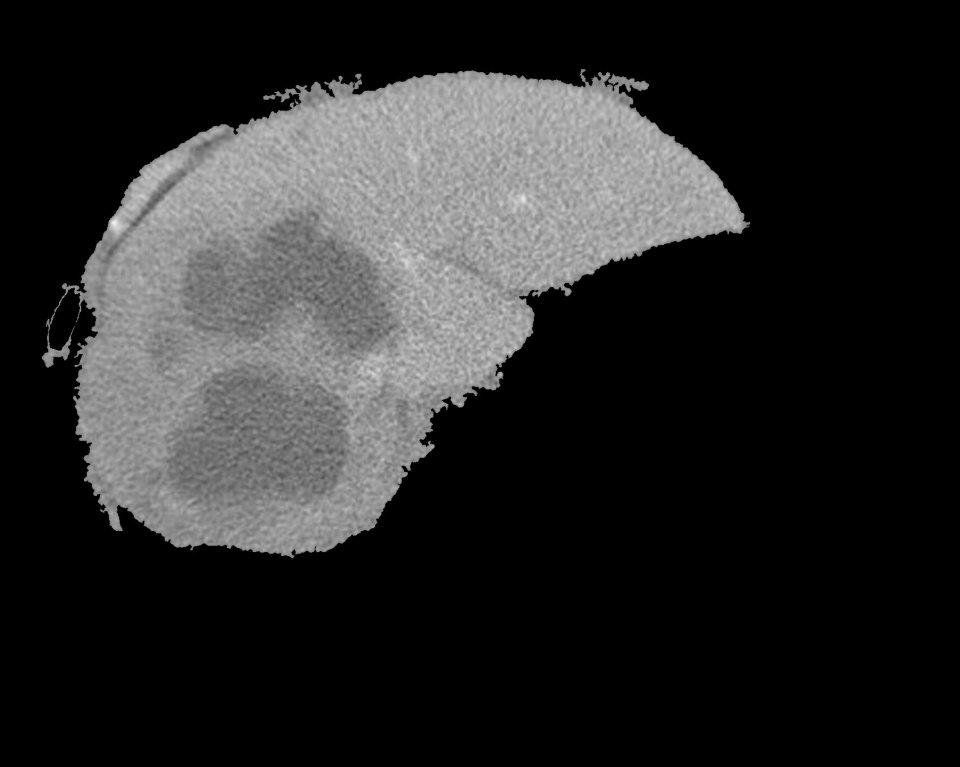
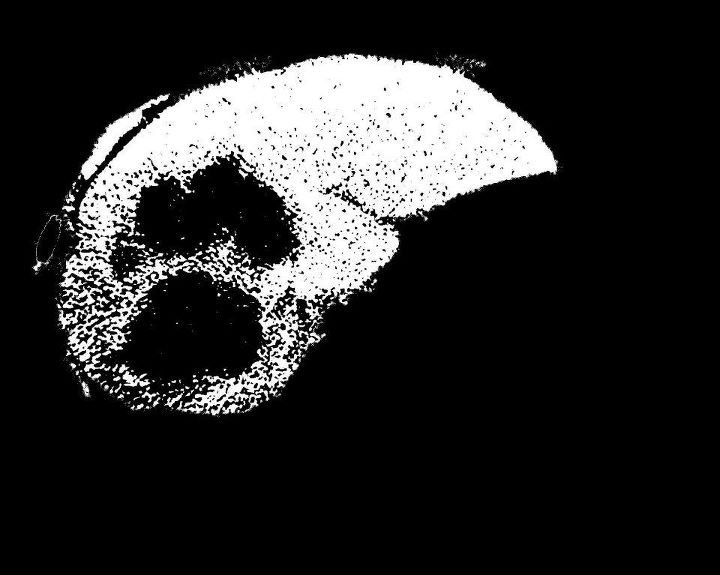
从这里开始
我试图补充使用imcomplement()获得的图像,但我得到的整个背景也是白色的,因为背景最初是黑暗的。请帮帮我。
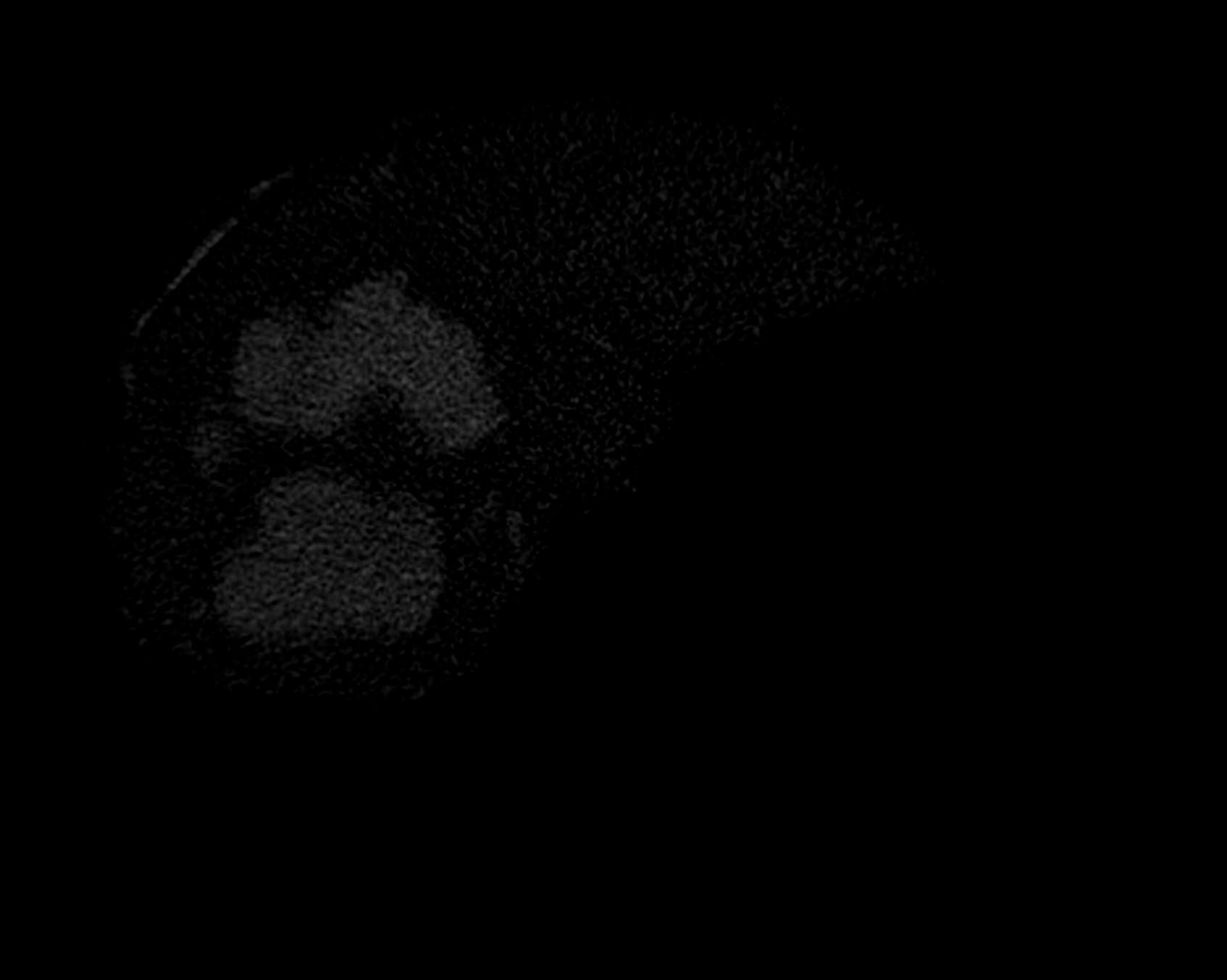

function [bw,level]=fcmthresh(IM,sw)
%FCMTHRESH Thresholding by 3-class fuzzy c-means clustering
% [bw,level]=fcmthresh(IM,sw) outputs the binary image bw and threshold level of
% image IM using a 3-class fuzzy c-means clustering. It often works better
% than Otsu's methold which outputs larger or smaller threshold on
% fluorescence images.
% sw is 0 or 1, a switch of cut-off position.
% sw=0, cut between the small and middle class
% sw=1, cut between the middle and large class
%
% Contributed by Guanglei Xiong (xgl99@mails.tsinghua.edu.cn)
% at Tsinghua University, Beijing, China.
% check the parameters
if (nargin<1)
error('You must provide an image.');
elseif (nargin==1)
sw=0;
elseif (sw~=0 && sw~=1)
error('sw must be 0 or 1.');
end
data=reshape(IM,[],1);
[center,member]=fcm(data,3);
[center,cidx]=sort(center);
member=member';
member=member(:,cidx);
[maxmember,label]=max(member,[],2);
if sw==0
level=(max(data(label==1))+min(data(label==2)))/2;
else
level=(max(data(label==2))+min(data(label==3)))/2;
end
bw=im2bw(IM,level);%testfcmthresh.m
clear;clc;
im=imread('mliver3.jpg');
fim=mat2gray(im);
level=graythresh(fim);
bwfim=im2bw(fim,0.1);
[bwfim0,level0]=fcmthresh(fim,0);
[bwfim1,level1]=fcmthresh(fim,1);
subplot(2,2,1);
imshow(fim);title('Original');
subplot(2,2,2);
imshow(bwfim);title(sprintf('Otsu,level=%f',level));
subplot(2,2,3);
imshow(bwfim0);title(sprintf('FCM0,level=%f',level0));
subplot(2,2,4);
imshow(bwfim1);title(sprintf('FCM1,level=%f',level1));
% imwrite(bwfim1,'fliver6.jpg');回答 1
Stack Overflow用户
回答已采纳
发布于 2012-03-03 12:21:35
我的问题的答案已经告诉了我在我的前一个问题,“在边界内提取图像区域”。如果有人需要参考,请阅读that.Thank你的评论。
页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/9511781
复制相关文章
相似问题

