重建minitab正态概率图
重建minitab正态概率图
提问于 2010-10-14 02:21:55
我试图用R. Minitab重新创建下面的情节,将其描述为一个正常的概率图。
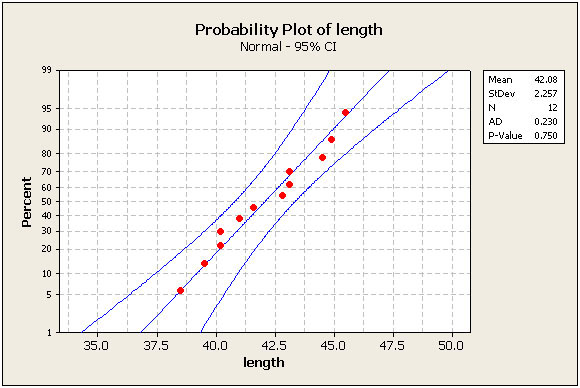
概率图把你带到那里的大部分时间。不幸的是,我不知道如何在这个图周围添加置信区间带。
类似地,ggplot的qq()似乎用转换后的x轴表示类似的信息。似乎geom_smooth()将是可能的候选加入乐队,但我还没有弄清楚。
最后,“让遗传学完成”的人描述了类似的这里。
重新创建上面的绘图的示例数据:
x <- c(40.2, 43.1, 45.5, 44.5, 39.5, 38.5, 40.2, 41.0, 41.6, 43.1, 44.9, 42.8)如果有人有一个基本图形或图形的解决方案,我会很感激的!
编辑
在查看了probplot的详细信息之后,我确定了它是如何在图形上生成fit行的:
> xl <- quantile(x, c(0.25, 0.75))
> yl <- qnorm(c(0.25, 0.75))
> slope <- diff(yl)/diff(xl)
> int <- yl[1] - slope * xl[1]
> slope
75%
0.4151
> int
75%
-17.36 实际上,将这些结果与从概率对象中获得的结果进行比较似乎是非常好的:
> check <- probplot(x)
> str(check)
List of 3
$ qdist:function (p)
$ int : Named num -17.4
..- attr(*, "names")= chr "75%"
$ slope: Named num 0.415
..- attr(*, "names")= chr "75%"
- attr(*, "class")= chr "probplot"
> 但是,将这些信息合并到ggplot2或基本图形中并不会产生相同的结果。
probplot(x)
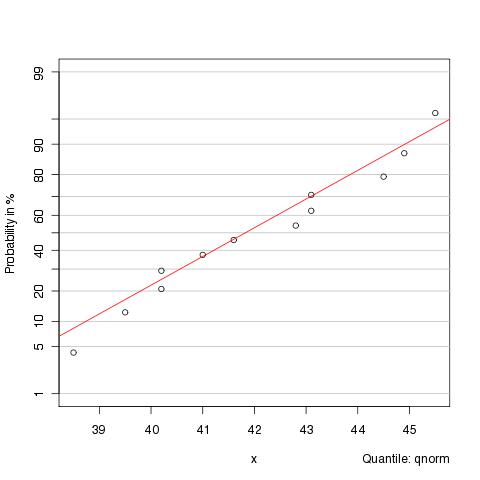
相对于:
ggplot(data = df, aes(x = x, y = y)) + geom_point() + geom_abline(intercept = int, slope = slope)
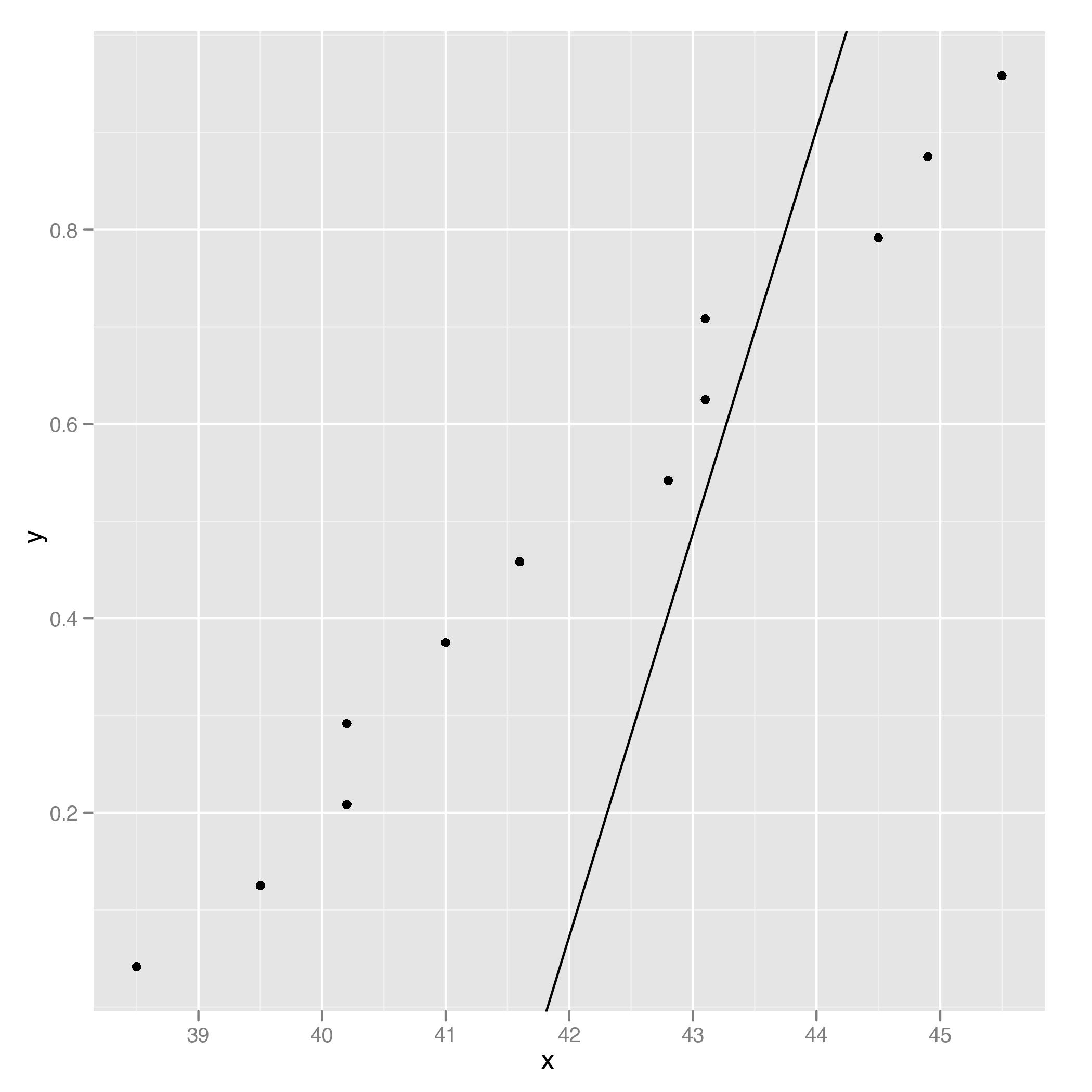
我用R的基本图形得到了类似的结果
plot(df$x, df$y)
abline(int, slope, col = "red")最后,我了解到,传说的最后两行提到了安德森-达林测试的正常度,并且可以用nortest包复制。
> ad.test(x)
Anderson-Darling normality test
data: x
A = 0.2303, p-value = 0.7502回答 5
Stack Overflow用户
回答已采纳
发布于 2010-10-14 05:38:58
也许这将是你可以建立的东西。默认情况下,stat_smooth()使用level=0.95。
df <- data.frame(sort(x), ppoints(x))
colnames(df) <- c("x","y")
ggplot(df, aes(x,y)) +
geom_point() +
stat_smooth() +
scale_y_continuous(limits=c(0,1),breaks=seq(from=0.05,to=1,by=0.05), formatter="percent")Stack Overflow用户
发布于 2011-10-28 20:19:31
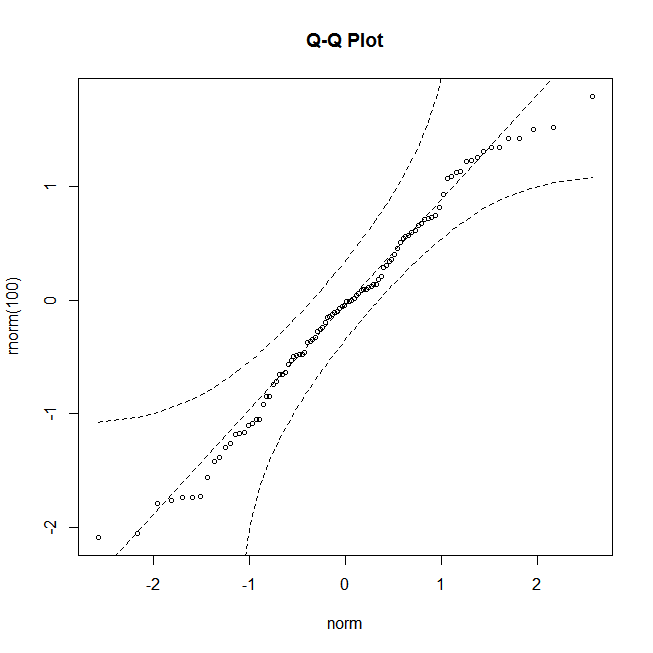
尝试qqPlot包中的QTLRel函数。
require("QTLRel")
qqPlot(rnorm(100))
Stack Overflow用户
发布于 2012-02-09 17:15:55
如果使用的是不正确的"y",它们应该是分位数(用概率标记)。下面显示了正确位置上的行:
df<-data.frame(x=sort(x),y=qnorm(ppoints(length(x))))
probs <- c(0.01, 0.05, seq(0.1, 0.9, by = 0.1), 0.95, 0.99)
qprobs<-qnorm(probs)
xl <- quantile(x, c(0.25, 0.75))
yl <- qnorm(c(0.25, 0.75))
slope <- diff(yl)/diff(xl)
int <- yl[1] - slope * xl[1]
ggplot(data = df, aes(x = x, y = y)) + geom_point() + geom_abline(intercept = int,slope = slope)+scale_y_continuous(limits=range(qprobs), breaks=qprobs, labels = 100*probs)+labs(y ="Percent" , x="Data")要像在Minitab中那样添加信任边界,可以执行以下操作
fd<-fitdistr(x, "normal") #Maximum-likelihood Fitting of Univariate Dist from MASS
xp_hat<-fd$estimate[1]+qprobs*fd$estimate[2] #estimated perc. for the fitted normal
v_xp_hat<- fd$sd[1]^2+qprobs^2*fd$sd[2]^2+2*qprobs*fd$vcov[1,2] #var. of estimated perc
xpl<-xp_hat + qnorm(0.025)*sqrt(v_xp_hat) #lower bound
xpu<-xp_hat + qnorm(0.975)*sqrt(v_xp_hat) #upper bound
df.bound<-data.frame(xp=xp_hat,xpl=xpl, xpu = xpu,nquant=qprobs)并从上面将以下两条线添加到您的ggplot中(另外,用估计的百分位数替换斜率和截取线)
geom_line(data=df.bound,aes(x = xp, y = qprobs))+
geom_line(data=df.bound,aes(x = xpl, y = qprobs))+
geom_line(data=df.bound,aes(x = xpu, y = qprobs))页面原文内容由Stack Overflow提供。腾讯云小微IT领域专用引擎提供翻译支持
原文链接:
https://stackoverflow.com/questions/3929611
复制相关文章
相似问题

